CDA Body
Inhaltsverzeichnis
- 1 Medizinische Inhalte im Body
- 1.1 Fachlicher Inhalt in den ELGA Interoperabilitätsstufen (EIS)
- 1.2 Aufbau des Body
- 1.2.1 Strukturierter Body („structuredBody“)
- 1.2.2 Sektion Brieftext
- 1.2.3 Sektion Überweisungsgrund
- 1.2.4 Bereiche (Specialities)
- 1.2.5 Gruppen (Befundgruppen)
- 1.2.6 Zusätzliche medizinische Informationen
- 1.2.7 Allgemeine Strukturrichtlinien für Body-Elemente
- 1.2.8 Narrativer Block
- 1.2.9 CDA Entry Level („Level 3“)
- 1.2.10 Harmonisierung des Befundaufbaus – Value Set „ELGA_Laborparameter“
- 1.3 Spezifikation der Befunddarstellung Level 2
- 1.3.1 Überblick
- 1.3.2 Formatierung von Datums- und Zeitangaben
- 1.3.3 Level 2 Befundstruktur
- 1.3.4 Probeninformation
- 1.3.5 Vorgaben zur Darstellung einzelner Elemente
- 1.3.6 Stylecodes
- 1.3.7 Bemerkungen/Kommentare
- 1.3.8 Eigenschaften des Materials/Mikroskopie
- 1.3.9 Kultureller Erregernachweis
- 1.3.10 Antibiogramm
- 1.3.11 Minimale Hemmkonzentration
- 1.3.12 Testergebnisse/Molekularer Erregernachweis
- 1.3.13 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012
- 1.3.14 Angabe des Akkreditierungs-Logos
- 1.3.15 Angabe des Untersuchungs- bzw Messverfahrens
- 1.3.16 Vorgaben für den Befunddruck
- 1.4 Spezifikation des Body Level 3
- 1.4.1 Überblick
- 1.4.2 Überweisungsgrund
- 1.4.3 Laboratory Report Data Processing Entry
- 1.4.4 Der Spezimen-Act
- 1.4.5 Probeninformationen (Specimen-Section)
- 1.4.6 Befundgruppen (Laboratory Battery Organizer)
- 1.4.7 Laborergebnisse (Laboratory Observation)
- 1.4.8 Kultureller Erregernachweis
- 1.4.9 Antibiogramm (Laboratory Isolate Organizer)
- 1.4.10 Minimale Hemmkonzentration
- 1.4.11 Testergebnisse/Molekularer Erregernachweis
- 1.4.12 Significant Pathogens (Notifiable Conditions)
- 1.4.13 Befundtext: Anmerkungen und Kommentare
- 1.4.14 Multimedia Content
1 Medizinische Inhalte im Body
1.1 Fachlicher Inhalt in den ELGA Interoperabilitätsstufen (EIS)
1.1.1 Fachlicher Inhalt in EIS „Basic“ und „Structured“
Enthält das Dokument entweder unstrukturierten oder eingebetteten Inhalt (z.B. PDF) oder strukturierten Inhalt3 , wobei jedoch nicht alle Sektionen den Vorgaben von EIS „Enhanced“ oder „Full Support“ folgen, dann liegt das Dokument in ELGA Interoperabilitätsstufe (EIS) „Basic“ vor. Die Sektionen MÜSSEN jedenfalls in der von diesem Leitfaden definierten Reihenfolge vorliegen, damit die erforderliche ELGA Interoperabilitättstufe „Structured“ erreicht wird.
Die Verwendung von EIS Basic ist in ELGA nicht mehr zulässig.
3 Ensprechend den CDA Body Choices „NonXMLBody“ und „StructuredBody“, unconstrained CDA specification („CDA Level One“)
1.1.2 Fachlicher Inhalt in EIS „Enhanced“ oder „Full support“
Ein Dokument liegt in der ELGA Interoperabilitätsstufe (EIS) „Enhanced“ oder „Full support“ vor, wenn das Dokument strukturierten Inhalt enthält und alle Sections den Vorgaben von EIS „Enhanced“ oder höher folgen.
- EIS „Enhanced“
- Alle Sections folgen ausnahmelos den Vorgaben von EIS „Enhanced“ oder höher, aber nicht alle Sections folgen den Vorgaben von EIS „Full support“.
- EIS „Full support“
- Alle Sections folgen ausnahmelos den Vorgaben von EIS „Full support“.
1.2 Aufbau des Body
1.2.1 Strukturierter Body („structuredBody“)
Für Laborbefunde im Rahmen der ELGA sollten ausschließlich strukturierte Befunde übermittelt werden. Ein ELGA-Labor CDA-Dokument mit ausschließlich einem unstrukturiertem Body (nonXMLBody) ist im Rahmen der EIS Structured in einer Übergangsphase zulässig! Danach werden im Rahmen von EIS Enhanced und EIS Full Support ausschließlich nur mehr Level 3 codierte Befunde übermittelt.
Ein strukturierter Laborbefund MUSS zumindest eine Gliederungsebene („Bereiche“), kann aber zwei Gliederungsebenen („Bereiche“ und „Befundgruppen“) beinhalten.
1.2.2 Sektion Brieftext
Die Verwendung der Sektion Brieftext ist im Laborbefund ERLAUBT (Spezifikation siehe Allgemeiner Leitfaden [4], TemplateID: 1.2.40.0.34.11.1.2.1). Über diese Sektion können eine Anredefloskel und maximal ein Logo der Organisation des Autors angegeben werden. Mehrere Logos (zB wenn zusätzlich ein Akkreditierungs-Logo angegeben werden soll) sind in eine Grafikdatei zusammenzufassen.
1.2.3 Sektion Überweisungsgrund
Die optionale Sektion Überweisungsgrund enthält die vom Auftraggeber bestimmte und dem Labor übermittelte Auftrag- oder Verdachtsdiagnose oder die Fragestellung. Siehe Kapitel Überweisungsgrund.
1.2.4 Bereiche (Specialities)
Jeder CDA–Laborbefund ist laut vorliegender Headerdefinition als „Multidisciplinary Report“ ausgewiesen (vgl. Kapitel), kann jedoch mehrere unterschiedliche Teilbefunde aus verschiedenen Bereichen im Body des Dokumentes beinhalten (z.B. Hämatologie oder Bakteriologie oder beide Arten gemeinsam). D.h. diese Teilbefunde bilden die erste Gliederungsebene des Bodys - die „Bereiche“ oder - in Anlehnung an die Definitionen der „IHE“ – „Specialities“ (vgl. [3]). Die nachfolgen Abbildung zeigt die mögliche Gliederung auf der ersten Ebene innerhalb des Bodys.
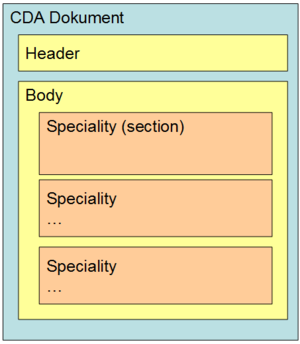
Abbildung 3: Gliederung nach Bereiche /Specialities
Die derzeit für den österreichischen Laborbefund definierten Specialities werden im Rahmen des hierarchisch organisierten Value Sets „ELGA_Laborstruktur“ definiert, wobei für Bereiche nur Einträge der Ebene 0 und 1 verwendet werden dürfen. Die nachfolgende Tabelle gibt einen auszugsweisen Überblick über die derzeit festgelegten Specialities. Die Anwendung der Bereiche ist optional. Es können auch alle Untersuchungen in einer Section unter dem Bereich „Allgemeiner Laborbefund“ zusammengefasst werden. Bei Verwendung der Bereiche ist die Reihenfolge gem. Value Set verpflichtend einzuhalten.
Für EIS „Enhanced“ ist die Codierung der Bereiche (als unterschiedliche section-Elemente) zwingend vorgeschrieben.
| Code | Bereich (Speciality) |
|---|---|
| 100 | Blutgruppenserologie |
| 200 | Blutgasanalytik |
| 300 | Hämatologie |
| 400 | Gerinnung/Hämostaseologie |
| 500 | Klinische Chemie/Proteindiagnostik |
| 600 | Hormone/Vitamine/Tumormarker |
| 900 | Toxikologie |
| 1000 | Medikamente |
| 1100 | Infektionsdiagnostik |
| 1300 | Autoimmundiagnostik |
| 1800 | Allergiediagnostik |
| 1400 | Urindiagnostik |
| 1500 | Stuhldiagnostik |
| 1600 | Liquordiagnostik |
| 2300 | Genetische Diagnostik |
| 2500 | Sonstige |
Tabelle 4: Liste der Bereiche, auszugsweise gem. ELGA Value Set „ELGA_Laborstruktur“, die sich auch in ELGA_Laborparameter widerspiegelt.
1.2.5 Gruppen (Befundgruppen)
Innerhalb dieser Bereiche erfolgt in der Regel eine Strukturierung und Gliederung der Ergebnisse zur besseren Lesbarkeit und Auffindbarkeit in „Befundgruppen“. Das ELGA Value Set „ELGA_Laborstruktur“ definiert zulässige Befundgruppen. Es besteht jedoch auch die Möglichkeit Ergebnisse ohne Befundgruppenstrukturierung zu übermitteln. Die nachfolgende Abbildung zeigt die möglichen Gliederungsarten.
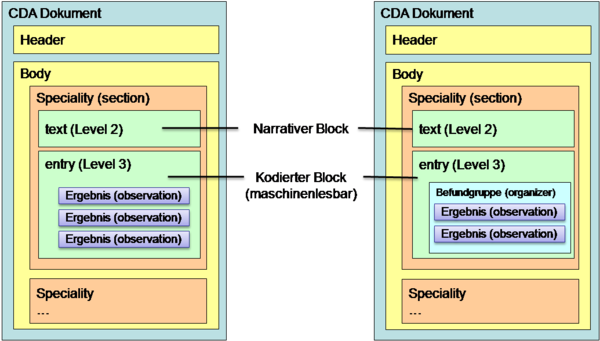
Abbildung 4: Strukturierungsmöglichkeiten Body
Die beiden nachfolgenden Abbildungen zeigen Ausschnitte aus Beispielen zu Laborbefunden mit Befundgruppen und den entsprechenden medizinischen Inhalten. Der „Allgemeine Laborbefund“ enthält die Bereiche „Hämatologie“ und „Hämostaseologie“ mit darunter liegenden Befundgruppen; der „Bakteriologische Befund“ enthält ein Bespiel für die Darstellung eines Antibiogrammes.
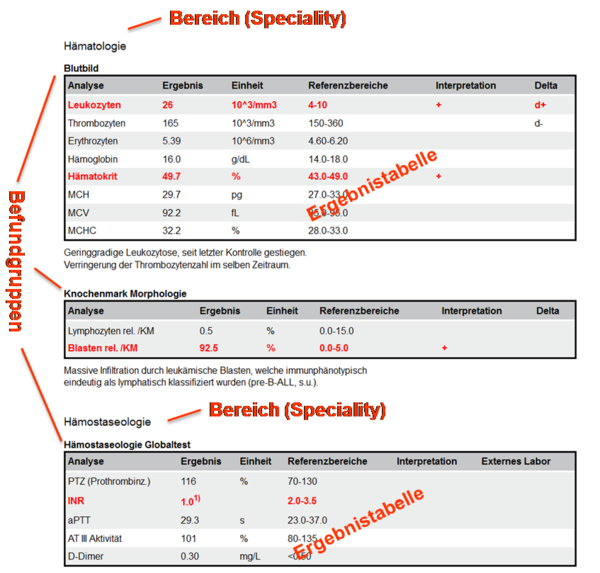
Abbildung 5: Ausschnitt Beispielbefund
Bereiche (Specialities) und Gruppen werden in CDA Level 3 in entsprechende Klassen umgesetzt und gemäß des hierarchischen Value Sets „ELGA_Laborstruktur“ codiert. Die Codierung der Bereiche erfolgt durch Elemente der ersten und zweiten Ebene (0 bzw. 1) und die der Befundgruppen durch Elemente der drittenValue Set Ebene (2). Die Reihenfolge der Bereiche bzw. Gruppen gem. Value Set ist verpflichtend einzuhalten.
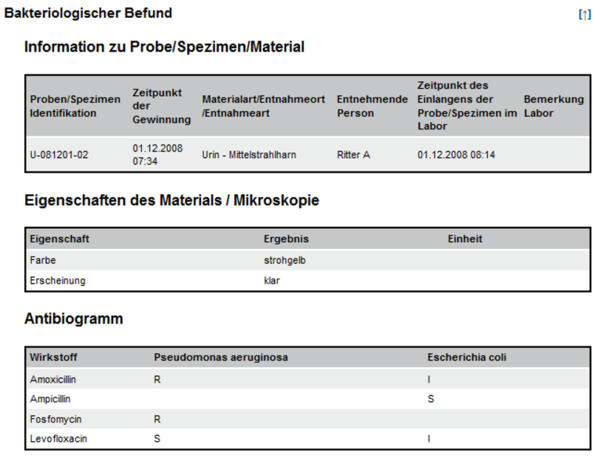
Abbildung 6: Ausschnitt Bakteriologie Beispielbefund
1.2.6 Zusätzliche medizinische Informationen
Unter Umständen ist es von Bedeutung und Interesse in dem Befund zusätzliche medizinische Informationen anzugeben. Dies betrifft z.B. die Aufnahmediagnose oder die medizinische Fragestellung bei der Auftragserteilung an das Labor. Diese Informationen können parallel zu den Befundarten als eigene Sections im CDA-Dokument angegeben werden. Die Codierung der Informationen innerhalb dieser Sections hat jedoch gemäß den Vorgaben des IHE „Patient Care Coordination“ Framework (PCC) [6] zu erfolgen!
1.2.7 Allgemeine Strukturrichtlinien für Body-Elemente
Die Gliederung eines Laborbefundes wurde bereits in Kapitel Aufbau des Body ausführlich dargestellt. Die Definitionen der Elemente werden von den Vorgaben der IHE ([3]) übernommen. Demgemäß entspricht ein Bereich einem anzugebenen Template:
<templateId root="1.3.6.1.4.1.19376.1.3.3.2.1"/>
Eine Ausnahme besteht für den Bereich (section) Probeninformation, in welchem nicht die IHE templateId „1.3.6.1.4.1.19376.1.3.3.2.1“ zu codieren ist, da diese Sektion nicht IHE konform ist.
Die nachfolgende Tabelle zeigt die abzubildenden Elemente:
| Feld | Element | Details/Codierung |
|---|---|---|
| Id | structuredBody/component/ section/id | Angabe einer Identifikation auf der Basis eines lokalen Nummernkreises |
| Code | structuredBody/component/section/code | Definition des Bereichs. Codierung nach „ELGA_Laborstruktur“ (Entsprechend der Werte der Tabelle mit Level 1). Siehe auch Tabelle 4 in 6.2.4 |
| Title | structuredBody/component/section/title | Angezeigter Titel der Befundart |
| Text | structuredBody/component/section/text | Narrativer Text (Gliederung nach den Werten der Tabelle mit Level 2) (siehe 6.3.3) |
| Entry | structuredBody/component/section/entry | Laboratory Report Data Processing Entry (siehe 6.4.3) |
Tabelle 5: Elemente einer Befundart
<component>
<section>
<templateId root="1.3.6.1.4.1.19376.1.3.3.2.1"/>
<id extension="P-body" root="2.16.840.1.113883.3.933.1.1"/>
<code code="1" codeSystem="1.2.40.0.34.5.11" codeSystemName="ELGA_LaborparameterErgaenzung" displayName="Allgemeiner Laborbefund"/>
<title>Allgemeiner Laborbefund</title>
<!-- start level 2 -->
:
<text>
</text>
<!-- start level 3 -->
<entry typeCode="DRIV">
:
</entry>
</section>
</component>
1.2.8 Narrativer Block
Jedes CDA-Dokument enthält verpflichtend einen narrativen Text (component/section/text). Die inhaltlichen Vorgaben in Bezug auf den Laborbefund betreffen die verpflichtend anzuführenden Felder, deren mögliche Ausprägungen und Grobstruktur in der die Daten im Level 2 darzustellen sind. Die Vorgaben finden sich in den nachfolgenden Kapiteln. Die Vorgaben für die Darstellung der Befunde sind in Kapitel Spezifikation der Befunddarstellung Level 2 beschrieben.
1.2.8.1 Strukturbeispiel
<!-- Start Level 2 --> <text> <paragraph styleCode="xELGA_h3">Blutbild</paragraph> <!-- Ergebnistabelle Blutbild --> <table> <thead> <tr> <th>Analyse</th> <th>Ergebnis</th> <th>Einheit</th> <th>Referenzbereiche</th> <th>Interpretation</th> <th>Delta</th> </tr> </thead> <tbody> <tr ID="OBS-1-1" styleCode="xELGA_red"> <td>Leukozyten</td> <td>26.42</td> <td>10^3/mm3</td> <td ID="OBSREF-1-1">4.4-11.3</td> <td>+</td> <td>d+</td> </tr> <tr ID="OBS-1-2"> <td>Thrombozyten</td> <td>165</td> <td>10^3/mm3</td> <td ID="OBSREF-1-2">150-360</td> <td/> <td>d-</td> </tr> </tbody> </table> <paragraph> <content ID="haematologyComment">Geringgradige Leukozytose, seit Letzter Kontrolle gestiegen. <br/> Verringerung der Thrombozytenzahl im selben Zeitraum. </content> </paragraph>
1.2.9 CDA Entry Level („Level 3“)
In den „Level 3“-konformen Teilen des Dokuments werden die maschinenlesbaren, codierten Daten zu den zuvor in Level 2 dargestellten Laborwerten abgebildet. Die erste Gruppierungsebene ist verpflichtend und stellt die Befundart (Speciality) dar. Die Abbildung der Befundarten erfolgt dabei über entsprechende component/section Strukturen. Jede dieser section-Elemente beinhaltet genau einen Entry Block, welcher genau einem spezifischen Template folgt und als „Laboratory Report Data Processing Entry“ bezeichnet wird (siehe Kapitel Laboratory Report Data Processing Entry). Das entry-Element besitzt genau ein einziges act-Element als Subelement – den sogenannten „Specimen-Act“ (siehe Kapitel Der Spezimen-Act). Das bedeutet, dass im entry-Block eines section-Elements nur ein einziges direktes Subelement abgebildet ist unter dem alle weiteren Strukturen gegliedert sind. Darunter werden unter anderem optional die Befundgruppen mittels organizer-Elementen abgebildet, welche wiederum die Einzeluntersuchungen („Observations“ observation) beinhalten. Das Codebeispiel in der nachfolgenden Abbildung zeigt die Strukturierung des Befundes aus der Abbildung "Ausschnitt Beispielbefund". Eine detaillierte Beschreibung der Strukturen erfolgt in Kapitel Spezifikation des Body Level 3.

Abbildung 7: Codefragment Beispielbefund
1.2.9.1 Ableitung Level 2 aus Level 3
Im Falle der Definition des ELGA-Labor Befundes ist eine vollständige Konstruktion des narrativen Teils des CDA-Dokuments (Level 2) aus der maschinenlesbaren, strukturierten Darstellung des Level 3 möglich! Dieses Faktum wird durch das Attribut typeCode=“DRIV“ des entry-Elementes ausgedrückt.
1.2.9.2 Referenz von Level 3 auf Level 2
In manchen Fällen ist es notwendig aus dem codierten Level 3 Teil des CDA-Dokuments auf Teile des Level 2 Teiles zu verweisen (z.B. bei Kommentaren um sich eine doppelte Angabe längerer Textpassagen zu ersparen). Dabei werden die zu referenzierenden Teile in Level 2 mit einer ID versehen (z.B. mit dem Attribute id=“refID“ im content-Element). Auf diese ID kann dann aus dem Level 3 mittels eines text-Elementes mit einem reference-Subelement (<reference value=“#refID“>) referenziert werden. Nachfolgende Beispiele zeigen eine Referenz auf einen Kommentar (siehe auch Bemerkungen/Kommentare und Spezifikation Antibiogramm) bzw. eine Referenz auf eine ganze Tabellenzeile (Analyseergebnis, siehe auch Kapitel Laborergebnisse).
… <text> … <paragraph> <content ID="haematologyComment">Geringgradige Leukozytose, seit letzter Kontrolle gestiegen. <br/>Verringerung der Thrombozytenzahl im selben Zeitraum. </content> </paragraph> … </text> <entry> … <component typeCode="COMP"> <act classCode="ACT" moodCode="EVN"> <templateId root="1.2.40.0.34.11.4.3.2"/> <templateId root="2.16.840.1.113883.10.20.1.40"/> <templateId root="1.3.6.1.4.1.19376.1.5.3.1.4.2"/> <code code="48767-8" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Annotation Comment"/> <text> <reference value="#haematologyComment"/> </text> <statusCode code="completed"/> </act> </component> … </entry> … <text> … <tbody> <tr ID="OBS-1-1"> <td>Hämoglobin</td> <td>16.0</td> <td>g/dL</td> <td ID="OBSREF-1-1">14.0-18.0</td> <td/> <td/> </tr> … </tbody> … </text> <entry> <observation classCode="OBS" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.6"/> <code code="718-7" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Hämoglobin"/> <text> <reference value="#OBS-1-1"/> </text> … </observation> … </entry> …
1.2.9.3 Dokumentenbasis
Die Umsetzung des Laborbefundes erfolgt in Anlehnung an das IHE Laboratory Technical Framework (vgl. [3]).
1.2.10 Harmonisierung des Befundaufbaus – Value Set „ELGA_Laborparameter“
Im Rahmen der Arbeiten zum vorliegenden Dokument wurde in der Expertengruppe die grundsätzliche Übereinkunft getroffen, auch die Befundgruppen und die damit verbundene Testzuordnung entsprechend österreichweit abzustimmen. Die Strukturierung eines Laborbefundes wurde in Form des hierarchischen Value Sets „ELGA_Laborparameter“ festgelegt.
Strukturierung, Reihenfolge der Parameter sowie die Bezeichnung der Parameter sind durch das Value Set ELGA Laborparameter verpflichtend vorgegeben!
Eine Hilfestellung zum Mapping der lokalen Codes auf die vorgeschriebenen Codes des Value Sets bietet der „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
1.3 Spezifikation der Befunddarstellung Level 2
1.3.1 Überblick
Die nachfolgende Tabelle gibt einen Überblick über die im lesbaren Text anzugebenden und in Level 2 (unter component/section) zu anzugebenden medizinischen Inhalte. Die Optionalität bezieht sich auf die Darstellung des jeweiligen Elements in der Tabelle. Die Befüllung ergibt sich aus den Vorgaben für Level 3 (z.B. ist die „Bemerkung Labor“ in dieser Übersicht mit [R] angegeben, d.h. das Tabellenelement ist verpflichtend anzugeben, befüllt muss es nur werden, wenn tatsächlich eine Bemerkung vorhanden ist).
Die Reihenfolge der Elemente innerhalb einer Gruppe ist zu beachten.
Die Angabe der Sektion Brieftext ist im Laborbefund ERLAUBT (Siehe Allgem. Leitfaden [4] TemplateID: 1.2.40.0.34.11.1.2.1).
| Feld | Opt | Darstellung | Details | |
|---|---|---|---|---|
| Befundbereiche | <section/title>Name des Befundbereichs</section/title>
Der Name des Befundbereichs wird in <section/title> codiert und nicht innerhalb des <section/text> Elements | |||
| <Component/section/text> Inhalt | ||||
| Allgemeine Befundinformationen | O | |||
| 1 | Auftragsdiagnose (Zuweiser-diagnose) | O [0..*] |
<paragraph> </paragraph> |
|
| 2 | Fragestellung | O [0..1] |
<paragraph> </paragraph> |
|
| 3 | Befundtext | O | < table> </ table> |
|
| Spezimeninformation | < table> pro Spezimen eine Zeile < tr> </ tr>
Sollte ein Befund aus mehreren Sections bestehen, wird die Spezimeninformation ausschließlich in einer eigenen Section angegeben und als erste Section geführt.Generell gilt, dass die Angabe von Informationen zu Proben/Spezimen/Material vorgeschrieben ist.
| |||
| 1 | Material-ID | O | <td></td> | Identifikator der Probe |
| 2 | Probenentnahme | R | <td></td> | Zeitpunkt der Probebentnahme, muss nicht angegeben werden bzw darf „unbekannt“ sein. Format: dd.MM.yyyy hh24:mi (6.4.5.3.3.4) |
| 3 | Untersuchtes Material | R | <td></td> | Materialart [R] (6.4.5.3.3.7) und Entnahmeort [O] (6.4.5.3.3.5) (Freitext ist zulässig) |
| 4 | Probenentnahme durch | O | <td></td> | Für Probenentnahme zuständige Person und ggf Organisation [O] (6.4.5.3.3.6) |
| 5 | Probeneingang | R | <td></td> | Probeneingang im Labor, Format: dd.MM.yyyy hh24:mi |
| 6 | Bemerkung Labor | R | <td></td> | Allfällige Bemerkungen zur Probenqualität sollen angegeben werden |
| Befundgruppen | <paragraph styleCode="xELGA_h3"> Name der Gruppe</paragraph> | |||
| Gruppierung / Befundgruppen (Organizer) | ||||
| Ergebnistabelle (Observations)4 | < table> je Test eine Zeile <tr></tr> | |||
| 1 | Analyse | M | <td></td> | Bezeichnung der Analyse (entsprechen dem displayName in Value Set ELGA-Laborparameter) |
| 2 | Ergebnis | M | <td></td> | Ergebnis der Analyse5, siehe 6.3.5.2 |
| 3 | Einheit | M | <td></td> | Einheit (UCUM printName), siehe 6.3.5.3 |
| 4 | Referenzbereiche | R2 | <td></td> | Mehrere Referenzbereiche können angegeben werden, getrennt durch Zeilenumbruch im Text6 |
| 5 | Interpretation | R2 | <td></td> | Codiert! Siehe 6.3.5.4 sowie Kapitel Tabelle 7 und Tabelle 8 |
| 6 | Externes Labor | R2 | <td></td> | Angabe von „E“, wenn die Analyse von einem externen Dienstleister gemessen wurde |
| Eigenschaften des Materials / Mikroskopie | < table> pro Eigenschaft eine Zeile <tr></tr> | |||
| 1 | Eigenschaft | M [1..1] |
<td></td> | |
| 2 | Ergebnis | M [1..1] |
<td></td> | |
| 3 | Einheit | O [0..1] |
<td></td> | |
| Kultureller Erregernachweis | < table> pro Erreger eine Zeile<tr></tr> | |||
| 1 | Erreger | M [1..1] |
<td></td> | |
| 2 | Methode | R2 [0..1] |
<td></td> | Mögliche Werte vgl. Tabelle 12: Beispiele für Codes für Erregernachweis-Methodik |
| 3 | Keimzahl | M [1..1] |
<td></td> | |
| Antibiogramm | < table> je Antibiotikum Zeile <tr></tr> | |||
| 1 | Name des Erregers | M [1..1] |
<th></th> | Darstellung als Spaltenüberschriften |
| 2 | Wirkstoff | M | <td></td> | Antibiotischer Wirkstoff |
| 3 | Resistenzkennung | M | <td></td> | Codiert! Siehe Tabelle 13. (Am Schnittpunkt von Erreger (Spalte) und Wirkstoff (Zeile)) |
| minimale Hemmkonzentration | < table> je Antibiotikum Zeile <tr></tr> | |||
| 1 | Name des Erregers, sowie Einheit der Konzentration | M [1..1] |
<th></th> | Darstellung als Spaltenüberschriften |
| 2 | Wirkstoff | M | <td></td> | Antibiotischer Wirkstoff |
| 3 | Konzentration | M | <td></td> | Schnittpunkt von Erreger (Spalte) und Wirkstoff (Zeile) |
| Testergebnisse / Molekularer Erregernachweis | < table> je Analyse/Erreger eine Zeile <tr></tr> | |||
| 1 | Analyse / Erreger / Methode | M [1..1] |
<td></td> | |
| 2 | Ergebnis | M | <td></td> | |
| 3 | Einheit | O [0..1] |
<td></td> | |
| 4 | Referenzbereich / Nachweisgrenze / Linearitätsbereich | O [0..1] |
<td></td> | |
| 5 | Interpretation | R2 | <td></td> | Codiert: Siehe Tabelle 7 und Tabelle 8 |
Tabelle 6: Übersicht Medizinische Inhalte Level 2
4 Spezialuntersuchungen, die nicht in das angegebene Schema passen (z.B Molekulare Diagnostik, Allergiediagnostik etc.), können bei Bedarf auch anders dargestellt werden. Ensprechende Beispieldokumente stehen zur Verfügung.
5 Es wird EMPFOHLEN, bei Dezimalzahlen einen Punkt als Dezimaltrennzeichen zu verwenden – gleich wie im maschinenlesbaren Teil.
6 Es wird EMPFOHLEN, bei Dezimalzahlen einen Punkt als Dezimaltrennzeichen zu verwenden – gleich wie im maschinenlesbaren Teil
1.3.2 Formatierung von Datums- und Zeitangaben
Datums- und Zeitangaben sind im lesbaren Teil im Format „dd.MM.yyyy“ bzw. „dd.MM.yyyy hh24:mi“ anzugeben. Dabei gilt:
| dd | Tag |
| MM | Monat als zweistellige Zahl |
| yyyy | Jahr |
| hh24 | Stunden im 24 Stunden Format |
| mi | Minuten |
1.3.3 Level 2 Befundstruktur
Bei der Darstellung der Befunde ist die Struktur gemäß der nachfolgenden Abbildung verpflichtend abzubilden.
| Spezimen Bereich | Spezimen Section: enthält Tabelle mit Spezimen in <text> | ||
| Befundbereich (Section) | Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| Befundgruppe | Befundgruppenbezeichnung | ||
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| .. | .. | ||
| Befundbereich (Section) | Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| Befundgruppe | Befundgruppenbezeichnung | ||
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| .. | .. | ||
| .. | ... | ||
| Befund Bemerkung Bereich | Befundbemerkung Section enthält: Bemerkung zu Befund in <text> | ||
Abbildung 8: Befundstruktur Level 2 mit mehreren Sections
Enthält ein Befund nur genau einen Bereich (Section) kann eine vereinfachte Darstellung mit folgender Befundstruktur verwendet werden:
| Tabelle mit Spezimen | ||
| Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | ||
| Bemerkung zur Befundgruppe | ||
| Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | ||
| Bemerkung zur Befundgruppe | ||
| ... | ... | |
| Bemerkung zur Befundart | ||
Abbildung 9: Befundstruktur Level 2 mit einer Section
1.3.4 Probeninformation
Der Inhalt dieser Sektion enthält sämtliche Information über das zu befundende Material, inklusive, soweit sinnvoll, der Lokalisation, der Entnahmeart, des Entnahmegeräts, der Person, welche die Entnahme durchgeführt hat, sowie Zeitpunkt der Materialentnahme und der Materialannahme.
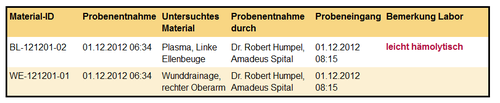
Abbildung 10: Probeninformation, vollständig.
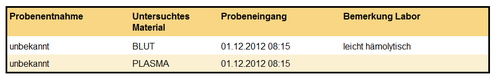
Abbildung 11: Probeninformation, minimal.
Menschenlesbare Informationen zum Spezimen MÜSSEN angegeben werden, wenn bekannt.
In dem folgenden Strukturbeispiel ist die Codierung der Informationen in einer Tabelle ersichtlich. Die einzelnen Zeilen, welche jeweils ein Spezimen codieren, können mit Identifikatoren gekennzeichnet werden um auf diese im weiteren CDA Befund referenzieren zu können. Die Optimierung der Spaltenbreiten kann im ELGA Referenz-Stylesheet durch die ELGA-Stylecodes „xELGA_colw:nn“ erfolgen.
Die Abbildung der Spezimeninformation kann auf zwei Arten erfolgen:
- Enthält ein Befund nur einen Bereich, so kann die Codierung gemäß IHE LAB TF-3 innerhalb der einen Befundsektion erfolgen
ODER
- Bei Verwendung von mehreren Bereichen (vgl. Anforderung) in einem Laborbefund kann es zu Überschneidungen der Spezimeninformationen kommen (ein spezielles Spezimen kann in zwei Bereichen analysiert werden). Die Level 3 Codierung eines Spezimens darf jedoch nur einmal im gesamten Laborbefund erfolgen. Daher sind die Informationen zu den Spezimen in einer eigenen führenden Probeninformation Section mit dem Code „10“ und der TemplateID 1.2.40.0.34.11.4.2.1 zu codieren.
1.3.5 Vorgaben zur Darstellung einzelner Elemente
1.3.5.1 Analysen
Analysen (bzw Laborwerte, Laborleistungen oder Labormessgrößen) MÜSSEN in der einheitlichen Schreibweise angegeben sein, die im Value Set „ELGA_Laborparameter“ vorgegeben wird („Begriff“ bzw „display name“ im Value Set). Das erleichtert das Lesen und speziell für Patienten die Recherche von Laborwerten im Gesundheitsportal (www.gesundheit.gv.at). Siehe dazu auch den „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
Ein Beispiel zur Darstellung findet sich in Abbildung 12. Die Tabelle besteht aus mindestens fünf und maximal sechs Spalten. Für jede Gruppe wird ein Block angelegt, Bereichsüberschriften entsprechen Kapitelüberschriften. Zusätzlich kann eine Spalte mit „Extenes Labor“ notwendig sein. Sollen genauere Angaben zur Methode gemacht werden, als durch den Namen der Analysen bereits hervorgeht, soll dies über einen Analysenkommentar umgesetzt werden (siehe 6.3.8.1).
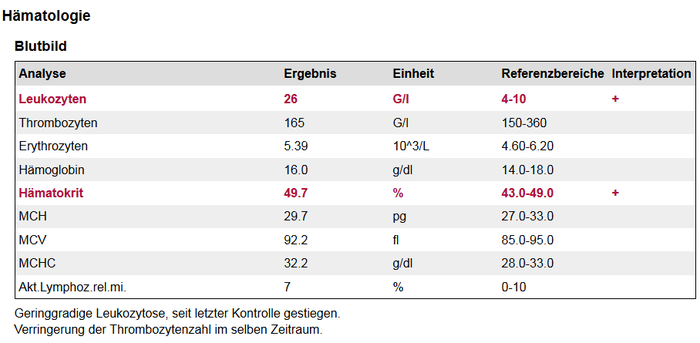
Abbildung 12: Beispiel einer ausführlichen Laborwerte-Ergebnistabelle
1.3.5.2 Ergebnis
Dieses Element enthält ein numerisches, nominales, ordinales oder narratives Ergebnis der Analyse zu diesem Testcode. Da in der Definition des CDA-Schemas keinerlei Längenbeschränkung vorgegeben ist, kann dieses Feld auch größere Textmengen fassen um große verbale Beurteilungen zu ermöglichen.
1.3.5.3 Einheit
Zu jedem Ergebnis MUSS eine passende Einheit angegeben werden. Bevorzugt zu verwenden sind die Einheiten, die im Value Set „ELGA_Laborparameter“ vorgeschlagen werden.
Es wird EMPFOHLEN, anstelle von Einheitenpräfixen („Giga“, „Mega“, „Milli“, „Mikro“ etc.) eine Potenzschreibweise zu wählen, vor allem, wenn die Groß/Klein-Schreibung eine Rolle spielt und Verwechslungen möglich sind (z.B. „G/L“=Giga pro Liter vs. „g/L“=Gramm/Liter). Also '10^6 ' statt 'M' (Mega), '10^9 ' statt 'G ' (Giga) usw.
1.3.5.4 Befundinterpretation
Es ist in Laborbefunden üblich, eine codierte Bewertung zu jedem Ergebnis anzugeben. Häufig wird eine Notierung mit +/- verwendet.
Folgende Tabelle 7 ist ein Auszug aus dem Value Set „ELGA_ObservationInterpretation“ und zeigt die normative Befundinterpretation für numerische Ergebnisse, Tabelle 8 (ebenfalls aus dem gleichen Value Set) die Kennzeichnung für nicht numerische Ergebnisse.
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| ++ | HH | Oberhalb des Referenzbereiches und über einer oberen Warngrenze |
| + | H | Oberhalb des Referenzbereiches |
| N | Normal (innerhalb des Referenzbereiches) | |
| - | L | Unterhalb des Referenzbereiches |
| -- | LL | Unterhalb des Referenzbereiches und unter einer unteren Warngrenze |
Tabelle 7: Befundinterpretation numerischer Ergebnisse
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| N | Normal (innerhalb des Referenzbereiches) | |
| * | A | Abnormal |
| ** | AA | Abnormal Warngrenze |
Tabelle 8: Befundinterpretation nicht numerischer Ergebnisse (nominal, ordinal, narrativ)
Zur Interpretation von Ergebnissen der Allergiediagnostik wurden zusätzlich RAST-Klassen als Klassifikation erlaubt, siehe Kapitel Empfehlungen für die Darstellung der Allergiediagnostik.
1.3.5.5 Empfehlungen für die Darstellung der Allergiediagnostik
In der Allergiediagnostik gibt es gegebenenfalls Abweichungen zur normalen Struktur des Laborbefundes. Die Angabe der getesteten Allergene bei Globalmarkern oder die zusätzliche Angabe von RAST-Klassen machen eine alternative Darstellung notwendig.
Folgende Darstellung wird dazu EMPFOHLEN:

Abbildung 13: Empfohlene Darstellung von Globalmarkern und Angabe der RAST-Klasse als Interpretation eines numerischen Ergebnisses. Sofern die RAST-Klasse angegeben wird, ist Option 3 empfohlen.
Folgendes Codebeispiel zeigt die Befunddarstellung der Globalmarker im narrativen Text:
<table>
<thead>
<tr>
<th styleCode="xELGA_colw:80">Analyse</th>
<th styleCode="xELGA_colw:10">Ergebnis</th>
<th styleCode="xELGA_colw:10">Interpretation</th>
</tr>
</thead>
<tbody>
<tr ID="OBS-1-1">
<td>sx1 Inhalatives Screening<br/>
<content styleCode="italics">Lieschgras, Roggen, Birke, Beifuß, Dermatophagoides pteronyssinus,
Katzenschuppen, Hundeschuppen, Cladosporium herbarum</content>
</td>
<td>negativ</td>
<td></td>
</tr>
<tr ID="OBS-1-2" styleCode="xELGA_red">
<td>mx1 Schimmelpilzemix 1<br/>
<content styleCode="italics">Alternaria alternata, Aspergillus fumigatus, Cladosporium herbarum,
Penicillium notatum</content></td>
<td>positiv</td>
<td>A</td>
</tr>
</tbody>
</table>
1.3.6 Stylecodes
Für die spezifische grafische Darstellung und bessere optische Aufbereitung stehen verschiedene definierte Stylecodes zur Verfügung. Tabelle 9 zeigt einen Überblick.
| Stylecode | Primäre Verwendung in Element | Nutzung |
|---|---|---|
| xELGA_h1 | <paragraph> | Überschriften gem. HTML < h1> |
| xELGA_h2 | <paragraph> | Überschriften gem. HTML < h2> |
| xELGA_h3 | <paragraph> | Überschriften gem. HTML < h3> |
| xELGA_red | <tr> | Kennzeichnung pathologischer Messwerte (ganze Ergebniszeile) |
Tabelle 9: Level 2 Stylecodes
1.3.7 Bemerkungen/Kommentare
Es gibt vier Arten von Bemerkungen:
- zu einem einzelnen Analyseergebnis
- zu einer Befundgruppe
- zu einem Bereich
- zum gesamten Befund, über alle Bereiche
1.3.7.1 Bemerkungen zu Analysen oder Analyseergebnissen
Existiert zu einer Analyse oder einem Analyseergebnis eine Bemerkung (z.B. um die Analyse oder das Ergebnis näher zu beschreiben), so wird die Analyse oder das Ergebnis mit einer Fußnotenreferenz versehen und die eigentliche Bemerkung im Footer der Ergebnistabelle dargestellt.
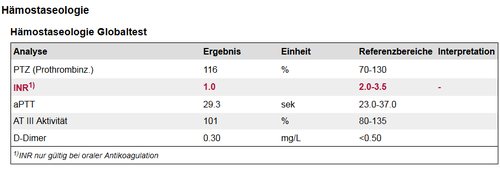
Abbildung 14: Darstellung einer Bemerkung zu einer Analyse
Die Fußnotenreferenzen werden fortlaufend nummeriert und durch einen sup-Tag hochgestellt. Der Text wird unter tfoot-Element mit dem footnote-Tag gekennzeichnet. Die ID gibt eine eindeutige Referenz auf den Text einer Fußnote.
<table>
<thead>
...
</thead>
<tfoot>
<tr>
<td>
<footnote ID="fn1">
<sup>1)</sup>INR nur gültig bei oraler Antikoagulation
</footnote>
</td>
</tr>
</tfoot>
<tbody>
...
<tr ID="OBS-2-2" styleCode="xELGA_red">
<td>INR<sup>1)</sup></td>
<td>1.0</td>
<td></td>
<td ID="OBSREF-2-2">2.0-3.5</td>
<td>-</td>
</tr>
...
<tbody>
</table>
1.3.7.2 Bemerkungen zu Befundgruppen
Bemerkungen zu Befundgruppen werden als eigener Absatz (paragraph-Element) nach der entsprechenden Ergebnistabelle codiert. Um den Text der Bemerkung aus Level 3 referenzierbar zu machen, MUSS dieser von einem content-Tag mit einer eindeutigen ID eingeschlossen werden (vgl. Kapitel Referenz von Level 3 auf Level 2).
<!-- Befundgruppe Blutbild --> <caption styleCode="xELGA_h2">Blutbild</caption> <table> ... </table> <paragraph> <content ID="BB_Comment">Das ist eine Bemerkung für die Gruppe Blutbild</content> </paragraph>
1.3.7.3 Bemerkungen zu einem Befundbereich
Bemerkungen zu einer Befundart werden am Ende der Codierung des Befundbereichs(Speciality) als Tabelle codiert. Um den Text der Bemerkung aus Level 3 referenzierbar zu machen, MUSS dieser von einem content-Tag mit einer eindeutigen ID eingeschlossen werden (vgl. Referenz von Level 3 auf Level 2).
<table>
<thead>
<tr>
<th>Befundbewertung</th>
</tr>
</thead>
<tbody>
<tr>
<td><paragraph><content ID="commonComment1">Das ist die Bewertung für den
"Allgemeinen Laborbefund". Diese kann auch sehr lange ausfallen.
</content></paragraph>
</td>
</tr>
</tbody>
</table>
1.3.7.4 Bemerkung zum gesamten Befund über alle Bereiche
Bemerkungen oder Kommentare, welche für den gesamten Befund von Bedeutung sind, werden in einer eigenen Sektion am Befundende geführt. Der menschenlesbare Text im <text> Element ist mit einer ID zu versehen, um auf diesen Text im Level 3 entry-Element referenzieren zu können. Die Spezifikation dieses Elements ist in Kapitel Bereichsübergreifende Befundbewertung ersichtlich.
1.3.8 Eigenschaften des Materials/Mikroskopie

Abbildung 16: Eigenschaften des Materials/Mikroskopie
Die Tabellendarstellung zeigt eine Eigenschaft des zu untersuchenden Materials mit dem zugehörigen Ergebnis sowie, wenn anwendbar, einer physikalischen Einheit.
1.3.8.1 Spezifikation
| Id | 1.2.40.0.34.11.4.2.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | MikroskopieSektion | Bezeichnung | Sektion Mikroskopie | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Eigenschaften des Materials/Mikroskopie | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.3 Sektion Mikroskopie (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.3.9 Kultureller Erregernachweis
Der Erregernachweis enthält Ergebnisse, welche mit Hilfe von Kulturen erlangt werden, und repräsentiert diese als Tabelle. Jede Zeile dieser Tabelle enthält die Bezeichnung des Erregers, die Methodik der Untersuchungsdurchführung sowie die Keimzahl. Vorgeschlagene Methodiken wären zum Beispiel:
- Kultur (nach Bedarf anaerob/aerob)
- Pilzkultur
- …
Sollte kein Erreger nachweisbar sein (ggf. aber apathogene Keime), wird folgende Formulierung EMPFOHLEN: „Erreger nicht nachweisbar“.
Sollten gar keine Keime (oder Mikroorganismen) nachweisbar sein, wird wird folgende Formulierung EMPFOHLEN: „Keime (oder Mikroorganismen) nicht nachweisbar“.
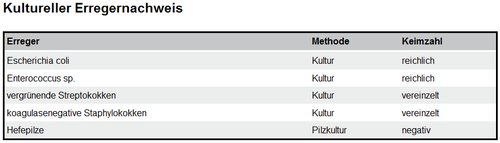
Abbildung 17: Kultureller Erregernachweis
1.3.9.1 Strukturbeispiel
:
<title>Kultureller Erregernachweis</title>
<text>
<table>
<thead>
<tr>
<th>Erreger</th>
<th>Methode</th>
<th>Keimzahl</th>
</tr>
</thead>
<tbody>
<tr ID="OBS-2-3">
<td>Escherichia coli</td>
<td>Kultur</td>
<td>reichlich</td>
</tr>
<tr ID="OBS-2-4">
<td>Enterococcus sp.</td>
<td>Kultur</td>
<td>reichlich</td>
</tr>
:
</tbody>
</table>
:
</text>
1.3.10 Antibiogramm
Das Antibiogramm wird bei Vorliegen von mehreren Antibiogrammen im Befund als Matrix dargestellt. Falls die Matrixdarstellung bei zu vielen Antibiogrammen zu unübersichtlich wird, können die einzelnen Antibiogramme jeweils als dem Erreger nachgereihte Tabelle angegeben werden. Die folgende Abbildung zeigt ein Beispiel mit zwei Erregern als Matrixdarstellung.
1.3.10.1 Strukturbeispiel
<table> <thead> <tr> <th>Wirkstoff</th> <th>Pseudomonas aeruginosa</th> <th>Escherichia coli</th> </tr> </thead> <tbody> <tr ID="AB-1-1"> <td>Amoxicillin</td> <td>R</td> <td>I</td> </tr> <tr ID="AB-2-1"> <td>Ampicillin</td> <td></td> <td>S</td> </tr> <tr ID="AB-3-1"> <td>Fosfomycin</td> <td>R</td> <td></td> </tr> </tbody> </table>
1.3.11 Minimale Hemmkonzentration
Die minimale Hemmkonzentration (MHK) wird im Befund als Matrix angezeigt. Die folgende Abbildung zeigt ein Beispiel für die Bildschirmdarstellung der minimalen Hemmkonzentration.

Abbildung 19: Minimale Hemmkonzentration
1.3.11.1 Strukturbeispiel
<table> <thead> <tr> <th>Wirkstoff</th> <th>Pseudomonas aeruginosa<br/>Abs.Wert[ug/mL]</th> <th>Escherichia coli<br/>Abs.Wert[ug/mL]</th> </tr> </thead> <tbody> <tr ID="MIC-1-1"> <td>Amoxicillin</td> <td>4</td> <td>2</td> </tr> <tr ID="MIC-2-1"> <td>Ampicillin</td> <td></td> <td>0.5</td> </tr> <tr ID="MIC-3-1"> <td>Fosfomycin</td> <td>16</td> <td></td> </tr> <tr ID="MIC-4-1"> <td>Levofloxacin</td> <td>0.25</td> <td>4</td> </tr> </tbody> </table>
1.3.12 Testergebnisse/Molekularer Erregernachweis
Die Ergebnisse werden in einer Tabelle angeführt, welche strukturell einer Ergebnistabelle ähnelt. Abbildung 20 zeigt ein Beispiel der Tabellenstruktur. In die Spalte „Analyse/Erreger/Methode“ wird der Erreger eingetragen, sowie die Methodik vermerkt, mit der der Erreger untersucht wurde. Das Value Set „ELGA_Laborparameter“ definiert gültige Bezeichnungen für die Spalte „Analyse/Erreger/Methode“. Die Umsetzung erfolgt analog zur Level 2 Befundstruktur (siehe Kapitel Level 2 Befundstruktur).
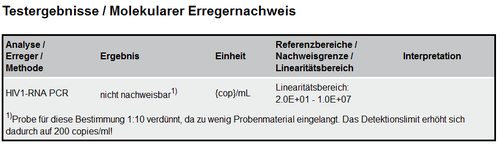
Abbildung 20: Testergebnisse/Molekularer Erregernachweis
1.3.13 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012
Die Vorgaben dieses Implementierungsleitfadens erlauben die Erzeugung von Befunden gemäß ISO 15189:2012 "Medizinische Laboratorien - Anforderungen an die Qualität und Kompetenz" [10], speziell in Hinblick auf die dort angegebenen Kapitel 5.8 (Befundberichte) und 5.9 (Freigabe der Ergebnisse). Für akkreditierte Laboratorien sind neben [10] folgende Hinweise zu beachten:
1.3.14 Angabe des Akkreditierungs-Logos
Das Akkreditierungs-Logo kann neben dem Logo des Labors angegeben werden. Technisch erfolgt das über die Section Brieftext, das Logo ist ggf. gemeinsam mit dem Logo des Labors in einer Grafikdatei anzugeben (6.2.2).

Abbildung 21: Angabe des Akkreditierungs-Logos im Briefkopf
Ein Labor muss nicht zwingend für alle Analysen, die es durchführen kann, akkreditiert sein. Das Akkreditierungs-Logo kann angegeben werden, sobald es akkreditierte Analysen gibt; wenn „nicht akkreditierte Analysen“ am Befund erscheinen, soll bei diesen angegeben werden können, dass das Labor für diese Analyse nicht akkreditiert ist. Für die entsprechend Markierung wird die Verwendung von Anmerkungszeichen (wie z.B. *) und Endnoten empfohlen.
1.3.15 Angabe des Untersuchungs- bzw Messverfahrens
Wenn der Name der Analysen keinen Rückschluss auf die Methode erlaubt, aber Untersuchungs- bzw Messverfahren dennoch angegeben werden sollen ([10], Vorgabe 5.8.3 a)), soll dies als Kommentar zur Analyse erfolgen (siehe Bemerkungen zu Analysen oder Analyseergebnissen).
1.3.16 Vorgaben für den Befunddruck
Einige Vorgaben von ISO 15189:2012 beziehen sich auf Qualitätsmerkmale für gedruckte Befunde ([10], Vorgabe 5.8.3 d „Identifizierung des Patienten und den Aufenthaltsort des Patienten auf jeder Seite“ und Vorgabe 5.8.3 p „Seitenzahl zur Gesamtzahl der Seiten“). Dieser Leitfaden definiert ein elektronisches Format, das diese Anforderungen grundsätzlich unterstützt. Am ELGA-Portal (Zugriff für Bürger) werden Tools zur Darstellung eingesetzt, die diese Vorgaben unterstützen. Diese Tools werden auch von der ELGA GmbH zum Download bereigestellt (Referenzstylesheet, CDA2PDF auf http://www.elga.gv.at/CDA).
1.4 Spezifikation des Body Level 3
1.4.1 Überblick
| Feld | Opt | Darstellung | Details |
|---|---|---|---|
| Allgemeine Befundinformationen | |||
| Auftragsdiagnose und Fragestellung | ClinicalDocument/component/structuredBody/component/section/.. | O [0..*] |
Link |
| Spezimeninformation | |||
| Abnahmeinformationen (Specimen Collection) | ../entry/act/entryRelationship/procedure <template root=”1.3.6.1.4.1.19376.1.3.1.2”> | R2 [0..*] |
Link |
| Annahmeinformationen (Specimen Received) | ../entry/act/entryRelationship/procedure/entryRelationship/act <template root=”1.3.6.1.4.1.19376.1.3.1.3”> | R2 [0..*] |
Link |
| Befundgruppen | |||
| Befundgruppen (Laboratory Battery Organizer) | ../entry/act/entryRelationship/organizer | O [0..*] |
Link |
| Laborergebnisse (Laboratory Observation) | ../entry/act/entryRelationship/organizer/component/observation/ <templateId root="1.3.6.1.4.1.19376.1.3.1.6"> | ||
| Analyse: Identifikation/Codierung | ../id und ../code | M [1..1] |
Link |
| Ergebnis und Einheit | ../value | M [1..1] |
Link |
| Referenzbereiche | ../referenceRange | R2 [0..*] |
Link |
| Befundinterpretation | ../interpretationCode | R2 [0..*] |
Link |
| Kommentar zu einer Analyse | ../entryRelationship/act | 0 [0..1] |
Link |
| Externes Labor | ../performer | C [0..1] |
Link |
| Kultureller Erregernachweis | ../entry/act/entryRelationship/organizer | ||
| Erregernachweis mit Definition der Methodik | ../component/observation | R2 [0..*] |
Link |
| Antibiogramm und minimale Hemmkonzentration | ../entry/act/entryRelationship/organizer | ||
| Antibiogramm und minimale Hemmkonzentration | ../component/organizer | R2 [0..*] |
Link, Link |
| Testergebnisse / Molekularer Erregernachweis | ../entry/act/entryRelationship/organizer | ||
| Testergebnisse und Molekularer Erregernachweis | ../component/observation | R2 [0..*] |
Link |
| Significant Pathogens | ../entry/act/entryRelationship/organizer | ||
| Significant Pathogens | ../component/organizer | C [0..1] |
Link |
1.4.2 Überweisungsgrund
Der Überweisungsgrund enthält die dem Labor übermittelte Auftrags- oder Verdachtsdiagnose bzw. Fragestellung.Die Angabe erfolgt in einer Section im Body des CDA-Dokuments.
1.4.2.1 Überblick
| EIS „Enhanced“ und „Full Support“ | |
|---|---|
| Template ID | ELGA: 1.2.40.0.34.11.4.2.4 |
| Parent Template ID | - |
| Titel der Sektion | Überweisungsgrund |
| Definition | Der Grund für eine Gesundheitsdienstleistung (hier: Laborbefund). Enthält eine narrative Beschreibung des Grundes für den Auftrag (Beschreibung aus der Sicht des Gesundheitsdiensteanbieters) und/oder die eigene Beschreibung des Patienten (z.B. Hauptsymptom des Patienten) |
| Codierung | LOINC: 46239-0, „Chief complaint+Reason for visit“ |
| Konformität | [O] |
| Konformität Level 3 | [NP] |
1.4.2.2 Spezifikation
| Id | 1.2.40.0.34.11.4.2.4 ref elgabbr- | Gültigkeit ab | 2015‑09‑24 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Ueberweisungsgrund | Bezeichnung | Überweisungsgrund | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.4 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.4 Überweisungsgrund (2015‑09‑24) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.3 Laboratory Report Data Processing Entry
Die Angabe eines entry-Eintrages im Rahmen der Codierung einer Befundart ist Pflicht. Dieses Element wird gem. [3] als „Laboratory Report Data Processing Entry“ bezeichnet und folgt einem spezifischen Template.
<templateId root="1.3.6.1.4.1.19376.1.3.1" extension="Lab.Report.Data.Processing.Entry"/>
Der entry-Eintrag ist mit dem Attribute typeCode=“DRIV“ zu versehen, um anzuzeigen, dass der Level 2 vollständig aus dem Level 3 erzeugt werden kann.
Das entry-Element enthält genau ein act-Subelement – den sogenannten „Spezimen-Act“.
1.4.4 Der Spezimen-Act
Wie bereits in Kapitel CDA Entry Level („Level 3“) angeführt, erfolgt die Codierung der Ergebnisse zu einer Befundart immer auf oberster Ebene unter genau einem act-Element – dem „Spezimen–Act“. Damit befindet sich unter dem component/section/entry-Element immer genau ein Unterelement. Alle weiteren Elemente - sowohl Spezimen als auch Befundgruppen, Untersuchungen etc. - werden in der Hierarchie unter dem Spezimen-Act codiert. Der Act MUSS zumindest eine Untersuchung beinhalten.
1.4.4.1 Spezifikation
| Id | 1.2.40.0.34.11.30020 ref elgabbr- | Gültigkeit ab | 2017‑02‑22 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpezimenActEntryAllgemein | Bezeichnung | ELGA Spezimen-Act-Entry Allgemein | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30020 ELGA Spezimen-Act-Entry Allgemein (2017‑02‑22) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.5 Probeninformationen (Specimen-Section)
1.4.5.1 Überblick
In der aktuellen Version des „Laboratory Technical Framework Volume 3 – Revision 3.0“ (LAB TF-3) wurde die Vorgangsweise zur Codierung des Spezimen grundlegend geändert. Die zum Teil noch verbreitete Variante der Spezimen-Codierung laut „Laboratory Technical Framework Volume 3 – Revision 2.1“ sah vor, dass man ein oder mehrere Specimen/Proben mittels des specimen-Elementes innerhalb des Specimen-Act codieren konnte. In Version 3.0 des LAB TF-3 kann ein Spezimen/Probe nur über ein entryRelationship als Specimen-Collection angegeben werden.
Die Codierung von Informationen zum Spezimen ist für Befunde der ELGA Interoperabilitäts Stufe „Full support“ verpflichtend. Diese Codierung erfolgt bei Befunden, welche aus mehreren Bereichen bestehen in einer eigenen Sektion „Probeninformation“. Bei Befunden, welche nur aus einer Sektion bestehen kann die Codierung der Information zum Spezimen auch in dieser Sektion geschehen.
1.4.5.2 Spezimen-Section
1.4.5.2.1 Spezifikation
Specimen Section
| Id | 1.2.40.0.34.11.4.2.1 ref elgabbr- | Gültigkeit ab | 2013‑11‑07 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpezimenSection | Bezeichnung | Spezimen-Section | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.1 Spezimen-Section (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Specimen Entry
| Id | 1.2.40.0.34.11.4.3.1 ref elgabbr- | Gültigkeit ab | 2013‑02‑10 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratorySpecimenEntry | Bezeichnung | Laboratory Specimen Entry | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.5.3 Abnahmeinformationen (Specimen Collection)
1.4.5.3.1 Überblick
Abnahmeinformationen werden analog zu den Vorgaben der IHE ([3]) als „Specimen Collection“ Block unter dem Spezimen-Act codiert. Die Darstellung erfolgt über ein act-Element, welches über eine entryRelationship Verbindung mit dem Spezimen-Act verbunden ist (../entry/act/entryRelationship/act).
1.4.5.3.2 Spezifikation
| Id | 1.2.40.0.34.11.30021 ref elgabbr- | Gültigkeit ab | 2014‑03‑04 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpecimenCollection | Bezeichnung | Abnahmeinformationen (Specimen Collection) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30021 Abnahmeinformationen (Specimen Collection) (2014‑03‑04) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.5.4 Annahmeinformationen (Specimen Received)
1.4.5.4.1 Überblick
Informationen zur Probenannahme werden analog zu den Vorgaben der IHE ([3]) als „Specimen Received“ Block unter dem Spezimen-Act codiert. Die Darstellung erfolgt über ein act-Element, welches über eine entryRelationship Verbindung mit dem Spezimen-Act verbunden ist (../entry/act/entryRelationship/act).
1.4.5.4.2 Spezifikation
| Id | 1.2.40.0.34.11.30022 ref elgabbr- | Gültigkeit ab | 2014‑03‑04 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpecimenReceived | Bezeichnung | Annahmeinformationen (Specimen Received) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30022 Annahmeinformationen (Specimen Received) (2014‑03‑04) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.5.4.3 Allgemeine Anmerkungen des Labors zur Spezimenqualität
Anmerkungen zur Spezimenqualität werden als Annotation-Act unter dem act-Element über eine Verknüpfung durch ein entryRelationship-Element implementiert (vgl. Kommentar zu einer Analyse).
1.4.6 Befundgruppen (Laboratory Battery Organizer)
1.4.6.1 Überblick
Innerhalb einer Befundart kann auf zweiter Ebene die Strukturierung nach Befundgruppen erfolgen. Diese werden in Form von Laboratory Battery Organizer (vgl. [3]), welche eine Gruppierung von Ergebnissen ermöglichen, dargestellt. Die Implementierung erfolgt über einen organizer, welcher mittels entryRelationship mit dem Spezimen-Act verbunden ist. Die Struktur entspricht einem Template, welches verpflichtend anzugeben ist.
<templateId root="1.3.6.1.4.1.19376.1.3.1.4"/>
Die Untersuchungsergebnisse werden als component unter dem Organizer abgebildet.
Für die Codierung des code-Elementes sind Codes der Ebene 2 der hierarchischen Liste „ELGA_Laborstruktur“ zu verwenden.
1.4.6.2 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.1.4 ref elgabbr- | Gültigkeit ab | 2017‑02‑23 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryBatteryOrganizer | Bezeichnung | Befundgruppen (Laboratory Battery Organizer) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.4 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.4 Befundgruppen (Laboratory Battery Organizer) (2017‑02‑23) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.6.2.1 Laborergebnis
| Id | 1.3.6.1.4.1.19376.1.3.1.6 ref elgabbr- | Gültigkeit ab | 2020‑06‑15 08:50:28 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryObservation | Bezeichnung | Laborergebnisse (Laboratory Observation) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.6 Laborergebnisse (Laboratory Observation) (2015‑03‑26) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.6.2.2 Befundtext (Anmerkungen und Kommentare)
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.7 Laborergebnisse (Laboratory Observation)
1.4.7.1 Überblick
Ergebnisse einer Laboruntersuchung werden als observation-Block codiert. Jede Observation stellt das Ergebnis zu genau einer Laboruntersuchung dar; entweder als Einzeluntersuchung direkt unter dem Spezimen-Act oder als Teil einer Befundgruppe (Laboratory Battery Organizer). Dies entspricht einem spezifischen Template welches verpflichtend als Element anzuführen ist.
<templateId root="1.3.6.1.4.1.19376.1.3.1.6"/>
1.4.7.2 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.1.6 ref elgabbr- | Gültigkeit ab | 2020‑06‑15 08:50:28 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryObservation | Bezeichnung | Laborergebnisse (Laboratory Observation) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.6 Laborergebnisse (Laboratory Observation) (2015‑03‑26) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.7.2.1 Durchführende Instanz / externes Labor (observation/performer)
| Id | 1.2.40.0.34.11.4.3.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryPerformer2 | Bezeichnung | Laboratory Performer 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Element zur Kennzeichnung einer Analyse, die in einem externen Labor durchgeführt wurde. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.3 Laboratory Performer 2 (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.7.2.2 EntryRelationship (observation/entryRelationship)
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.7.3 Analyse: Identifikation/Codierung
Die Angabe der Laboruntersuchungen (Analyse, Test) hat prinzipiell codiert zu erfolgen. Das entsprechende Element ist das code-Element (das id-Feld stellt eine interne Codierung dar und ist optional). Siehe dazu auch den „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
1.4.7.3.1 Strukturbeispiel
<id extension="OBS-1-3" root="2.16.840.1.113883.2.16.1.99.3.1"/> <code code="26453-1" codeSystem="2.16.840.1.113883.6.1!" codeSystemName="LOINC" displayName="Erythrozyten"/>
1.4.7.3.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| code | CE CWE |
0..1 | C | Codierung der Analyse / des Tests | |
| Konditionale Konformität: EIS „Enhanced“ EIS „Basic“ |
1..1 0..1 |
R O |
Ein maschinenlesbares Element. NullFlavor siehe 6.4.7.4.3 Maschinenlesbares Element optional Ist kein Code für eine zu codierende Analyse verfügbar, ist laut Kapitel Laborergebnisse ohne passenden Code vorzugehen. | ||
| @code | cs | 1..1 | M | Code aus Value Set ELGA_Laborparameter | |
| @displayName | st | 0..1 | R2 | Displayname des Code-Werts aus dem Value Set ELGA_Laborparameter | |
| @codeSystem | uid | 1..1 | M | Parent-OID aus Value Set ELGA_LaborParameter (1.2.40.0.34.10.44) | |
| @codeSystemName | st | 0..1 | R2 | Parent-Codesystemname aus Value Set ELGA_LaborParameter | |
1.4.7.3.3 Laborergebnisse ohne passenden Code
Sollte in dem Value Set „ELGA_Laborparameter“ kein Code für die Laboranalyse verfügbar sein, kann die Analyse dennoch maschinenlesbar hinterlegt werden mit der Kennzeichnung, dass der Wert nicht aus dem Value Set stammt. Das gilt auch für den Fall, dass ein passender LOINC Code exisitiert, aber nicht im aktuellen Value Set „ELGA_Laborparameter“ enthalten ist.Es wird gebeten, dass benötigte Codes umgehend an ELGA gemeldet werden um diese im Zuge von Reviewzyklen in die Codelisten und Value Sets einzupflegen.
Für die Befunddarstellung solcher Analysen wird empfohlen, dass diese jeweils am Ende der thematisch passendsten Gruppe einzureihen sind, solange es noch keine andere Vorgabe oder Empfehlung gibt.
1.4.7.3.3.1 Strukturbeispiel
<id extension="OBS-1-3" root="2.16.840.1.113883.2.16.1.99.3.1"/> <code nullFlavor="OTH"> <translation code="alternativerCode" codeSystem="alternativeCodeSystem" displayName="klarTextDarstellung" codeSystemName="NameDesCodeSystems"/> </code>
1.4.7.3.3.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |||
|---|---|---|---|---|---|---|---|
| code | CE CWE |
1..1 | C | ||||
| Konditionale Konformität:Anzugeben wenn im Value Set „ELGA_Laborparameter“ kein passender Code für die Laboranalyse verfügbar ist. | |||||||
| @nullFlavor | cs | 1..1 | M | Fester Wert: OTH | |||
| translation | CE CWE |
1..1 | M | Codierung der Analyse in einem alternativen Codesystem
Die Verwendung von LOINC Codes wird empfohlen. | |||
| @code | cs | 1..1 | M | Code aus einem alternativen Codesystem | |||
| @codeSystem | uid | 1..1 | M | Identifikation des alternativen Codesystems | |||
| @displayName | st | 0..1 | R2 | Displayname des Codes | |||
| @codeSystemName | st | 0..1 | R2 | Codesystemname | |||
1.4.7.4 Ergebnis und Einheit
Die Angabe des Ergebnisses einer Laboruntersuchung erfolgt durch das value-Element. Die Codierung erfolgt gemäß dem Datentyp, welcher durch das xsi:type-Attribut ausgedrückt wird, hinter dem sich eine fixe Liste möglicher Datentypen verbirgt. Numerische Ergebnisse werden in der Regel als „physical quantity“ PQ dargestellt, was die Angabe einer UCUM codierten Einheit erforderlich macht. Es MUSS die „case sensitive“ Variante (c/s) der maschinenlesbaren Form des UCUM verwendet werden. Die bevorzugte Einheit für jede Analyse wird Value Set ELGA_Laborparameter vorgeschlagen, jeweils in der „print“ Variante (für die Darstellung) und in der maschinenlesbaren Form.
Es wird EMPFOHLEN, anstelle von Einheitenpräfixen („Giga“, „Mega“, „Milli“, „Mikro“ etc.) eine Potenzschreibweise zu wählen, vor allem, wenn die Groß/Klein-Schreibung eine Rolle spielt und Verwechslungen möglich sind (z.B. „G/L“=Giga pro Liter vs. „g/L“=Gramm/Liter). Also '10^6 ' statt 'M' (Mega), '10^9 ' statt 'G ' (Giga) usw.
1.4.7.4.1 Strukturbeispiele
Die Dokumentation eines numerischen Ergebniswertes erfolgt in diesem Fall als Attribut.
<value xsi:type="PQ" value="49.7" unit="%"/>
Die Codierung von textuellen Ergebnissen erfolgt in der Regel durch den “ST” Datentyp. Die Angabe des Ergebnisses erfolgt hier als Wert des Elementes.
<value xsi:type="ST">strohgelb</value>
Im narrativen Block MUSS derselbe Text wie im Entry dargestellt werden.
Auch für dimensionslose Einheiten wird in UCUM häufig eine Einheit angegeben, wie z.B. "[ph]" für den pH-Wert. Wenn keine UCUM-Einheit vorgeschlagen ist, können dimensionslose Einheiten auch mit @unit="1" dargestellt werden, hier für INR:
<value xsi:type="PQ" value="1.1" unit="1"/>
Für Verhältnisangaben, wie sie etwa für Titer verwendet werden (z.B. „1:128“) steht der Datentyp RTO (Ratio) zur Verfügung. Ein Anwendungsbeispiel:
<value xsi:type="RTO"> <numerator value="1" xsi:type="INT"/> <denominator value="128" xsi:type="INT"/> </value>
Intervalle können mit dem Datentyp IVL angegeben werden, z.B. „20-30 mg/L“:
<value xsi:type="IVL_PQ" > <low value="20" unit="mg/dl" inclusive="true"/> <high value="30" unit="mg/dl" inclusive="true"/> </value>
Das Attribut inclusive gibt mit true/false an, ob die Intervallgrenze im Intervall enthalten ist oder nicht (offenes oder geschlossenes Intervall)
1.4.7.4.2 Spezifikation
Für numerische Werte gilt:
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| value | PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ | 0..1 | O | ||
| @unit | cs | 1..1 | C | Physikalisch Einheit des Messwertes. UCUM Codierung empfohlen (siehe [7]) | |
| Konditionale Konformität: Bei EIS „Basic“ Bei EIS „Enhanced“ und „Full Support“ |
1..1 1..1 |
R2 M |
Angabe der Einheit erforderlich Angabe der Einheit nach UCUM (c/s) erforderlich. | ||
| @value | real | 1..1 | M | Größe des Messwertes | |
| @xsi:type | cs | 1..1 | M | Datentyp: für numerische Werte PQ | |
1.4.7.5 Befundinterpretation
Die Befundinterpretation wird als Subelement interpretationCode unter der observation codiert. Je Bereich darf nur eine entsprechend codierte Bewertung angegeben werden (nur eine Befundinterpretation). Die Codierung erfolgt gem. ELGA Value Set „ELGA_ObservationInterpretation“. Folgende Tabelle 10 zeigt die normative Befundinterpretation für numerische Ergebnisse, Tabelle 11 die Kennzeichnung für nicht numerische Ergebnisse, die nominal, ordinal und narrativ sein können.
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| ++ | HH | Oberhalb des Referenzbereiches und über einer oberen Warngrenze |
| + | H | Oberhalb des Referenzbereiches |
| N | Normal (innerhalb des Referenzbereiches) | |
| - | L | Unterhalb des Referenzbereiches |
| -- | LL | Unterhalb des Referenzbereiches und unter einer unteren Warngrenze |
Tabelle 10: Befundinterpretation numerischer Ergebnisse
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| N | Normal (innerhalb des Referenzbereiches) | |
| * | A | Abnormal |
| ** | AA | Abnormal Warngrenze |
Tabelle 11: Befundinterpretation nicht numerischer Ergebnisse
1.4.7.5.1 Strukturbeispiel
Beispiel für numerische Ergebnisse
<interpretationCode code="H" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation" displayName="High"/>
Beispiel für nicht-numerische Ergebnisse
<interpretationCode code="AA" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation" displayName="Abnormal Alert"/>
1.4.7.5.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| interpretationCode | CE CNE | 0..1 | CE CNE | ||
| Konditionale Konformität: EIS „Enhanced“ EIS „Basic“ |
1..1 0..1 |
M O |
Ein maschinenlesbares Element Ein maschinenlesbares Element | ||
| @code | cs | 1..1 | M | Code aus Value Set „ELGA_ObservationInterpretation“ | |
| @codeSystem | uid | 1..1 | M | Fester Wert: „2.16.840.1.113883.5.83“ | |
| @codeSystemName | st | 0..1 | R2 | Fester Wert: „HL7:ObservationInterpretation“ | |
| @displayName | st | 0..1 | R2 | Klartext-Darstellung des Codes | |
1.4.7.6 Validator
Zu jedem Ergebnis kann optional die validierende Person angegeben werden. Die Codierung erfolgt unter der Observation als participant mit dem Attribut typeCode=“AUTHEN“ und folgt einem spezifischen Template, welches diesen Participant als Validator kennzeichnet. Das Template ist verpflichtend anzugeben.
<templateId root="1.3.6.1.4.1.19376.1.3.3.1.5"/>
Weiters sind bei jeder Personenangabe die Elemente telecom und addr verpflichtend anzuführen, können jedoch mit einem nullFlavor versehen werden.
Wird zu einem Ergebnis eine validierende Person gelistet, ist diese auch im Header als authenticator anzuführen.
1.4.7.6.1 Strukturbeispiel
<participant typeCode="AUTHEN">
<templateId root="1.3.6.1.4.1.19376.1.3.3.1.5"/>
<time>
<low value="20130123211000.007-0500"/>
<high nullFlavor="UNK"/>
</time>
<participantRole>
<id extension="332" root="1.3.6.1.4.1.19376.1.3.4"/>
<addr nullFlavor"UNK"/>
<telecom value="tel: 312.555.5555"/>
<playingEntity>
<name>Susanne Hecht</name>
</playingEntity>
</participantRole>
</participant>
1.4.7.6.2 Spezifikation
1.4.7.6.2.1 Validator - Allgemein (observation/participant)
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| participant | POCD_MT000040.Participant | 0..* | O | ||
| @typeCode | cs | 1..1 | M | Fester Wert: AUTHEN | |
1.4.7.6.2.2 TemplateId (participant/templateId)
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| templateId | II | 1..1 | M | Template zur Codierung einer validierenden Person | |
| @root | uid | 1..1 | M | Fester Wert: „1.3.6.1.4.1.19376.1.3.3.1.5“ | |
1.4.7.6.2.3 TemplateId (participant/templateId)
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| time | IVL_TS | 1..1 | M | Zeitpunkt der Validierung: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ |
1.4.7.6.2.4 Angaben zur validierenden Person (participant/participantRole)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||
|---|---|---|---|---|---|---|
| participantRole | POCD_MT000040.ParticipantRole | 1..1 | M | |||
| id | II | 1..1 | M | Identifikation der Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ | ||
| addr | AD | 1..1 | R | Adresse der Person/Organisation: Identifikation der Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ Zugelassene nullFlavor: UNK | ||
| telecom | TEL | 1..* | R | Kontaktdaten zur Person/Organisation:Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ Zugelassene nullFlavor: UNK | ||
| playingEntity | POCD_MT000040.PlayingEntity | 1..1 | R | |||
| name | PN | 1..1 | M | Name der validierenden Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ | ||
1.4.7.7 Referenzbereiche
Für die Bewertung der Laborergebnisse werden Referenzbereiche herangezogen, welche im Befund zu dokumentieren sind. Die Angabe erfolgt als referenceRange-Block unter der observation. Die Werte werden darunter in einem Block observationRange als Element value abgelegt. Die Ausprägung des Elementes erfolgt wiederum gem. einem Datentyp, welcher durch das Attribut xsi:type angegeben wird. Für numerische Werte wird der Referenzbereich in den meisten Fällen ein Intervall physikalischer Größen „IVL_PQ“ sein, welches in der Regel durch einen low und einen high Wert angegeben wird. Nachfolgendes Beispiel zeigt die Verwendung des referenceRange-Blocks mit einem Referenzbereich für normale Werte.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-1-5"> <td>Hämatokrit</td> <td>47.9</td> <td>G/l</td> <td ID="OBSREF-1-5">43.0 - 49.0</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-1-5"/> </text> <value xsi:type="IVL_PQ"> <low value="43.0" unit="%"/> <high value="49.0" unit="%"/> </value> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation"/> </observationRange> </referenceRange>
Im Falle eines einseitig unbeschränkten Intervalls wie z.B. bei „>40“ kann entweder nur der low, bzw. high Wert angegeben werden, wobei auf der Seite, der die Intervallgrenze fehlt, einen NullFlavor angegeben werden MUSS.
Ein „kleiner als“ Referenzbereich wie z.B. „<17“ SOLL als Intervall von 0 bis 17 beschrieben werden.
Im text-Bereich MUSS „>“ durch „& gt;“ und „<“ durch „& lt;“ ersetzt werden.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-3-19"> <td>HDL-Cholesterin</td> <td>0.30</td> <td>mg/dl</td> <td ID="OBSREF-3-19>>60</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-3-19"/> </text> <value xsi:type="IVL_PQ"> <low value="6 0.0" unit=" mg/dL" inclusive="false"/> <high nullFlavor="PINF"/> </value> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation"/> </observationRange> </referenceRange>
Da oftmals die Kriterien für die Bewertung von Laborergebnissen nicht vollständig vorliegen, muss für einen Laborbefund die Angabe mehrerer möglicher Referenzbereiche möglich sein, welche sich durch unterschiedliche Vorbedingungen (preconditions) unterscheiden. Leider ist die Angabe solcher unter dem referenceRange laut CDA Rel.2 Definition nicht möglich. Deshalb MUSS an dieser Stelle eine Angabe in Textform erfolgen. Nachfolgendes Beispiel zeigt die Verwendung des 'referenceRange-Blocks mit mehreren Referenzbereichen mit Preconditions.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-4-7"> <td>Östron</td> <td>165</td> <td>pg/ml</td> <td ID="OBSREF-4-7">Zyklus<br/> Follikelphase: 37-138<br/> Ovulationspeak: 60-230<br/> Lutealphase: 50-114</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-4-7"/> </text> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83"/> </observationRange> </referenceRange>
1.4.7.7.1 Spezifikation
1.4.7.7.1.1 Referenzbereich (observation/referenceRange)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||||
|---|---|---|---|---|---|---|---|---|
| referenceRange | POCD_MT000040.ReferenceRange | 0..1 | O | |||||
| @typeCode | cs | 1..1 | M | Fester Wert: REFV | ||||
| observationRange | POCD_MT000040.ReferenceRange | 1..1 | M | |||||
| @classCode | cs | 1..1 | M | Fester Wert: OBS | ||||
| @moodCode | cs | 1..1 | M | Fester Wert: EVN.CRT | ||||
| text | ED | 1..1 | M | Referenz auf den Referenzbereich im Narrativen Text | ||||
| reference | 1..1 | M | ||||||
| @value | 1..1 | M | Referenz auf Referenzbereich im narrativen Block (vgl. 6.2.9.2) | |||||
| value | PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ | 0..1 | O | Wert des Kriteriums | ||||
| interpretationCode | CE CNE | 1..1 | M | Fester Wert: N Analog zu Kapitel 6.4.7.3.8 mit der Einschränkung code=“N“ | ||||
1.4.7.7.1.2 Werte des Referenzbereichs (referenceRange/value)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||
|---|---|---|---|---|---|---|
| value | IVL_PQ | 0..1 | O | |||
| @xsi:type | cs | 1..1 | M | Fester Wert: IVL_PQ (für physical quantity) | ||
| low | PQ | 1..1 | R | Unterer Grenzwert Zugelassene nullFlavor: NINF (negativ unendlich), NA (nicht anwendbar) | ||
| @value | cs | 1..1 | M | Wert des unteren Grenzwerts | ||
| @unit | cs | 1..1 | M | Physikalische Einheit des unteren Grenzwerts (MUSS ident der Einheit des oberen Grenzwertes sein) | ||
| @inclusive | BL | 0..1 | O | Offene oder abgeschlossene Intervallgrenze
| ||
| high | PQ | 1..1 | R | Oberer Grenzwert Zugelassene nullFlavor: PINF (positiv unendlich), NA (nicht anwendbar) | ||
| @value | cs | 1..1 | M | Wert des oberen Grenzwerts | ||
| @unit | cs | 1..1 | M | Physikalische Einheit des oberen Grenzwerts (MUSS ident der Einheit des unteren Grenzwertes sein) | ||
| @inclusive | BL | 0..1 | O | Offene oder abgeschlossene Intervallgrenze | ||
1.4.7.8 Externes Labor
Die Codierung erfolgt gemäß observation/performer auf Ebene „Laboratory Observation“ (Siehe IHE-Labor Template 1.3.6.1.4.1.19376.1.3.1.6).
Gemäß der Abstimmung der medizinischen Inhalte ist es nicht notwendig, das konkrete externe Labor zu kennzeichnen. Demgemäß kann die ID des Labors mittels nullFlavor angegeben werden. Der code gibt an, dass es sich um ein externes bzw. „Fremdlabor“ handelt. Der code wurde mit „E“ fixiert.
1.4.7.8.1 Spezifikation
| Id | 1.2.40.0.34.11.4.3.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryPerformer2 | Bezeichnung | Laboratory Performer 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Element zur Kennzeichnung einer Analyse, die in einem externen Labor durchgeführt wurde. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.3 Laboratory Performer 2 (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.8 Kultureller Erregernachweis
Für die Codierung des Erregernachweises findet der „Laboratory Isolate Organzier“ (organizer) Verwendung. Dieses organizer-Element, welches über ein entryRelationship in den Specimen-Act (vgl. Kapitel Der Spezimen-Act) gebunden ist, codiert in dem code-Element die Methodik, welche für den Erregernachweis Verwendung findet. Die folgende Tabelle enthält Beispiele für Codes für die Methodik wie sie zum Beispiel in LOINC enthalten sind.
| @code | @displayName | code/originalText |
|---|---|---|
| 6463-4 | Bacteria XXX Cult | Kultur |
| 634-6 | Bacteria XXX Aerobe Cult | Aerobe Kultur |
| 635-3 | Bacteria XXX Anaerobe Cult | Anaerobe Kultur |
| 580-1 | Fungus XXX Cult | Pilzkultur |
Tabelle 12: Beispiele für Codes für Erregernachweis-Methodik entnommen aus LOINC
Für die Codierung der Methode können auch andere, hier nicht näher spezifizierte, LOINC Codes verwendet werden.LOINC-codierte Methoden für den kulturellen Erregernachweis sind mit der Methode „culture“ gekennzeichnet. Suche auf http://search.loinc.org mit Eingabe des entsprechenden Suchbegriffes method:culture.
1.4.8.1 Spezifikation
| Id | 1.2.40.0.34.11.30025 ref elgabbr- | Gültigkeit ab | 2017‑02‑23 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | KulturellerKeimnachweis | Bezeichnung | Kultureller Keimnachweis (Laboratory Isolate Organzier) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30025 Kultureller Keimnachweis (Laboratory Isolate Organzier) (2017‑02‑23) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.9 Antibiogramm (Laboratory Isolate Organizer)
Um das Antibiogramm in Level 3 darstellen zu können, wird das Antibiogramm als „Cluster“-Organizer zusammengefasst. Darin findet sich immer ein Isolat als Probenmaterial (specimen) an dem die Empfindlichkeitstests durchgeführt werden.
<organizer classCode="CLUSTER" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.5"/>
Sind mehrere Erreger im Befund vorhanden, wird für jeden ein „Isolat-Cluster“ angelegt. Für jeden Erreger ist eine eindeutige Nummer (ID) anzugeben. Die OID-Root stammt von der einsendenden Organisation.
Die durchgängige Codierung der Isolate bzw. Erreger ist momentan nicht durchführbar. Die Empfindlichkeitstests werden als „Battery“-Cluster angeführt.
<organizer classCode="BATTERY" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.4"/>
Innerhalb des Organizers werden die einzelnen Antibiotika-Resistenztests zum Isolat wie „normale“ Laboranalysen gehandhabt.
Für die Codierung des Antibiogramms im Organizer ist der LOINC 29576-6 „Bacterial susceptibility panel“ vorgeschrieben.
Die einzelnen Antibiotika-Empfindlichkeitstests sind als LOINC anzugeben. Z.B.: 18993-6 steht für einen Tetracyclin-Empfindlichkeitstest.
Die Interpretation erfolgt über die entsprechenden Codes aus „ELGA_ObservationInterpretation“. Tabelle 13 zeigt einen Ausschnitt.
| Codierung | Resistenz |
|---|---|
| R | Resistent |
| I | Intermediär (intermediate) |
| S | Sensibel (susceptible) |
Tabelle 13: Codierung der Resistenzen
1.4.9.1 Spezifikation
| Id | 1.2.40.0.34.11.30026 ref elgabbr- | Gültigkeit ab | 2014‑04‑15 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Antibiogram | Bezeichnung | Antibiogram (Laboratory Isolate Organzier) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30026 Antibiogram (Laboratory Isolate Organzier) (2014‑04‑15) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.10 Minimale Hemmkonzentration
Die Angabe der erforderlichen Daten für die minimale Hemmkonzentration erfolgt in Level 2 und Level 3 in unterschiedlicher Struktur. In Level 2 (vgl. Kapitel Minimale Hemmkonzentration) werden die Werte in eine eigene Tabelle geschrieben. Die Codierung für Level 3 erfolgt jedoch gemeinsam mit der Codierung eines Antibiogramms (vgl. Kapitel Kultureller Erregernachweis). Der Absolutwert wird innerhalb von organizer/component/observation/value als „Physical Quantity“ codiert. Das interpretationCode-Element hingegen codiert die, für das Antibiogramm notwendige, Information über die Suszeptibilität (R, I, oder S).
1.4.11 Testergebnisse/Molekularer Erregernachweis
Die Level 3 Codierung von „Testergebnissen/Molekularer Erregernachweis“ erfolgt analog der Codierung von Laborergebnissen (vgl. Laborergebnisse). Eine Gruppierung kann mit Hilfe von „Befundgruppen“ (vgl. Befundgruppen) erfolgen.
1.4.12 Significant Pathogens (Notifiable Conditions)
Wichtige Erreger können in Level 3 codiert werden. Diese Erreger sind in der Codeliste „ELGA_SignificantPathogens“ (1.2.40.0.34.5.45) aufgelistet. Diese Liste enthält etwa die meldepflichtigen Krankheiten. Die Level 3-Codierung erfolgt über einen „Notification Organizer“ (organizer-Element) mit „Notifiable Condition“ als observation-Element.
1.4.12.1 Spezifikation Notification Organizer
| Id | 1.3.6.1.4.1.19376.1.3.1.1 ref elgabbr- | Gültigkeit ab | 2013‑09‑09 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | NotificationOrganizer | Bezeichnung | Notification Organizer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.1 Notification Organizer (2013‑09‑09) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.12.2 Spezifikation Notifiable Condition
| Id | 1.3.6.1.4.1.19376.1.3.1.1.1 ref elgabbr- | Gültigkeit ab | 2013‑09‑09 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | NotifiableCondition | Bezeichnung | Notification Condition | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.1.1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.1.1 Notification Condition (2013‑09‑09) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.13 Befundtext: Anmerkungen und Kommentare
Die Codierung von Anmerkungen und Kommentaren erfolgt in jedem Fall gem. IHE als sogenannter „Annotation-Act“. Die Codierung erfolgt als act-Element, welches mittels entsprechender Beziehung (entryRelationship oder component) an das übergeordnete Element gebunden wird. Die Elemente templateId und code sind fix vorbelegt. Das einzige veränderbare Element ist der text-Block. Dieser SOLL eine Referenz auf ein Element innerhalb der Level 2 Codierung enthalten (vgl. Kapitel Referenz von Level 3 auf Level 2: Beziehung von Level 3 über den Referenz Verweis reference-Element mit Attributevalue=“refID“ auf die ID eines Elements in Level 2 wie z.B. content ID=“refID“).
1.4.13.1 Spezifikation
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.13.2 Bereichsübergreifende Befundbewertung
Im Falle einer Gliederung eines Laborbefundes in zwei Hierarchieebenen (Bereiche und Befundgruppen) besteht die Notwendigkeit einer bereichsübergreifenden Befundbewertung/eines Befundkommentars. Die Abbildung derartiger bereichsübergreifender Befundbewertungen erfolgt über eine eigene Annotation Section (siehe [4]).
1.4.13.2.1 Spezifikation
| Id | 1.2.40.0.34.11.4.2.2 ref elgabbr- | Gültigkeit ab | 2013‑02‑10 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryReportCommentSection | Bezeichnung | Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.2 Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) (2013‑02‑10) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.13.2.2 Spezifikation Befundtext
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
1.4.14 Multimedia Content
Im Laborbefund sind folgende Mulitmedia Formate zulässig: eingebettete PDF/A-Dateien („application/pdf“) sowie Grafiken im Format „image/jpeg“, „image/gif“ oder „image/png. Alle Grafiken und Bilder sind inline Base64 zu codieren und zu übertragen. Referenzen auf externe Grafiken sind NICHT ERLAUBT.
<value mediaType="image/jpeg" representation="B64">
Die Codierung von Multimedia Inhalten erfolgt gem. „Allgemeinem Implementierungsleitfaden“, Kapitel Einbetten von Dokumenten/Multimedia-Dateien ([4]).
Alternativ zur allgemeingültigen Variante kann die Level 3 Codierung auch als component-Element auf Ebene direkt unter dem Bereich (Spezimen-Act) oder der Befundgruppe (siehe Laboratory Battery Organizer) erfolgen.
1.4.14.1 Spezifikation
Keine Versionen mit Status draft, active, review oder pending.


