Autoren
| [unmarkierte Version] | [unmarkierte Version] |
| Zeile 1: | Zeile 1: | ||
| − | |||
{{#seo: | {{#seo: | ||
|title=Laborbefund | |title=Laborbefund | ||
| Zeile 6: | Zeile 5: | ||
|description=Der in diesem Leitfaden beschriebene Laborbefund dient also zum Austausch von fertiggestellten, und fachärztlich vidierten Befunden innerhalb und zwischen Einrichtungen des Gesundheitswesens. | |description=Der in diesem Leitfaden beschriebene Laborbefund dient also zum Austausch von fertiggestellten, und fachärztlich vidierten Befunden innerhalb und zwischen Einrichtungen des Gesundheitswesens. | ||
}} | }} | ||
| − | + | ||
{{Underconstruction}} | {{Underconstruction}} | ||
Version vom 3. Oktober 2017, 13:39 Uhr
|
|
Diese Seite oder Abschnitt ist derzeit ein Entwurf und kann sich noch ändern. This article was last edited by Lahnsteiner (talk| contribs) 7 years ago. This article or section is in the middle of an expansion or major restructuring. This article was last edited by Lahnsteiner (talk| contribs) 7 years ago. |
|
|
Dieses Dokument gibt wieder:
Implementierungsleitfaden Laborbefund (2.06.2), OID: n.n., Datum: 20. März 2017, Status: Entwurf. Die Teilmaterialien gehören der Kategorie elga-cdalab-2.06.2 an. |
Implementierungsleitfäden
Laborbefund
Gesundheitswesen [1.2.40.0.34.7.1.6.2]
Inhaltsverzeichnis
- 1 Informationen über dieses Dokument
- 2 Harmonisierung
- 3 Einleitung
- 4 Anwendungsfälle
- 4.1 Anwendungsfall LAB01: „Laboruntersuchung eines niedergelassenen Labors“
- 4.2 Anwendungsfall LAB02: „Laboruntersuchung im Rahmen eines stationären Aufenthalts in einem Spital“
- 4.3 Anwendungsfall LAB03: „Teilweise externe Vergabe von Laboruntersuchungen“
- 4.4 Anwendungsfall LAB04: „Update von Laborbefunden“
- 5 Administrative Daten (CDA Header)
- 5.1 Überblick
- 5.2 Dokumentenstruktur
- 5.2.1 Elemente ohne spezielle Vorgaben
- 5.2.2 XML Metainformationen
- 5.2.3 Wurzelelement
- 5.2.4 Hoheitsbereich des Dokuments („realmCode“)
- 5.2.5 Dokumentformat („typeId“)
- 5.2.6 Dokumenten-Id („id”)
- 5.2.7 Erstellungsdatum des Dokuments („effectiveTime“)
- 5.2.8 Vertraulichkeitscode („confidentialityCode“)
- 5.2.9 Sprachcode des Dokuments („languageCode“)
- 5.2.10 Elemente mit spezielle Vorgaben
- 5.3 Teilnehmende Parteien
- 5.3.1 IHE LAB TF-3 Konformität
- 5.3.2 Elemente ohne spezielle Vorgaben
- 5.3.3 Patient („recordTarget/patientRole“)
- 5.3.4 Personen der Dateneingabe („dataEnterer“)
- 5.3.5 Verwahrer des Dokuments („custodian“)
- 5.3.6 Beabsichtigte Empfänger des Dokuments („informationRecipient“)
- 5.3.7 Verfasser des Dokuments („ClinicalDocument/author“)
- 5.3.8 Medizinischer Validator („ClinicalDocument/legalAuthenticator“)
- 5.3.9 Validator („ClinicalDocument/authenticator“)
- 5.3.10 Weitere Beteiligte („participant“)
- 5.4 Referenz zum Auftrag
- 5.5 Dokumentation der Gesundheitsdienstleistung
- 5.6 Dokumentation der Gesundheitsdienstleistung
- 5.7 Informationen zum Patientenkontakt
- 6 Medizinische Inhalte im Body
- 6.1 Fachlicher Inhalt in den ELGA Interoperabilitätsstufen (EIS)
- 6.2 Aufbau des Body
- 6.2.1 Strukturierter Body („structuredBody“)
- 6.2.2 Sektion Brieftext
- 6.2.3 Sektion Überweisungsgrund
- 6.2.4 Bereiche (Specialities)
- 6.2.5 Gruppen (Befundgruppen)
- 6.2.6 Zusätzliche medizinische Informationen
- 6.2.7 Allgemeine Strukturrichtlinien für Body-Elemente
- 6.2.8 Narrativer Block
- 6.2.9 CDA Entry Level („Level 3“)
- 6.2.10 Harmonisierung des Befundaufbaus – Value Set „ELGA_Laborparameter“
- 6.3 Spezifikation der Befunddarstellung Level 2
- 6.3.1 Überblick
- 6.3.2 Formatierung von Datums- und Zeitangaben
- 6.3.3 Level 2 Befundstruktur
- 6.3.4 Probeninformation
- 6.3.5 Vorgaben zur Darstellung einzelner Elemente
- 6.3.6 Stylecodes
- 6.3.7 Bemerkungen/Kommentare
- 6.3.8 Eigenschaften des Materials/Mikroskopie
- 6.3.9 Kultureller Erregernachweis
- 6.3.10 Antibiogramm
- 6.3.11 Minimale Hemmkonzentration
- 6.3.12 Testergebnisse/Molekularer Erregernachweis
- 6.3.13 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012
- 6.3.14 Angabe des Akkreditierungs-Logos
- 6.3.15 Angabe des Untersuchungs- bzw Messverfahrens
- 6.3.16 Vorgaben für den Befunddruck
- 6.4 Spezifikation des Body Level 3
- 6.4.1 Überblick
- 6.4.2 Überweisungsgrund
- 6.4.3 Laboratory Report Data Processing Entry
- 6.4.4 Der Spezimen-Act
- 6.4.5 Probeninformationen (Specimen-Section)
- 6.4.6 Befundgruppen (Laboratory Battery Organizer)
- 6.4.7 Laborergebnisse (Laboratory Observation)
- 6.4.8 Kultureller Erregernachweis
- 6.4.9 Antibiogramm (Laboratory Isolate Organizer)
- 6.4.10 Minimale Hemmkonzentration
- 6.4.11 Testergebnisse/Molekularer Erregernachweis
- 6.4.12 Significant Pathogens (Notifiable Conditions)
- 6.4.13 Befundtext: Anmerkungen und Kommentare
- 6.4.14 Multimedia Content
- 7 Technische Konformitätsprüfung
- 8 Anhang
1 Informationen über dieses Dokument
1.1 Allgemeines
Ziel dieses Implementierungsleitfadens ist die Beschreibung von Struktur, Format und Standards von medizinischen Dokumenten der Elektronischen Gesundheitsakte "ELGA" gemäß Gesundheitstelematikgesetz 2012 (GTelG 2012), aber auch für medizinische Dokumente im österreichischen Gesundheitswesen.
Die Anwendung dieses Implementierungsleitfadens hat im Einklang mit der Rechtsordnung der Republik Österreich und insbesondere mit den relevanten Materiengesetzen (z.B. Ärztegesetz 1998, Apothekenbetriebsordnung 2005, Krankenanstalten- und Kuranstaltengesetz, Gesundheits- und Krankenpflegegesetz, Rezeptpflichtgesetz, Datenschutzgesetz 2000, Gesundheitstelematikgesetz 2012) zu erfolgen. Technische Möglichkeiten können gesetzliche Bestimmungen selbstverständlich nicht verändern, vielmehr sind die technischen Möglichkeiten im Einklang mit den Gesetzen zu nutzen.
1.2 Sprachliche Gleichbehandlung
Soweit im Text Bezeichnungen nur im generischen Maskulinum angeführt sind, beziehen sie sich auf Männer und Frauen in gleicher Weise. Unter dem Begriff "Patient" werden sowohl Bürger, Kunden und Klienten zusammengefasst, welche an einem Behandlungs- oder Pflegeprozess teilnehmen als auch gesunde Bürger, die derzeit nicht an einem solchen teilnehmen. Es wird ebenso darauf hingewiesen, dass umgekehrt der Begriff Bürger auch Patienten, Kunden und Klienten mit einbezieht.
1.3 Verbindlichkeit
Mit der ELGA-Verordnung 2015 (in der Fassung der ELGA-VO-Nov-2015) macht die Bundesministerin für Gesundheit und Frauen die Festlegungen für Inhalt, Struktur, Format und Codierung verbindlich, die in den Implementierungsleitfäden Entlassungsbrief Ärztlich, Entlassungsbrief Pflege, Pflegesituationsbericht, Laborbefunde, Befund bildgebender Diagnostik, e-Medikation sowie XDS Metadaten (jeweils in der Version 2.06) getroffen wurden. Die anzuwendende ELGA-Interoperabilitätsstufen ergeben sich aus §21 Abs.6 ELGA-VO. Die Leitfäden in ihrer jeweils aktuell gültigen Fassung sowie die aktualisierten Terminologien sind von der Gesundheitsministerin auf www.gesundheit.gv.at zu veröffentlichen. Der Zeitplan zur Bereitstellung der Dokumente für ELGA wird durch das Gesundheitstelematikgesetz 2012 (GTelG 2012) und darauf basierenden Durchführungsverordnungen durch die Bundesministerin für Gesundheit und Frauen vorgegeben.
Die Verbindlichkeit und die Umsetzungsfrist dieses Leitfadens ist im Gesundheitstelematikgesetz 2012, BGBl.I Nr.111/2012 sowie in den darauf fußenden ELGA-Verordnungen geregelt.
Neue Hauptversionen der Implementierungsleitfäden KÖNNEN ab dem Tag ihrer Veröffentlichung durch die Bundesministerin für Gesundheit und Frauen (www.gesundheit.gv.at) verwendet werden, spätestens 18 Monate nach ihrer Veröffentlichung MÜSSEN sie verwendet werden. Andere Aktualisierungen (Nebenversionen) dürfen auch ohne Änderung dieser Verordnung unter www.gesundheit.gv.at veröffentlicht werden.
Die Einhaltung der gesetzlichen Bestimmungen liegt im Verantwortungsbereich der Ersteller der CDA-Dokumente.
1.4 Zielgruppe
Anwender dieses Dokuments sind Softwareentwickler und Berater, die allgemein mit Implementierungen und Integrationen im Umfeld der ELGA, insbesondere der ELGA-Gesundheitsdaten, betraut sind. Eine weitere Zielgruppe sind alle an der Erstellung von CDA-Dokumenten beteiligten Personen, einschließlich der Endbenutzer der medizinischen Softwaresysteme und der Angehörigen von Gesundheitsberufen.
1.5 Hinweis auf verwendete Grundlagen
Der vorliegende Leitfaden wurde unter Verwendung der nachstehend beschriebenen Dokumente erstellt. Das Urheberrecht an allen genannten Dokumenten wird im vollen Umfang respektiert.
Dieser Standard beruht auf der Spezifikation "HL7 Clinical Document Architecture, Release 2.0", für die das Copyright © von Health Level Seven International gilt. HL7 Standards können über die HL7 Anwendergruppe Österreich (HL7 Austria), die offizielle Vertretung von Health Level Seven International in Österreich bezogen werden (www.hl7.at). Alle auf nationale Verhältnisse angepassten und veröffentlichten HL7-Spezifikationen können ohne Lizenz- und Nutzungsgebühren in jeder Art von Anwendungssoftware verwendet werden.
Dieser Leitfaden beruht auf Inhalten des LOINC® (Logical Observation Identifiers Names and Codes, siehe http://loinc.org). Die LOINC-Codes, Tabellen, Panels und Formulare unterliegen dem Copyright © 1995-2014, Regenstrief Institute, Inc. und dem LOINC Committee, sie sind unentgeltlich erhältlich. Lizenzinformationen sind unter http://loinc.org/terms-of-use abrufbar. Weiters werden Inhalte des UCUM® verwendet, UCUM-Codes, Tabellen und UCUM Spezifikationen beruhen auf dem Copyright © 1998-2013 des Regenstrief Institute, Inc. und der Unified Codes for Units of Measures (UCUM) Organization. Lizenzinformationen sind unter http://unitsofmeasure.org/trac/wiki/TermsOfUse abrufbar.
1.6 Danksagung
Die ELGA GmbH weist auf das Dokument „Arztbrief auf Basis der HL7 Clinical Document Architecture Release 2.0 für das deutsche Gesundheitswesen“ hin, welches vom Verband der Hersteller von IT-Lösungen für das Gesundheitswesen (VHitG) herausgegeben wurde. Einige Ausführungen in dem genannten Dokument wurden in das vorliegende Dokument übernommen. Das Urheberrecht an dem Dokument „Arztbrief auf Basis der HL7 Clinical Document Architecture Release 2.0 für das deutsche Gesundheitswesen“, wird im vollen Umfang respektiert.
1.7 Revisionsliste
Diese Version ist eine Nebenversion zur Hauptversion 2.06 und ersetzt diese. Die durchgeführten Änderungen ersehen Sie der Revisionsliste.
1.8 Weitere unterstützende Materialien
Gemeinsam mit diesem Leitfaden werden auf der Website der ELGA GmbH [1] weitere Dateien und Dokumente zur Unterstützung bereitgestellt: Beispieldokumente, zu verwendende Codes, Vorgaben zur Registrierung von CDA-Dokumenten, das Referenz-Stylesheet zur Darstellung von CDA-Dokumenten, Algorithmen zur Prüfung der Konformität von CDA-Dokumenten etc.
Fragen, Kommentare oder Anregungen für die Weiterentwicklung können an cda@elga.gv.at[2] gesendet werden. Weitere Informationen finden Sie unter http://www.elga.gv.at/CDA.
1.9 Bedienungshinweise für die PDF-Version
Nutzen Sie die bereitgestellten Links im Dokument (z.B. im Inhaltsverzeichnis), um direkt in der PDF-Version dieses Dokuments zu navigieren. Folgende Tastenkombinationen können Ihnen die Nutzung des Leitfadens erleichtern:
- Rücksprung: Alt + Pfeil links und Retour: Alt + Pfeil rechts
- Seitenweise blättern: "Bild" Tasten
- Scrollen: Pfeil nach oben bzw. unten
- Zoomen: Strg + Mouserad drehen
- Suchen im Dokument: Strg + F
1.10 Impressum
Medieneigentümer, Herausgeber, Hersteller, Verleger:
ELGA GmbH, Treustraße 35-43, Wien, Österreich. Telefon: 01. 2127050. Internet: http://www.elga.gv.at.
Email: cda@elga.gv.at.
Geschäftsführer: DI Dr. Günter Rauchegger, DI (FH) Dr. Franz Leisch
Redaktion, Projektleitung, Koordination:
Mag. Dr. Stefan Sabutsch, stefan.sabutsch@elga.gv.at
Abbildungen: © ELGA GmbH
Nutzung: Das Dokument enthält geistiges Eigentum der Health Level Seven® Int. und HL7® Austria, Franckstrasse 41/5/14, 8010 Graz; www.hl7.at.
Die Nutzung ist zum Zweck der Erstellung medizinischer Dokumente ohne Lizenz- und Nutzungsgebühren ausdrücklich erlaubt. Andere Arten der Nutzung und auch auszugsweise Wiedergabe bedürfen der Genehmigung des Medieneigentümers.
Download unter www.gesundheit.gv.at und www.elga.gv.at/cda
2 Harmonisierung
Erarbeitung des Implementierungsleitfadens
Dieser Implementierungsleitfaden entstand durch die Harmonisierungsarbeit der „Arbeitsgruppe Laborbefund“ im Zeitraum zwischen 2008 und 2012, bestehend aus den unten genannten Personen.
| Autoren | ||
|---|---|---|
| Kürzel | Organisation | Person1 |
| Herausgeber, Editor, CDA Koordinator | ||
| SSA | ELGA GmbH | Stefan Sabutsch |
| Autoren, Fachkoordinatoren und Moderatoren | ||
| SS | Fachhochschule Technikum Wien | Stefan Sauermann |
| AM | Fachhochschule Technikum Wien, HL7 Austria | Alexander Mense |
| SSA | ELGA GmbH, HL7 Austria | Stefan Sabutsch |
| MF | Fachhochschule Technikum Wien | Matthias Frohner |
| Autoren | ||
|---|---|---|
| Organisation | Person1 | |
| Begleitung, Fachliche Beratung | ||
| Medicon Medical Consulting | Georg Paucek | |
| Ärztliche Vertreter | ||
| Kurienversammlung der niedergelassenen Ärzte der OÖ Ärztekammer | Franz Burghuber | |
| Österreichische Ärztekammer, KH St. Pölten, Inst. für Laboratoriumsmedizin | Alexander Haushofer | |
| Österreichische Ärztekammer, Wiener KAV, Sozialmedizinisches Zentrum Ost - Donauspital, Institut für Labormedizin | Jörg Hofmann | |
| Österreichische Ärztekammer, ON-K 238 | Gerhard Holler | |
| Rotes Kreuz, Blutspendezentrale Wien | Christof Jungbauer | |
| Sozialmedizinisches Zentrum Ost | Walter Krugluger, Thomas Leitha | |
| Elisabethinen Linz | Helmut Mittermayer | |
| Initiative-ELGA | Susanna Michalek | |
| Medizinisches Labor Perné | Johann Perné | |
| Österreichische Ärztekammer, Bundesfachgruppe Labor | Georg Mustafa | |
| Österreichische Ärztekammer | Thomas Szekeres | |
| Krankenhausträger | ||
| Vinzenz Gruppe Krankenhausbeteiligungs- und Management GmbH | Bernhard Böhm | |
| KAV Wien, Generaldirektion | Christian Cebulla | |
| Wilhelminenspital der Stadt Wien, Zentrallabor, KAV Wien | Georg Endler | |
| KFJ – Sozialmed. Zentrum Süd, Institut für Laboratoriumsdiagnostik | Manuela Födinger | |
| Univ.Klin. Innsbruck, Zentralinst. Labordiagnostik | Andrea Griesmacher | |
| ÖQUASTA; KH Hietzing + NZ Rosenhügel, Institut f. Labordiagnostik | Walter-Michael Halbmayer | |
| LKH Vöcklabruck, Institut f. Med.Chem. Labordiagnostik u. Blutdepot | Susanne Hauptlorenz | |
| Wiener Krankenanstaltenverbund, KAV-IT | Konrad Hölzl | |
| KAV Wien,, Wilhelminenspital, Zentrallabor, ÖGLMKC | Wolfgang Hübl | |
| GESPAG Gesundheitsinformatik-Bereichsleiter | Christian Kampenhuber | |
| KABEG (LKH Klagenfurt, Wolfsberg, Lass und Hermagor) | Gerald Regenfelder | |
| Tilak, Informationstechnologie/IT-Abteilung | Dietmar Reiter | |
| LK Weinviertel Mistelbach, Laborinstitut, NÖ LK-Holding | Harald Rubey | |
| Med. Uni. Wien, Klinik f. Blutgruppenserologie u. Transfusionsmedizin | Dieter Schwartz | |
| Kages Zentrallabor | Beate Tiran | |
| Softwarehersteller / Befundprovider | ||
| Max management Consulting GmbH | Helmuth Gamper | |
| act Management Consulting GmbH | Bernhard Göbl | |
| Systema | Christian Kraml, Herbert Matzenberger | |
| vision4health Deutschland GmbH & Co. KG | Michael Krausenbaum | |
| Labatech Handelsgesellschaft m.b.H. | Hans Richter | |
| Assista Laborelectronics GmbH | Wolfgang Sischka | |
| HCS, Health Communication Service | Christoph Unfried | |
| Universitäten / Fachhochschulen | ||
| Fachhochschule Technikum Wien | Ferenc Gerbovics, Philipp Urbauer | |
| Medizinische Universität Graz, Institut für Hygiene, Mikrobiologie und Umweltmedizin | Harald Kessler | |
| Patronanz, Akkordierung, Ergänzungen, Zustimmung | ||
|---|---|---|
| Organisation | Person1 | |
| Bundesministerium für Gesundheit | Clemens Auer | |
| ELGA GmbH | Hubert Eisl, Susanne Herbek, Martin Hurch, Oliver Kuttin | |
| Medizinisches Zentrallaboratorium GmbH | Peter Fraunberger | |
| Steiermärkische Krankenanstalten-ges. m.b.H. | Josef Galler | |
| Solve Consulting | Gerhard Gretzl | |
| Landeskrankenhaus Feldkirch, Institut für Pathologie | Ulrike Gruber-Mösenbacher | |
| Krankenhaus der Barmherzigen Schwestern Ried, Inst. f. Pathologie | Milo Halabi | |
| A.ö. Krankenhaus der Elisabethinen Linz, Institut für Medizinische und Chemische Labordiagnostik | Elisabeth Haschke-Becher | |
| Oö. Gesundheitsfonds / eHealth Management | Wolfgang Hiesl | |
| Med. Uni. Wien, Klinisches Institut für Medizinische und Chemische Labordiagnostik | Stylianos Kapiotis | |
| B&S Zentrallabor | Peter Konrath | |
| Tilak, Abteilungsleiter Informationstechnologie/IT-Abteilung | Georg Lechleitner | |
| Steiermärkische Krankenanstalten-ges. m.b.H. | Hubert Leitner | |
| Österreichische Agentur für Gesundheit und Ernährungssicherheit GmbH - AGES | Helmut Lindorfer | |
| Österreichische Ärztekammer, Sekretariat | Sabine Manhardt | |
| Labor Dr. Hans Georg Mustafa, Fachgesellschaft Labormedizin | Hans Georg Mustafa | |
| GRZ IT Center Linz GmbH | Achim Mühlberger | |
| Gibodat EDV- und Organisationsberatungs GmbH | Michael Nebel | |
| AUVA - Unfallkrankenhaus Meidling, Labor | Susan Netzl | |
| A.ö. Krankenhaus der Elisabethinen Linz, Institut für Medizinische und Chemische Labordiagnostik, EDV | Claudia Perndl | |
| BKH Hall in Tirol, EDV | Sven Plattner | |
| NÖ Landeskliniken-Holding | Thomas Pöckl | |
| Sozialmedizinisches Zentrum Ost – Donauspital, Pathologisch-Bakteriologisches Institut | Angelika Reiner-Concin | |
| NÖ Landesklinikenholding | Alexander Schanner | |
| Österreichische Ärztekammer, Labor Schobesberger | Gerhard Schobesberger | |
| Medizinische Universität Wien / AKH Wien, klinische Abteilung für Medizinisch-chemische Labordiagnostik | Christian Schweiger | |
| Bartelt GmbH | Peter Schöttel | |
| AKH Linz, Institut für Laboratoriumsmedizin | Herbert Stekel | |
| HCS, Health Communication Service | Romana Thiel | |
| Labene | Michael Danninger | |
| Telekom Austria | Peter Uher | |
| Assista | Michael Weidenauer | |
| Medizinische Universität Wien | Thomas Wrba | |
| Andere ELGA Arbeitsgruppen | ||
|---|---|---|
| Entlassungsbrief Arzt und Pflege | CodeWerk Software Services and Development GmbH | Jürgen Brandstätter |
| Befundbericht Radiologie | AIMC Lindner TAC |
Martin Weigl Andreas Lindner |
AG Laborbefund 2017
Die Änderungen für Version 2.06.2 wurde von der AG Laborbefund am 12.1.2017 abgenommen. Teilnehmer der AG Laborbefund waren:
| Maria Abzieher (Wiener Krankenanstaltenverbund) | Herbert Matzenberger (CompuGroup Medical CEE GmbH) |
| Robert Alscher (Humanomed IT Solutions Gmbh) | Daniel Außerdorfer (Univ.Klin. Innsbruck, Zentralinstitut für Medizinische und |
| Chemische Labordiagnostik (ZIMCL)) | René Berger (Synlab) |
| Barbara Dall (CGM) | Zeljko Drljaca (Institut für medizinische und chemische Labordiagnostik Gesellschaft m.b.H) |
| Daniela Eisner (Salzburger Landeskliniken ) | Christian Fersterer (Salzburger Landeskliniken) |
| Matthias Frohner (FH Technikum Wien) | Josef Galler (Steiermärkische Krankenanstalten-ges. m.b.H.) |
| Andrea Griesmacher (Univ.Klin. Innsbruck, Zentralinstitut für Medizinische und Chemische Labordiagnostik (ZIMCL)) | Gernot Gruber (Institut für medizinische und chemische Labordiagnostik Gesellschaft m.b.H) |
| Sylvia Handler (biomed austria - Österreichischer Berufsverband der Biomedizinischen AnalytikerInnen) | Susanne Hauptlorenz (Salzkammergut-Klinikum Vöcklabruck, Institut für Med.Chem. Labordiagnostik und Blutdepot) |
| Alexander Haushofer (ÖGLMKC; Klinikum Wels-Grieskirchen) | Wolfgang Hießl (Oö. Gesundheitsfonds / eHealth Management) |
| Michael Hubmann (Med. Zentrallaboratorium GmbH) | Günter Igler (Analyse BioLab; KH Elisabethinen Linz) |
| Sonja Jansen-Skoupy (KAV Wien, SMZ Süd) | Michael Krausenbaum (CGM LAB Deutschland GmbH) |
| Herwig Loidl (Carecenter Software GmbH) | Birgit Luxbacher (biomed austria - Österreichischer Berufsverband der Biomedizinischen AnalytikerInnen) |
| Alexander Mense (Fachhochschule Technikum Wien, HL7 Austria) | Hans Georg Mustafa (Labor Dr. Hans Georg Mustafa, BFG Med. u. Chem. Labordiagnostik, ÖGLMKC) |
| Stefan Mustafa (Labor Doz. Mag. DDr. Stefan Mustafa) | Michael Nöhammer (Ärztekammer Österreich) |
| Thomas Pöckl (NÖ Landeskliniken-Holding) | Elisabeth Presterl (Universitätsklinik für Krankenhaushygiene & Infektionskontrolle, Medizinische Universität Wien) |
| Sebastian Reimer (BMGF) | Harald Rubey (LK Weinviertel Mistelbach, Laborinstitut, NÖ LK-Holding) |
| Stefan Sabutsch (ELGA GmbH, HL7 Austria) | Ulrich Sagel (Universitätsklinik für Hygiene und Mikrobiologie) |
| Karin Salzmann (Univ. Klinik für Innere Medizin Innsbruck) | Clemens M. Sampl (BMGF) |
| Stefan Sauermann (FH Technikum Wien, Interoperabilitätsforum Österreich) | Peter Schöttel (Bartelt GmbH) |
| Christian Schweiger (Medizinische Universität Wien / AKH Wien, klinische Abteilung für Medizinisch-chemische Labordiagnostik) | Carina Seerainer (ELGA GmbH) |
| Josef Seier (Klinikum Wels-Grieskirchen) | Wolfgang Sischka (Assista Laborelectronics GmbH) |
| Herbert Stekel (Kepler Universitätsklinikum GmbH) | Michael Svizak (AUVA Hauptstelle - Ärztliche Direktion) |
| Gerhard Weigl (Inst. f. Labormedizin – Otto-Wagner-Spital Wien) |
1 Personen ohne Titel
3 Einleitung
3.1 Ausgangssituation
Die Elektronische Gesundheitsakte (ELGA) umfasst die relevanten multimedialen und gesundheitsbezogenen Daten und Informationen zu einer eindeutig identifizierten Person. Die Daten sind in einem oder mehreren computergestützten Informationssystemen gespeichert. Sie stehen allen berechtigten Personen entsprechend ihren Rollen und den datenschutzrechtlichen Bedingungen in einer bedarfsgerecht aufbereiteten elektronischen Form online zur Verfügung.
Die zentrale Anwendung von ELGA ist die Bereitstellung von patientenbezogenen medizinischen Dokumenten, die in vielen unterschiedlichen Informationssystemen der verschiedenen Gesundheitsdiensteanbieter erstellt werden. Diese Dokumente sollen nicht nur von Benutzern gelesen, sondern auch wieder in die IT-Systeme integriert und dort weiterverwendet werden können („Semantische Interoperabilität“). Beispielsweise können für den Arzt aus ELGA-Dokumenten automatisch Warnungen, Erinnerungen, Zusammenfassungen generiert und weitere Informationen berechnet und kontextbezogen angezeigt werden.
Um dieses Ziel zu ermöglichen, wird für Dokumente in ELGA der internationale Standard „Clinical Document Architecture, Release 2.0“ (CDA) von HL7 eingesetzt.
Der CDA-Standard wird für die Verwendung in ELGA im Detail ausspezifiziert, Vorgaben für einheitliche Dokumentation und Codierung der Information festgelegt und in implementierbaren Leitfäden veröffentlicht.
3.2 Zweck
Das vorliegende Dokument enthält die Definition der Inhalte des „Laborbefundes“ für das Österreichische Gesundheitswesen. Diese Spezifikation ist das Resultat einer Harmonisierungsarbeit mit dem Ziel medizinische Befunde, innerhalb der derzeit im Aufbau befindlichen österreichischen „Elektronischen Gesundheitsakte“ (ELGA), als abgestimmte und einheitlich strukturierte Dokumente darzustellen. Das Dokument wurde von einer Arbeitsgruppe von Vertretern der Österreichischen Ärztekammer, von mehreren Krankenhausträgern und Spitälern, Universitäten und Fachgesellschaften, des österreichischen Normeninstitutes, von der Health Level 7 (HL7) Anwendergruppe Österreich, sowie Personen aus der Wirtschaft erstellt. Sowohl angestellte als auch niedergelassene Labormediziner waren massiv an der Erarbeitung beteiligt.
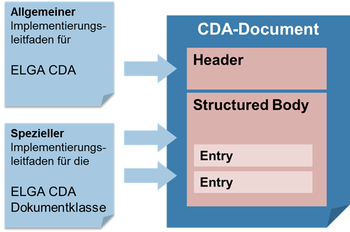
Die Abstimmung erfolgte gemeinsam mit anderen Arbeitsgruppen, die gleichzeitig an den Inhalten für den „Entlassungsbrief“ und den „Befund bildgebende Diagnostik“ arbeiten. Vor allem die Informationen über die betroffenen und handelnden Personen, Zeitangaben, Dokumentart und ähnliches im so genannten „Header“ wurden eng abgestimmt und im Rahmen eines zentralen Dokumentes „Allgemeiner Implementierungsleitfaden für ELGA CDA Dokumente [OID Root 1.2.40.0.34.7.1]“ [4] definiert.
Der Header enthält zum einen administrative Daten (allgemeine Angaben zum Dokument, Daten zum Patienten, usw.) und dient zum anderen zum Teil auch als Quelle für die Metadaten, die bei der Registrierung des Dokuments in ELGA verwendet werden. Der Header wurde über alle Anwendungsbereiche der ELGA einheitlich abgestimmt.
Die medizinisch relevanten Anteile sind im so genannten „Body“ enthalten. Die vorliegende Spezifikation der laborspezifischen Inhalte eines Labordokuments in ELGA wurde von der Expertengruppe beruhend auf einer Liste mit Vorgaben der österreichischen Gesellschaft für Labormedizin und klinische Chemie (ÖGLMKC) erstellt.
Als technische Basis dient das „Laboratory Technical Framework Volume 3 (LAB TF-3) Revision 3.0, 2011“ ([3]) der “Integrating the Healthcare Enterprise” (IHE).
Das Verständnis eines „Laborbefundes“ erstreckt sich in diesem Dokument über das gesamte Spektrum der laboranalytisch ermittelten Befunde. Die vorliegende Version definiert grundlegende Anforderungen für die Erstellung von Laborbefunden als CDA Dokumente. Insbesondere wurden Laborbefunde aus der Klinischen Chemie, Hämatologie, Immunchemie und Mikrobiologie/Bakteriologie in die Überlegungen mit einbezogen. Die gewählten Strukturen ermöglichen prinzipiell eine Übermittlung des gesamten Befundspektrums des Laborbereiches, jedoch sind die einzelnen Detailbereiche in folgenden Arbeiten detailliert zu analysieren, abzustimmen und für weitere Laborbefundarten zu definieren. Es existieren vielmehr auch dezidierte Bereiche - wie z.B. die Transfusionsmedizin – für die die Definitionen dieses Leitfadens aufgrund fehlender Strukturen und nicht definierter Codelisten nicht ausreichend sind. Dieser Leitfaden verwendet „Analysen“ als Sammelbegriff für Laboruntersuchungen, Laborleistungen und Labormessgrößen.
3.3 Vorgaben zum medizinischen Inhalt
3.3.1 Allgemeiner Laborbefund
Die inhaltlichen Definitionen beruhen auf den Mindestvorgaben der österreichischen Gesellschaft für Labormedizin und klinischen Chemie (ÖGLMKC) und wurden weiter verfeinert. Die nachfolgende Tabelle zeigt einen Überblick über die inhaltlich abzubildenden medizinisch relevanten Daten.
| Feld | Beschreibung | Bereich |
|---|---|---|
| Allgemeine Befundinformationen | ||
| Zeitpunkt der Auftragserfassung | Datum und Zeitpunkt, an dem das analysierende Labor die Anforderung vom Zuweiser in der Labor EDV erfasst hat | Header |
| Auftragsdiagnose (Zuweiserdiagnose) | Vom Auftraggeber bestimmte und dem Labor übermittelte Verdachtsdiagnose | Body |
| Fragestellung | Vom Auftraggeber übermittelte Fragestellung | Body |
| Befundtext | Kommentar zum gesamten Befund | Body |
| Spezimeninformation | ||
| Zeitpunkt der Spezimengewinnung | Damit ist jenes Datum und Zeitpunkt gemeint, an dem das Spezimen zur Analyse gewonnen wurde. Die Dokumentation des Zeitpunkts der Spezimengewinnung ist in der Verantwortung der entnehmenden Person, die in vielen Fällen mit dem Befundersteller nicht identisch ist, da meist Spezimen zur Analyse an Labors versendet werden. Daher ist der Zeitpunkt vielfach im Labor nicht feststellbar. | Body |
| Zeitpunkt des Einlangens des Spezimen | Datum und Zeit der Probenannahme im Labor | Body |
| Art des Spezimens (Specimen Type) | Art der Probe (=Materialart) | Body |
| Entnahmeort | Angabe der Körperstelle, von der das Spezimen stammt | Body |
| Entnahmeart (SpecimenCollectionProcedure) | Art der Gewinnung | Body |
| Specimen ID | Eindeutige Nummer des Spezimen | Body |
| Entnehmende Person (Performer) | Person, welche die Entnahme der Probe durchgeführt hat | Body |
| Kommentar zum Spezimen | Präanalytik pro Spezimen zur Spezimenqualität | Body |
| Allgemeine Anmerkungen des Labors zur Spezimenqualität | Textinformationen zur Spezimenqualität | Body |
| Allgemeine Laborergebnisse | ||
| Gruppierung / Befundgruppen (Organizer) | Analysengruppierung | Body |
| ID des Tests | Eindeutige Codierung des Tests | Body |
| Analysenbezeichnung | Bezeichnung der Analyse (aus dem Value Set ELGA_Laborparameter) |
Body |
| Ergebnis | Body | |
| Einheit | Body | |
| Referenzbereiche | Für die Beurteilung relevante Referenzwerte. Die Angabe mehrerer Referenzbereiche zu einem Test ist möglich. | Body |
| Befundinterpretation | Codierte Bewertung des Ergebnisses | Body |
| Deltacheck | Tendenzielle Veränderung zu Vorwerten | Body |
| Ergebniskommentar | Kommentar des Labors zu einem einzelnen Testergebnis | Body |
| Externes Labor | Kennzeichen ob ein Ergebnis extern ermittelt wurde | Body |
| Bakteriologische Ergebnisse | ||
| Analysen | Body | |
| Erreger2 (Isolate) | Body | |
| Antibiotischer Wirkstoff | Body | |
| Resistenzkennung | Codierte Bewertung der Resistenz (R,S,I) | Body |
Tabelle 1: Im Laborbefund abzubildende medizinische Daten
2 Erreger oder Krankheitserreger sind Stoffe oder Organismen, die in anderen Organismen potenziell gesundheitsschädigende Abläufe verursachen können.
3.3.2 Mikrobiologische Befunde
Unter den Analysen eines Laborbefunds finden sich viele aus dem Bereich der Mikrobiologie. Dieser Teil des Leitfadens beschäftigt sich mit den mikrobiologischen Methoden und Analysen im Labor, die sich nicht über die „klassische“ Struktur eines Laborbefundes darstellen lassen. Dies betrifft hauptsächlich die Bakteriologie zum Nachweis von Bakterien, z.B. mit der Darstellung von Keimwachstum, Koloniebeschreibung und Antibiogrammen. Die Strukturierung des mikrobiologischen Befundes folgt einem bestimmten Muster, das den Untersuchungsverlauf widerspiegelt: Beschreibung des entnommenen Materials (z.B. Mittelstrahlharn), die direkt untersuchten Eigenschaften des Materials (z.B. Farbe), mikroskopische Untersuchung des Materials (z.B. Erythrozyten, Leukozyten, grampositive Bakterien). Falls Bakterienwachstum festgestellt wird, folgt eine Beschreibung der Kulturen, eine Benennung der Reinkulturen (Isolate) mit Nennung der taxonomischen Bestimmung der Mikroorganismen (z.B. Streptococcus pyogenes) ggf. mit Angabe des Serovars/Pathovars. Meist wird ein Antibiogramm angefügt. Es kann auch eine minimale Hemmkonzentration (MHK) enthalten sein.
Dementsprechend ist folgende hierarchische Struktur abzubilden:
Zur Kennzeichnung des Mikrobiologiebefundes über die ServiceEvents siehe Kapitel Spezielle Vorgaben.
3.4 Hierarchie der Implementierungsleitfäden
Der vorliegende Implementierungsleitfaden basiert auf dem „Allgemeinen Implementierungsleitfaden“, der grundlegenden Implementierungsvorschrift für alle CDA Dokumente im österreichischen Gesundheitswesen [4]. Der CDA “Laborbefund“ hat grundsätzlich beiden aufeinander aufbauenden Implementierungsleitfäden zu folgen.
Die administrativen Daten im Dokumentheader und grundsätzliche Vorgaben für den medizinischen Inhalt werden vom „Abbildung 1: Allgemeinen Implementierungsleitfaden“ definiert. Der jeweilige „Spezielle Implementierungsleitfaden“ enthält die Vorgaben für die medizinischen Inhalte und ergänzt gegebenenfalls die Header-Vorgaben.
Für die Verwendung dieses Implementierungsleitfadens sind zusätzlich die Vorgaben aus
„HL7 Implementation Guide for CDA® R2: Allgemeiner Implementierungsleitfaden für ELGA CDA Dokumente“ [OID Root 1.2.40.0.34.7.1]
in der Hauptversion 2 vorausgesetzt.
3.5 Verweis auf den Allgemeinen Leitfaden
Verweis auf den Allgemeinen Leitfaden:
Die Elemente erfordern keine speziellen Vorgaben. Es gelten die Vorgaben der entsprechenden Kapitel des „Allgemeinen Implementierungsleitfadens“.
3.6 Menschenlesbar vs. maschinenlesbar: CDA Level 2 oder Level 3
CDA-Dokumente müssen grundsätzlich für menschliche Betrachter lesbar sein. Das gilt für sämtliche Inhalte, so wie sie vom Ersteller signiert worden sind. Technisch ist das über den so genannten CDA Text Level („Level 1“) und Section Level („Level 2“) umgesetzt.
Zusätzlich können CDA-Dokumente auch codierte Teile enthalten, die für die automatisierte maschinelle Weiterverarbeitung gedacht sind, etwa zur automatischen Erstellung von Zeitverläufen über Ergebnisse aus mehreren, zu verschiedenen Zeitpunkten erstellten Befunden. Die maschinenlesbaren Teile werden technisch im so genannten CDA Entry Level („Level 3“) Teil des Befundes abgelegt.
Dabei gelten folgende Regelungen, um sicherzustellen, dass der menschenlesbare Teil und der maschinenlesbare Teil keine widersprüchlichen Daten enthalten: Als verbindlich gelten die menschenlesbaren Inhalte, die im „Level 2“ dargestellt sind.
Für ELGA Laborbefunde gilt, dass, sollte eine Sektion maschinenlesbare Inhalte codieren, der meschenlesbare Inhalt des Dokuments vollständig aus den codierten Inhalten erzeugt werden kann. Dies bedeutet, dass sämtliche Informationen in einer Sektion sowohl maschinenlesbar als auch menschenlesbar vorliegen.
Der menschenlesbare Teil kann daher keine Daten enthalten, die im maschinenlesbaren Teil nicht enthalten sind.
3.7 IHE Konformität
3.7.1 Referenz
Der vorliegende Leitfaden baut auf den Definitionen des „Laboratory Technical Framework Volume 3 (LAB TF-3) Revision 3.0, 2011“ [3] auf, welche durch diesen Leitfaden weiter eingeschränkt werden. Dadurch erhalten die entsprechenden Templates ihre Gültigkeit und sind aus Konformitätsgründen bei Komponenten, welche über eine entsprechende Definition verfügen, auch anzugeben.
3.7.2 Angabe der Adresse und Telefonnummer
Entsprechend den Vorgaben des IHE Frameworks für Labor sind für Personen und Organisationen die Angabe einer Adresse (addr-Element) und Telekom Verbindung (telecom-Element) verpflichtend. Diese können jedoch mit einem nullFlavor versehen werden.
4 Anwendungsfälle
Definition: Der Laborbefund wurde für die Arbeit an diesem Leitfaden wie folgt definiert:
Ein Laborbefund (aus dem Bereich der med. u. chem. Labordiagnostik) ist der fachärztlich vidierte, kommentierte/interpretierte Befund morphologischer, biologischer, chemischer, molekularer, physikalischer und spezieller immunologischer Untersuchungsverfahren aus Körpersäften, der Beurteilung ihrer morphologischen Bestandteile sowie von ab- und ausgeschiedenem Untersuchungsmaterial zur Erkennung physiologischer Eigenschaften, krankhafter Zustände, zu Verlaufskontrollen und zur Gesundheitsvorsorge/Prophylaxe.
ELGA Laborbefunde umfassen u. a. klinische Chemie und Immunchemie, Hämatologie (Erkrankungen des Blutes) und Hämostaseologie (Störungen der Blutgerinnung), Proteinchemie, Serologie, molekulare Diagnostik, Toxikologie, Drugmonitoring, Mikrobiologie, Infektionsserologie, Zytologie, Untersuchungen und die Hilfestellung für andere Fächer im Rahmen von Therapievorschlägen bei Gerinnungsstörungen, Antikoagulanzientherapien, der Impfkontrolle, Vorsorgediagnostik und Risikostratifizierung.
Untersuchungen des Sonderfaches „Blutgruppenserologie und Transfusionsmedizin“ werden in einer gesonderten ELGA Dokumentenklasse (geplant) abgehandelt.
Sofern keine andere Regelung zutrifft, obliegt die Entscheidung ob ein Befund in ELGA gestellt wird dem Befundersteller.
Im ELGA Laborbefund dürfen nur dann Ergebnisse aus genetischen Analysen enthalten sein, wenn ihre Dokumentation in Übereinstimmung mit dem Gentechnikgesetz (GTG § 71a, BGBl. I Nr. 127/2005) erfolgt.
Der in diesem Leitfaden beschriebene Laborbefund dient also zum Austausch von fertiggestellten, und fachärztlich vidierten Befunden innerhalb und zwischen Einrichtungen des Gesundheitswesens. Ein wesentlicher Nutzer der Befunde ist auch der Patient selbst, der die Befunde über das ELGA Bürgerportal einsehen wird.
Der in diesem Leitfaden beschriebene Laborbefund ist zur Dokumentation und Kommunikation (vollständig) fertiggestellter Laborbefunde gedacht.
Der hier beschriebene Laborbefund ist nicht vorgesehen um Zwischenergebnisse und Nachrichten über einzelne Prozessschritte zu kommunizieren, wie etwa
- die Anforderung von Laboruntersuchungen
- das Einlangen einer Probe im Labor
- den Beginn, Stornierung oder die Fertigstellung einzelner Untersuchungen
Ergänzungen und Korrekturen von Laborbefunden werden unterstützt
4.1 Anwendungsfall LAB01: „Laboruntersuchung eines niedergelassenen Labors“
Typischerweise entstehen Laborbefunde in medizinischen Labors. Einerseits sind das niedergelassene Labors, die als selbständige Unternehmen Laboruntersuchungen anbieten. Diese werden vielfach auf Zuweisung von Patienten durch praktische Ärzte im niedergelassenen Bereich tätig. Die Entstehung eines Laborbefundes beginnt mit einer Überweisung durch einen niedergelassenen Arzt, oder mit einer Anforderung innerhalb eines Spitals. Entweder wird das Spezimen am Patienten gleichzeitig entnommen, und dann ins Labor geschickt oder der Patient muss das Labor aufsuchen, und das Spezimen wird dann erst dort entnommen. Nach Abschluss der Untersuchung wird der Befund dem zuweisenden Arzt und/oder dem Patienten in Papierform übermittelt.
Laboruntersuchungen im Rahmen ambulanter Aufenthalte in einem Spital fallen ebenso unter diesen Anwendungsfall.
4.2 Anwendungsfall LAB02: „Laboruntersuchung im Rahmen eines stationären Aufenthalts in einem Spital“
Im Rahmen von stationären Aufenthalten von Patienten in Spitälern kommt es in der Regel zu einer Reihe von Laboruntersuchungen, die in der internen Krankengeschichte (meistens auch elektronisch) abgelegt werden. Relevante Befunde werden dem einweisenden Arzt bzw. dem Patienten im Zuge der Entlassungsdokumentation mit übermittelt. Dieses passiert oftmals als Teil des Entlassungsbriefes. Welche Werte und welche Befunde entsprechende Relevanz haben um weitergeleitet zu werden, entscheidet das jeweilige ärztliche Fachpersonal in der Klinik.
4.3 Anwendungsfall LAB03: „Teilweise externe Vergabe von Laboruntersuchungen“
In vielen Fällen kommt es zu Kooperationen zwischen Laborbefund erstellenden Organisationen. Folgende Fälle seien angeführt:
- Spitäler kooperieren mit niedergelassenen Labors. Zum Teil verfügen nicht alle Spitäler über eigene Labors, andererseits werden auch Spezialuntersuchungen, die das Spitalslabor nicht durchführt, an niedergelassene Labors vergeben.
- Niedergelassene Labors verfügen nicht über das volle Leistungsspektrum und senden Laboruntersuchungen an Spitallabors, welche spezielle Parameter messen können.
- Es bestehen Kooperationen zwischen mehreren Spitälern. Einerseits sind das oft Spitäler, die dem gleichen Spitalsträger angehören. Teilweise bestehen auch Kooperationen zwischen Spitälern unterschiedlicher Träger, die durch die örtliche Nähe leicht Proben austauschen können.
In allen Fällen werden einzelne Labortests nicht selbst durchgeführt sondern diese Tests an ein externes kooperierendes Labor vergeben. Das externe Labor führt dann den Test durch, und übermittelt die Ergebnisse an das ursprünglich für die Untersuchungen zuständige Labor. Dort werden dann die vom externen Labor ermittelten Testergebnisse in den eigenen Laborbefund eingefügt. Das ursprünglich zuständige Labor, das den Befund erstellt, muss in diesem Fall die extern erbrachten Testergebnisse als solche erkennbar kennzeichnen.
4.4 Anwendungsfall LAB04: „Update von Laborbefunden“
Ein fertiggestellter Laborbefund wird korrigiert oder ergänzt, um
- die Inhalte des Befundes zu korrigieren (etwa das Ergebnis einer Analyse),
- einzelne (fehlerhafte) Analysen nachträglich aus dem Befund zu stornieren oder
- fehlende Analysen zu ergänzen (etwa besonders lang dauernde Analysen).
Änderungen sollen im Text für den Leser klar kenntlich gemacht werden (eine codierte Angabe kann im narrativen Text mit Revisionsmarken erfolgen).
Eine Korrekturversion MUSS in ELGA immer alle zum Befund gehörigen Analysen enthalten, da die Vorversion als veraltet (deprecated) gekennzeichnet wird. Stornierte Analysen sind explizit mit dem entsprechenden StatusCode zu kennzeichnen.
Für den Leser/Empfänger gilt: Eine neue Version ersetzt die alte Version des Befundes, alle Analysen sollen beim Import ersetzt bzw. überschrieben werden. Sollte eine Analyse in der neuen Version fehlen, soll diese als „storniert“ interpretiert werden.
5 Administrative Daten (CDA Header)
Dieses Kapitel basiert auf dem entsprechenden Kapitel im „Allgemeinen Implementierungsleitfaden“ [4] und beschreibt die laborspezifischen Implementierungen bzw. über die Basisdefinitionen hinausgehenden Spezifikationen zum Thema „Laborbefund“.
5.1 Überblick
| Feld | Element | Opt | Kapitel |
|---|---|---|---|
| Daten zum Dokument | |||
| Realm Code | ClinicalDocument/realmCode | M | Link |
| Dokumentenformat | ClinicalDocument/typeId | M | Link |
| Dokumenten-ID | ClinicalDocument/id | M | Link |
| Vertraulichkeitscode | ClinicalDocument/confidentialityCode | M | Link |
| Sprachcode | ClinicalDocument/languageCode | M | Link |
| Template | ClinicalDocument/templateId | M | Link |
| Dokumenttitel | ClinicalDocument/title | M | Link |
| Dokumentenklasse | ClinicalDocument/code | M | Link |
| Dokumentdatum | ClinicalDocument/effectiveTime | M | Link |
| Versionierung des Dokuments | ClinicalDocument/setId ClinicalDocument/versionNumber |
M | Link |
| Teilnehmende Parteien | |||
| Patient | ClinicalDocument/recordTarget | M | Link |
| Verwalter des originalen Dokuments | ClinicalDocument/custodian | M | Link |
| Rechtlicher Unterzeichner | ClinicalDocument/legalAuthenticator | M [1..1] |
Link |
| Verfasser des Dokuments | ClinicalDocument/author | M [1..*] |
Link |
| Vorgesehener Empfänger | ClinicalDocument/informationRecipient | O [0..*] |
Link |
| Validatoren | ClinicalDocument/authenticator | O [0..*] |
Link |
| Referenz zum Auftrag | |||
| Auftraggeber (IHE „Ordering Provider“) | ClinicalDocument/participant@typeCode=“REF“ | R [1..1] |
Link |
| Auftragsidentifikation | ClinicalDocument/inFulfillmentOf/order | M [1..1] |
Link |
| Dokumentation der Gesundheitsdienstleistung | |||
| Service Events | ClinicalDocument/documentationOf/serviceEvent | M [1..*] |
Link |
| Durchführende Labors | ClinicalDocument/documentationOf/serviceEvent/performer | O [0..*] |
Link |
| Informationen zum Patientenkontakt | |||
| Encounter | ClinicalDocument/componentOf/encompassingEncounter | O [0..1] |
Link |
Tabelle 2: Überblick administrative Daten (Header)
5.2 Dokumentenstruktur
5.2.1 Elemente ohne spezielle Vorgaben
Folgende Elemente erfordern keine speziellen Vorgaben:
- XML Metainformationen
- Wurzelelement
- Hoheitsbereich („realmCode“)
- Dokumentformat („typeId“)
- Dokumenten-Id („id”)
- Erstellungsdatum des Dokuments („effectiveTime“)
- Vertraulichkeitscode („confidentialityCode“)
- Sprachcode des Dokuments („languageCode“)
Verweis auf den Allgemeinen Leitfaden:
Das Element erfordert keine speziellen Vorgaben. Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“.
5.2.2 XML Metainformationen
5.2.2.1 Zeichencodierung
CDA-Dokumente MÜSSEN mit UTF-8 (8-Bit Universal Character Set Transformation Format, nach RFC 3629 / STD 63 (2003)) codiert werden.
<?xml version="1.0" encoding="UTF-8" standalone=”yes”?>
<ClinicalDocument xmlns="urn:hl7-org:v3">
:
5.2.2.2 Hinterlegung eines Stylesheets
Um ein CDA-Dokument in einem Webbrowser anzeigen zu können, muss es nach HTML tranformiert werden. Das kann durch eine XSLT-Transformation (ein so genanntes „Stylesheet“) geschehen. Ist das Stylesheet im angegebenen Pfad erreichbar, wird dieses beim Öffnen des CDA-Dokuments mit einem Browser üblicherweise automatisch auf das CDA-Dokument angewandt und die Darstellung gerendert.
ELGA stellt zur einheitlichen Darstellung von CDA-Dokumenten ein „Referenz-Stylesheet“ zur Verfügung (Download ist von der ELGA Website http://www.elga.gv.at/cda möglich). Da der Zugriff auf XSLT-Programme von den meisten Browsern eingeschränkt ist, wird kein absoluter Pfad auf eine Webressource angegeben.
<?xml version="1.0" encoding="UTF-8" standalone=”yes”?>
<?xml-stylesheet type="text/xsl" href="ELGA_Stylesheet_v1.0.xsl"?>
<ClinicalDocument xmlns="urn:hl7-org:v3">
:
Das Stylesheet „ELGA_Stylesheet_v1.0.xsl“ MUSS angegeben werden [M]. Die Angabe eines Pfades ist NICHT ERLAUBT. Ausnahmen können für automatisiert erstellte Dokumente notwendig sein, diese müssen im allgemeinen und speziellen Leitfäden beschrieben werden.
5.2.3 Wurzelelement
Der XML-Namespace für CDA Release 2.0 Dokumente ist urn:hl7-org:v3 (Default-Namespace). Dieser MUSS in geeigneter Weise in jeder CDA XML Instanz genannt werden. In speziellen Leitfäden können weitere namespace-Präfixe angegeben werden.
Für ELGA CDA-Dokumente MUSS der Zeichensatz UTF-8 verwendet werden.
CDA-Dokumente beginnen mit dem Wurzelelement ClinicalDocument, der grobe Aufbau ist im folgenden Übersichtsbeispiel gegeben.
<ClinicalDocument xmlns="urn:hl7-org:v3">
<!-- CDA Header -->
… siehe Beschreibung CDA R2 Header …
<!-- CDA Body -->
<component>
<structuredBody>
… siehe Beschreibung CDA R2 Body …
</structuredBody>
</component>
</ClinicalDocument>
5.2.4 Hoheitsbereich des Dokuments („realmCode“)
Dieses Element kennzeichnet, dass das Dokument aus dem Hoheitsbereich Österreich (bzw. Bereich der HL7 Affiliate Austria, Code „AT“) stammt.
5.2.4.1 Strukturbeispiel
<realmCode code="AT'"/>
5.2.4.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| realmCode | CS CNE |
1..1 | M | Hoheitsbereich des Dokuments Fester Wert: @code = AT |
5.2.5 Dokumentformat („typeId“)
Dieses Element kennzeichnet, dass das Dokument im Format CDA R2 vorliegt.
5.2.5.1 Strukturbeispiel
<typeId root="2.16.840.1.113883.1.3" extension="POCD_HD000040"/>
5.2.5.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| typeId | II | 1..1 | M | Dokumentformat CDA R2 Feste Werte: @root = 2.16.840.1.113883.1.3' @extension = POCD_HD000040 |
5.2.6 Dokumenten-Id („id”)
Die Dokumenten-Id eines CDA-Dokuments ist ein eindeutiger Instanzidentifikator, der das Dokument weltweit eindeutig und für alle Zeit identifiziert. Ein CDA-Dokument hat genau eine Id.
5.2.6.1 Strukturbeispiel
<id root="1.2.40.0.34.99.111.1.1" extension="134F989" assigningAuthorityName="Amadeus Spital"/>
5.2.6.2 Spezifikation
Es MUSS eine gültige und innerhalb des ID-Pools eindeutige Dokumenten-ID angegeben werden.
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| id | II | 1..1 | M | Dokumenten-Id Grundsätzlich sind die Vorgaben gemäß „Identifikations-Elemente“ zu befolgen. |
5.2.7 Erstellungsdatum des Dokuments („effectiveTime“)
5.2.7.1 Spezifikation
5.2.8 Vertraulichkeitscode („confidentialityCode“)
5.2.8.1 Spezifikation
| Id | 1.2.40.0.34.11.90009 ref elgabbr- | Gültigkeit ab | 2013‑11‑07 | |||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||
| Name | CDconfidentialityCode | Bezeichnung | CD confidentialityCode | |||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.90009 CD confidentialityCode (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||
5.2.9 Sprachcode des Dokuments („languageCode“)
5.2.9.1 Spezifikation
| Id | 1.2.40.0.34.11.90010 ref elgabbr- | Gültigkeit ab | 2013‑11‑07 | |||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||
| Name | CDlanguageCode | Bezeichnung | CD languageCode | |||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.90010 CD languageCode (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||
5.2.10 Elemente mit spezielle Vorgaben
5.2.10.1 Template („ClinicalDocument/templateId“)
Das Template definiert die Summe der Einschränkungen dieser Spezifikation in Bezug auf den CDA R2 Standard. Eine templateID für den ELGA Laborbefund ist anzugeben. Ein Dokument, welches dem vorliegenden Implementierungsleitfaden folgt, muss auch dem übergeordneten „Allgemeinen Implementierungsleitfaden“ folgen. Als templateID für CDA Labordokumente gemäß diesem Leitfaden ist 1.2.40.0.34.11.4 zu verwenden.
5.2.10.1.1 Strukturbeispiel
<ClinicalDocumentxmlns="urn:hl7-org:v3"> : <!-- ELGA CDA Dokumente --> <templateId root="1.2.40.0.34.11.1"/> <!-- ELGA CDA Laborbefund --> <templateId root="1.2.40.0.34.11.4"/> <!-- In Abhängigkeit von der ELGA Interoperabilitätsstufe (EIS) --> <!-- EIS „Basic“ --> <templateId root="1.2.40.0.34.11.4.0.1"/> ... oder ... <!-- EIS „Enhanced“ --> <templateId root="1.2.40.0.34.11.4.0.2"/> ... oder ... <!-- EIS „Full support“ --> <templateId root="1.2.40.0.34.11.4.0.3"/> : </ClinicalDocument>
5.2.10.1.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| templateId | II | 1..1 | M | ELGA TemplateId für den Allgemeinen Implementierungsleitfaden Fester Wert: @root = 1.2.40.0.34.11.1 |
| templateId | II | 1..1 | M | ELGA TemplateId für den speziellen Implementierungsleitfaden Laborbefund Fester Wert: @root = .2.40.0.34.11.4 |
| --- zusätzlich eine der folgenden templateIds --- | ||||
| Im Falle von EIS „Basic“ (Das Dokument enthält entweder unstrukturierten oder eingebetteten Inhalt (z.B. PDF) oder enthält strukturierten Inhalt, wobei jedoch nicht alle Sektionen den Vorgaben von EIS „Enhanced“ oder höher folgen) | ||||
| templateId | II | 1..1 | M | ELGA CDA Laborbefund Fester Wert @root = 1.2.40.0.34.11.4.0.1 |
| --- oder --- | ||||
| Im Falle von EIS „Enhanced“ (Alle Sections folgen ausnahmelos den Vorgaben von EIS „Enhanced“ oder höher, aber nicht alle Sections folgen den Vorgaben von EIS „Full support“) | ||||
| templateId | II | 1..1 | M | ELGA CDA Laborbefund in EIS „Enhanced“ Fester Wert @root = 1.2.40.0.34.11.4.0.2 |
| --- oder --- | ||||
| Im Falle von EIS „Full support“: (Alle Sektionen folgen ausnahmslos den Vorgaben von EIS „Full support“) | ||||
| templateId | II | 1..1 | M | ELGA CDA Laborbefund in EIS „Full support“ Fester Wert @root = 1.2.40.0.34.11.4.0.3 |
5.2.10.2 Dokumentenklasse (“ClinicalDocument/code”)
Die zur Anwendung kommende Dokumentenklasse wird durch den LOINC Code 11502-2 für einen allgemeinen Laborbefund („multidisciplinary laboratory report“) abgebildet.
Diese Codierung stellt einen allgemeinen Laborbefund dar, der es erlaubt beliebige Befundarten und Ergebnisse im Rahmen eines Dokumentes zu übermitteln, auch wenn der Befund nur eine bestimmte Befundart (wie z.B. Hämatologie) enthält. Diesem Umstand wird jedoch durch die Angabe der enthaltenen Laborbefundarten bei der Registrierung eines Labordokumentes in der Registry Rechnung getragen. Durch die Registrierung der in einem Labordokument enthaltenen Befundkategorien über die Service-Event-Metadaten („eventCodeList“) sind auch Detailbefunde in der ELGA einfach auffindbar.
Der Mikrobiologiebefund ist in den ServiceEvents mit dem Code 18725-2 (Microbiology studies) anzugeben.
5.2.10.2.1 Strukturbeispiel
<ClinicalDocumentxmlns="urn:hl7-org:v3">
:
<!-- Dokumentenklasse -->
<code code="11502-2" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Laboratory report"/>
<!-- Titel des Dokuments -->
<title>Allgemeiner Laborbefund</title>
:
</ClinicalDocument>
5.2.10.2.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| code | CE CWE |
1..1 | M | Code des Dokuments | |
| @code | cs | 1..1 | M | Fester Wert: 11502-2 (aus Value Set „ELGA_Dokumentklassen“ ) | |
| @displayName | st | 0..1 | R2 | Fester Wert: Laboratory report | |
| @codeSystem | uid | 1..1 | M | Fester Wert: 2.16.840.1.113883.6.1 | |
| @codeSystemName | ADXP | 0..1 | R2 | Fester Wert: LOINC | |
5.2.10.3 Dokumenttitel („ClinicalDocument/title“)
Der Titel des Dokumentes ist verpflichtend anzugeben, vom Ersteller frei zu vergeben und beschreibt die Art des Dokumentes näher. Der Titel des Dokuments ist für den lesenden Dokumentempfänger das sichtbare Element. Dieser wird nicht dem Attribut displayName des Elements code entnommen, sondern dem (verpflichtenden) Element title. Der Sinn der Benennung ist jedoch gemäß der Dokumentenklassen zu wählen. Im allgemeinen Fall wird die Bezeichnung „Laborbefund“ verwendet.
5.2.10.3.1 Strukturbeispiel
<ClinicalDocumentxmlns="urn:hl7-org:v3">
:
<!-- Dokumentenklasse -->
<code code="11502-2" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Laboratory report"/>
<!-- Titel des Dokuments -->
<title>Allgemeiner Laborbefund</title>
:
</ClinicalDocument>
5.2.10.3.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| title | ST | 1..1 | M | Dokumententitel Der Sinn der Benennung MUSS mit der Dokumentenklasse übereinstimmen. | |
5.2.10.4 Versionierung des Dokuments („setId“ und „versionNumber“)
Für alle Dokumente ist gemäß den Vorgaben des „Allgemeinen Implementierungsleitfadens“ eine Versionierung verpflichtend vorzusehen. Für Detailinformationen wird auf dieses Dokument verwiesen.
<ClinicalDocument xmlns="urn:hl7-org:v3"> : <!-- Versionierung des Dokuments --> <setId root="2.2.40.0.34.99.111.1.1" extension="AAAAAAAAAAAAAAAAAAA"/> <versionNumber value="1"/> : </ClinicalDocument>
5.3 Teilnehmende Parteien
5.3.1 IHE LAB TF-3 Konformität
Gem. [3] sind für Angaben zu Personen und Organisationen die Elemente name, addr und telecom verpflichtend. Ausgenommen sind Elemente definiert in Elemente ohne spezielle Vorgaben.
5.3.2 Elemente ohne spezielle Vorgaben
Folgende Elemente erfordern keine speziellen Vorgaben:
- Patient (recordTarget/patientRole)
- Personen bei der Dateneingabe (dataEnterer)
- Verwahrer des Dokuments (custodian)
- Beabsichtigte Empfänger des Dokuments(informationRecipient)
Verweis auf Allgemeinen Leitfaden:
Die Elemente erfordern keine speziellen Vorgaben. Es gelten die Vorgaben der entsprechenden Kapitel des „Allgemeinen Implementierungsleitfadens“.
5.3.3 Patient („recordTarget/patientRole“)
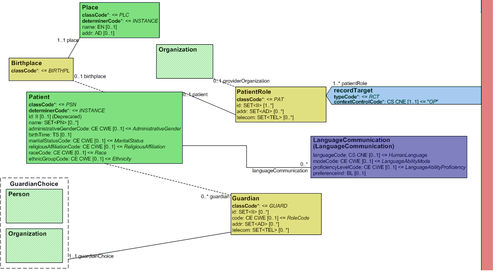
Im CDA-Header wird mindestes eine Patientenrolle beschrieben, die zu genau einer Person zugehörig ist. Die recordTarget Beziehung weist auf die Patient-Klasse und gibt an, zu welchem Patienten dieses Dokument gehört.
Auszug aus dem R-MIM:
5.3.3.1 Spezifikation
| Id | 1.2.40.0.34.11.20001 ref elgabbr- | Gültigkeit ab | 2017‑07‑20 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderRecordTarget | Bezeichnung | HeaderRecordTarget | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20001 HeaderRecordTarget (2017‑03‑27) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.3.3.1.1 id
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||
|---|---|---|---|---|---|---|
| id[1] | II | 1..1 | M | Identifikation des Patienten im lokalen System Grundsätzlich sind die Vorgaben gemäß Kapitel „Identifikations-Elemente“ zu befolgen. | ||
| id[2] | II | 1..1 | R | Sozialversicherungsnummer des Patienten Zugelassene nullFlavor:
| ||
| @root | uid | 1..1 | M | OID der Liste aller österreichischen Sozialversicherungen Fester Wert: 1.2.40.0.10.1.4.3.1 | ||
| @extension | st | 1..1 | M | Vollständige Sozialversicherungsnummer des Patienten (alle 10 Stellen) | ||
| @assigningAuthorityName | st | 0..1 | O | Fester Wert: Österreichische Sozialversicherung | ||
| id[3] | II | 0..1 | O | Bereichsspezifisches Personenkennzeichen, Bereichskennzeichen GH (Gesundheit) | ||
| @root | uid | 1..1 | M | OID der österreichischen bPK Fester Wert: 1.2.40.0.10.2.1.1.149 | ||
| @extension | st | 1..1 | M | bPK-GH des Patienten: Bereichskürzel + bPK (Base64, 28 Zeichen) (insg. 31 Stellen) Anmerkung: Das bPK dient ausschließlich der Zuordnung der elektronischen Identität und darf daher nicht am Ausdruck erscheinen | ||
| @assigningAuthorityName | st | 0..1 | O | Fester Wert: Österreichische Stammzahlenregisterbehörde | ||
Hinweis: Die Reihenfolge der id-Elemente MUSS unbedingt eingehalten werden!
5.3.3.1.2 addr
Es MUSS eine mögliche Adresse unterstützt werden. Spezielle Leitfäden (z.B. Entlassungsbrief Pflege) können es erforderlich machen, dass auch mehr als eine Adresse unterstützt werden muss.
5.3.3.1.3 patient/languageCommunication
In der Klasse languageCommunication können Informationen bezüglich der Sprachfähigkeiten und Ausdrucksform (z.B. gesprochen oder geschrieben) des Patienten angegeben werden.
Dieser Leitfaden schränkt die möglichen Werte für die Sprache auf Werte aus dem Value Set ELGA_HumanLanguage ein. Gemäß IETF / RFC 3066 enthält es ein bestimmtes Subset von Codes aus ISO 639-1 und ISO 639-2 (also zwei- und dreistellige Sprachcodes). Gemäß RFC 3066 ist es zulässig, eine Angabe der landestypischen Ausprägung der Sprache nach einem Bindestrich anzufügen. Das Land wird dabei nach ISO 3166-1 Alpha 2 angegeben. Dies MUSS bei der Auswertung des languageCodes berücksichtigt und toleriert werden.
5.3.3.1.4 patient/guardian
In der Klasse guardian können Informationen bezüglich eines Vormunds/Sachwalters des Patienten angegeben werden. Begriffsdefinition:
- Ein Vormund kann existieren, wenn die Person noch nie geschäftsfähig war
- z.B. Kinder
- Ein Sachwalter kann existieren, wenn die Person schon geschäftsfähig war, die Geschäftsfähigkeit aber entzogen wurde
- z.B. Alte Personen
Vormund/Sachwalter kann entweder eine Person (guardianPerson) oder eine Organisation (guardianOrganization) sein. Beim Patient können optional ein oder mehrere Vormund/Sachwalter Element(e) angegeben werden. Wenn ein Sachwalter bekannt ist, SOLL diese Information auch angegeben werden.
5.3.4 Personen der Dateneingabe („dataEnterer“)
5.3.4.1 Spezifikation
| Id | 1.2.40.0.34.11.20003 ref elgabbr- | Gültigkeit ab | 2013‑02‑10 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderDataEnterer | Bezeichnung | HeaderDataEnterer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Die das Dokument „schreibende“ Person (z.B. Schreibkraft, Stationsschwester, …). | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20003 HeaderDataEnterer (2013‑02‑10) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
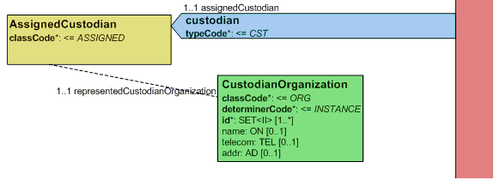
5.3.5 Verwahrer des Dokuments („custodian“)
Auszug aus dem R-MIM:
5.3.5.1 Spezifikation
| Id | 1.2.40.0.34.11.20004 ref elgabbr- | Gültigkeit ab | 2015‑05‑28 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderCustodian | Bezeichnung | HeaderCustodian | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20004 HeaderCustodian (2015‑05‑28) ref elgabbr- Version: Template 1.2.40.0.34.11.20004 HeaderCustodian (2011‑12‑19) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.3.5.1.1 id
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| id | II | 1..1 | R | Identifikation des Verwahrers des Dokuments aus dem GDA-Index. Grundsätzlich sind die Vorgaben gemäß Kapitel „Identifikations-Elemente“ zu befolgen.“
| |
 In der nächsten Version des Leitfadens wird die Konformität entsprechend dem CDA-Standard auf [M] erhöht, Null Flavors sind dann nicht mehr erlaubt.
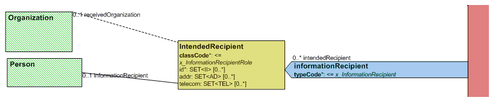
In der nächsten Version des Leitfadens wird die Konformität entsprechend dem CDA-Standard auf [M] erhöht, Null Flavors sind dann nicht mehr erlaubt.5.3.6 Beabsichtigte Empfänger des Dokuments („informationRecipient“)
Auszug aus dem R-MIM:
5.3.6.1 Spezifikation
| Id | 1.2.40.0.34.11.20005 ref elgabbr- | Gültigkeit ab | 2011‑12‑19 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderInformationRecipient | Bezeichnung | HeaderInformationRecipient | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20005 HeaderInformationRecipient (2011‑12‑19) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.3.7 Verfasser des Dokuments („ClinicalDocument/author“)
Der Autor ist grundsätzlich der „das Dokument verfassende Arzt“. Damit sind diejenigen Personen gemeint, welche das Dokument „inhaltlich“ verfassen (z.B.: diktieren, erheben, messen). Der Autor kann entweder eine Person, ein Software System oder beides sein. Gemäß [3] MUSS mindestens eine Person als Autor angegeben werden, mehrere Autoren sind zulässig.
5.3.8 Medizinischer Validator („ClinicalDocument/legalAuthenticator“)
Das verpflichtende legalauthenticator-Element MUSS angegeben werden und repräsentiert den rechtlichen Unterzeichner (typischerweise der „Medizinische Validator“ oder der laborverantwortliche Arzt).
Im ELGA Referenz-Stylesheet wird der rechtliche Unterzeichner als „Unterzeichnet von“ dargestellt.
5.3.9 Validator („ClinicalDocument/authenticator“)
Ein authenticator-Element repräsentiert einen Validator, der das Dokument inhaltlich freigibt (zusätzliche medizinische und technische Validatoren). Es können mehrere Validatoren angegeben werden. Einer davon kann auch ident mit dem „rechtlichen Unterzeichner“ („ClinicalDocument/legalAuthenticator“) sein.
Aufgrund der Konformität zu IHE [3] ist die Angabe von name, addr und telecom verpflichtend. Der „Validator“ ist weiters mit der templateId „1.3.6.1.4.1.19376.1.3.3.1.5“ zu kennzeichnen.
5.3.9.1 Spezifikation
| Id | 1.2.40.0.34.11.20007 ref elgabbr- | Gültigkeit ab | 2011‑12‑19 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderAuthenticator | Bezeichnung | HeaderAuthenticator | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Dokumente können neben dem verpflichtenden legalAuthenticator („rechtlichen Unterzeichner“, Hauptunterzeichner) auch beliebig viele weitere Mitunterzeichner beinhalten. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20007 HeaderAuthenticator (2011‑12‑19) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.3.10 Weitere Beteiligte („participant“)
Die Kardinalitäten/Konformitäten der Beteiligten sind wie folgt geändert:
| Kard | Konf | Art des Beteiligten |
|---|---|---|
| 0..1 | [R2] | Fachlicher Ansprechpartner |
Es ist EMPFOHLEN, die fachliche Ansprechperson (Callback contact) im Laborbefund anzugeben.
5.4 Referenz zum Auftrag
5.4.1 Einweisender/Zuweisender/Überweisender Arzt
Aufgrund der Tatsache, dass IHE in dem Laboratory Technical Framework den Auftraggeber als participant mit dem typeCode=“REF“ führt und ELGA den einweisenden/zuweisenden/überweisenden Arzt ebenfalls als participant mit dem typeCode=“REF“ definiert, sich diese Elemente jedoch strukturell unterscheiden ist die Verwendung des ELGA Elements (mit templateId 1.2.40.0.34.11.1.1.2) NICHT ERLAUBT.
Die Verwendung dieses ELGA participant-Elements mit templateId 1.2.40.0.34.11.1.1.2 ist im Labor NICHT ERLAUBT.
5.4.2 Auftraggeber/„Ordering Provider“
Der Auftraggeber (bzw „ordering provider“, ClinicaDocument/participant@typeCode=“REF““) ist die Organisation oder der Arzt, welche/welcher den Auftrag erstellt hat. Der Auftraggeber wird als participant mit dem typeCode=“REF“ (referrer) ausgeführt und ist [R] verpflichtend anzugeben. Die Verwendung von NullFlavor ist möglich.
Der Auftraggeber ist des Weiteren mit der templateId "1.3.6.1.4.1.19376.1.3.3.1.6" zu kennzeichnen (die templateId entfällt bei Verwendung des NullFlavors).
5.4.2.1 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.3.1.6 ref elgabbr- | Gültigkeit ab | 2016‑07‑05 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 2016 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | IHEOrderingProvider | Bezeichnung | Ordering Provider | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.3.1.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.3.1.6 Ordering Provider (2016‑07‑05) ref elgabbr- Spezialisierung: Template 2.16.840.1.113883.10.12.108 CDA participant (2005‑09‑07) ref ad1bbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.4.2.2 Auftragsdatum („ClinicalDocument/participant@typeCode="REF"/time“)
Das Auftragsdatum ist das Datum/Zeit an dem der Auftrag vom Auftraggeber abgesendet wird. Das Auftragsdatum wird als time-Element beim Auftraggeber ausgeführt (siehe Kapitel Auftraggeber/Ordering Provider), und ist verpflichtend anzugeben. Bei einer manuellen Erfassung eines Auftrags im Labor kann dieses als nullFlavor=“NA“ ausgeführt werden.
5.4.3 Auftragsidentifikation („ClinicalDocument/inFulfillmentOf/order“)
Das Element beschreibt die Referenz auf den Auftrag auf der Auftraggeberseite. Es ist das id-Element für die Auftragsnummer auf Auftraggeberseite anzuführen.
Da die Referenz auf einen Auftrag im Labor eine wesentliche Information darstellt, ist das Element in Änderung zur Definition gem. „Allgemeinen Implementierungsleitfaden“ verpflichtend anzugeben.
5.4.3.1 Spezifikation
| Id | 1.2.40.0.34.11.20009 ref elgabbr- | Gültigkeit ab | 2011‑12‑19 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderInFulfillmentOf | Bezeichnung | HeaderInFulfillmentOf | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20009 HeaderInFulfillmentOf (2011‑12‑19) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.5 Dokumentation der Gesundheitsdienstleistung
5.5.1 Service Events („ClinicalDocument/documentationOf/serviceEvent“)
In diesem Element erfolgt die Dokumentation der wesentlichen Untersuchungsinhalte, die in einem CDA Laborbefund enthalten sind. D.h. bei der Einbringung des Dokuments in die Registry sind die serviceEvents-Elemente die einzige Möglichkeit medizinische Informationen einzubringen. Es können beliebig viele serviceEvent-Elemente angegeben werden, es ist jedoch zumindest ein serviceEvent zu codieren.
Verweis auf Allgemeinen Leitfaden (mit Anpassungen):
Das Element ist grundsätzlich gemäß den Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ anzugeben, es sind jedoch spezielle Vorgaben vorgeschrieben.
5.6 Dokumentation der Gesundheitsdienstleistung
5.6.1 Service Events („documentationOf/serviceEvent“)
Mit der Assoziation documentationOf/serviceEvent wird die eigentliche Gesundheitsdienstleistung repräsentiert, die in dem Dokument dokumentiert wird (z. B. eine Koloskopie, Appendektomie, etc.). Dies ist in engem Zusammenhang mit dem Dokumententyp zu sehen, der in ClinicalDocument/code wiedergegeben ist. Mit der documentationOf Beziehung kann die dokumentierte Gesundheitsdienstleistung näher spezifiziert werden. Dies darf natürlich nicht im Widerspruch zum Dokumententyp stehen.
In serviceEvent/effectiveTime kann der Zeitpunkt/Zeitraum der Gesundheitsdienstleistung angegeben werden. Im Gegensatz zum Encounter (siehe Kapitel „Informationen zum Patientenkontakt“), der ggf. mehrere Gesundheitsdienstleistungen „umrahmt“.
Da diese Informationen in die XDS-Metadaten übernommen werden, ergeben sich folgende Implikationen:
- Die serviceEvents sind die einzigen (rein) medizinischen Informationen zum Dokument im Dokumentenregister
- Können daher als Such-/Filterkriterium verwendet werden
- Scheint ggf. in den Ergebnissen der Suchabfragen auf
-> Sollte eine wertvolle Information sein (für den Behandler!)
Auszug aus dem R-MIM:
5.6.1.1 Spezifikation
Da dieses Element automatisch in die XDS-Metadaten übernommen wird, SOLL mindestens eine Gesundheitsdienstleistung als documentationOf/serviceEvent-Element angegeben werden [R2].
ACHTUNG: Die Zeitangaben der Gesundheitsdienstleistung (erstes documentationOf/serviceEvent-Element) werden in die Dokument-Metadaten übernommen!
Die Bedeutung der Dokument-Metadaten-Elemente lautet daher wie folgt:
serviceStartTime: Beginn des ersten documentationOf/serviceEvent-Elements
serviceStopTime: Ende des ersten documentationOf/serviceEvent-Elements
Die semantische Bedeutung dieser Zeitpunkte wird in den speziellen Implementierungs-leitfäden festgelegt.
Es können beliebig viele weitere Gesundheitsdienstleistungen als weitere documentationOf/serviceEvent-Elemente angegeben werden.
| Id | 1.2.40.0.34.11.20010 ref elgabbr- | Gültigkeit ab | 2011‑12‑19 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderServiceEvent | Bezeichnung | HeaderServiceEvent | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20010 (2017‑07‑21 11:18:58) ref elgabbr- Version: Template 1.2.40.0.34.11.20010 HeaderServiceEvent (2011‑12‑19) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Verweis auf speziellen Implementierungsleitfaden:
serviceEvent Element Allgemein
Ob eine Gesundheitsdienstleistung angegeben werden muss, und welche Bedeutung dieses Element hat, ergibt sich aus dem jeweiligen speziellen Implementierungsleitfaden.
code
Welche Codierung angewandt werden soll, ergibt sich aus dem jeweiligen speziellen Implementierungsleitfaden.
effectiveTime
Welche Start- und Endezeiten eingetragen werden sollen, ergibt sich aus dem jeweiligen speziellen Implementierungsleitfaden.
performer
Ob und welche durchführende Entität eingetragen werden soll, ergibt sich aus dem jeweiligen speziellen Implementierungsleitfaden.
effectiveTime
Hinweis: Für die automatisierte Datenübernahme aus dem CDA-Dokument in die XDS-Dokumentmetadaten ist stets ein Zeitintervall anzugeben.
5.6.1.2 Spezielle Vorgaben
Für den Laborbefund sind alle im Befund enthaltenen Befundarten als serviceEvent mit der entsprechenden Codierung anzuführen. Als Codierung wird das ELGA Value Set „ELGA_ServiceEventsLabor“ vorgegeben. Die Auswahl der zu codierenden Events erfolgt durch die im Rahmen des Laborauftrags enthaltenen Parameter. Diese unterliegen über das hierarchische Value Set „ELGA_Laborparameter“ einer Hierarchie durch die sich die auf der obersten Ebene zu codierenden serviceEvent-Elemente ergeben. Die nachfolgende Abbildung zeigt einen Auszug der Liste. Enthält nun z.B. der Laborauftrag den Parameter 26515-7 „Thrombozyten“ so ist gem. Hierarchie auf der obersten Ebene der Eintrag 300 „Hämatologie“ zu finden, welcher als serviceEvent codiert wird.
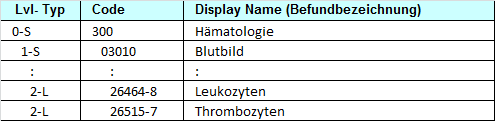
Abbildung 2: Auszug aus der Liste "ELGA_LaborParameter"
Der Mikrobiologiebefund ist in den ServiceEvents zusätzlich mit dem Code 18725-2 (Microbiology studies) anzugeben.
Ein Befund kann als Mikrobiologiebefund angegeben werden, wenn eine oder mehrere der Sektionen Bakteriologie, Kultureller Erregernachweis, Antibiogramm, Minimale Hemmkonzentration oder Molekularer Erregernachweis enthalten sind.
Die Angabe eines zeitlichen Erbringungsintervalls effectiveTime mit einer Start- low und Endzeit high ist verpflichtend. Optional kann der Erbringer der Leistung angegeben werden.
| Feld | Element |
|---|---|
| Service Event codiert | documentationOf/serviceEvent/code |
| Intervall der Erbringung | documentationOf/serviceEvent/effectiveTime |
| Leistungserbringende Stellen | documentationOf/serviceEvent/performer |
Tabelle 3: Überblick Elemente ServiceEvent
5.6.1.3 Spezifikation
| Id | 1.2.40.0.34.11.20010 ref elgabbr- | Gültigkeit ab | 2011‑12‑19 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | HeaderServiceEvent | Bezeichnung | HeaderServiceEvent | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.20010 (2017‑07‑21 11:18:58) ref elgabbr- Version: Template 1.2.40.0.34.11.20010 HeaderServiceEvent (2011‑12‑19) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.6.1.3.1 effectiveTime
Der Startzeitpunkt ist - sofern vorhanden - jenes Datum und jener Zeitpunkt, an dem das analysierende Labor die Anforderung vom Zuweiser in der Labor EDV erfasst hat. Anderenfalls sind Datum und Uhrzeit des Starts des Auftrags in der Labor EDV anzugeben. Die Endzeit ist die Abschlusszeit des Auftrags, welche in der Regel mit der medizinischen Freigabe des Auftrags ident ist.
5.6.2 Durchführende Labors („ClinicalDocument/documentationOf/serviceEvent/performer“)
Optional können die, die Laboruntersuchungen durchführenden, Labors dokumentiert werden. Nach [3] können diese an mehreren Stellen des Befundes angegeben werden. Wurde der Befund nur von einem Labor erstellt so ist dieses im Rahmen von ClinicalDocument/documentationOf/serviceEvent/performer anzugeben. Sind mehrere Labors an der Erstellung beteiligt so MUSS das Labor im structuredBody entweder auf entry-Ebene oder im Rahmen eines organizer oder direkt bei der Einzeluntersuchung (observation) angegeben werden.
Wird dieser Eintrag angeführt, so ist das Labor mit seinem Leiter angeführt. Gemäß [3] sind time, sowie name, telecom und addr VERPFLICHTEND anzugeben. Im Element time wird der Zeitpunkt oder die Zeitdauer angegeben, in der das Labor mit der Ausführung der Dienstleistung beschäftigt war. Weiters entspricht die Definition dem Template mit templateId „1.3.6.1.4.1.19376.1.3.3.1.7“, welche anzuführen ist.
5.6.2.1 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.3.1.7 ref elgabbr- | Gültigkeit ab | 2014‑05‑26 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryPerformer | Bezeichnung | Laboratory Performer | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.3.1.7 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.3.1.7 Laboratory Performer (2014‑05‑26) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
5.7 Informationen zum Patientenkontakt
5.7.1 Encounter (“componentOf/encompassingEncounter”)
Gemäß [3] ist die Angabe von Informationen zum Patientenkontakt im Rahmen des componentOf/encompassingEncounter-Elementes möglich. Da im Regelfall bei einer Laborleistung keine dementsprechende zu dokumentierende Leistung existiert, ist die Angabe dieser Information im österreichischen Laborbefund optional.
6 Medizinische Inhalte im Body
6.1 Fachlicher Inhalt in den ELGA Interoperabilitätsstufen (EIS)
6.1.1 Fachlicher Inhalt in EIS „Basic“ und „Structured“
Enthält das Dokument entweder unstrukturierten oder eingebetteten Inhalt (z.B. PDF) oder strukturierten Inhalt3 , wobei jedoch nicht alle Sektionen den Vorgaben von EIS „Enhanced“ oder „Full Support“ folgen, dann liegt das Dokument in ELGA Interoperabilitätsstufe (EIS) „Basic“ vor. Die Sektionen MÜSSEN jedenfalls in der von diesem Leitfaden definierten Reihenfolge vorliegen, damit die erforderliche ELGA Interoperabilitättstufe „Structured“ erreicht wird.
Die Verwendung von EIS Basic ist in ELGA nicht mehr zulässig.
3 Ensprechend den CDA Body Choices „NonXMLBody“ und „StructuredBody“, unconstrained CDA specification („CDA Level One“)
6.1.2 Fachlicher Inhalt in EIS „Enhanced“ oder „Full support“
Ein Dokument liegt in der ELGA Interoperabilitätsstufe (EIS) „Enhanced“ oder „Full support“ vor, wenn das Dokument strukturierten Inhalt enthält und alle Sections den Vorgaben von EIS „Enhanced“ oder höher folgen.
- EIS „Enhanced“
- Alle Sections folgen ausnahmelos den Vorgaben von EIS „Enhanced“ oder höher, aber nicht alle Sections folgen den Vorgaben von EIS „Full support“.
- EIS „Full support“
- Alle Sections folgen ausnahmelos den Vorgaben von EIS „Full support“.
6.2 Aufbau des Body
6.2.1 Strukturierter Body („structuredBody“)
Für Laborbefunde im Rahmen der ELGA sollten ausschließlich strukturierte Befunde übermittelt werden. Ein ELGA-Labor CDA-Dokument mit ausschließlich einem unstrukturiertem Body (nonXMLBody) ist im Rahmen der EIS Structured in einer Übergangsphase zulässig! Danach werden im Rahmen von EIS Enhanced und EIS Full Support ausschließlich nur mehr Level 3 codierte Befunde übermittelt.
Ein strukturierter Laborbefund MUSS zumindest eine Gliederungsebene („Bereiche“), kann aber zwei Gliederungsebenen („Bereiche“ und „Befundgruppen“) beinhalten.
6.2.2 Sektion Brieftext
Die Verwendung der Sektion Brieftext ist im Laborbefund ERLAUBT (Spezifikation siehe Allgemeiner Leitfaden [4], TemplateID: 1.2.40.0.34.11.1.2.1). Über diese Sektion können eine Anredefloskel und maximal ein Logo der Organisation des Autors angegeben werden. Mehrere Logos (zB wenn zusätzlich ein Akkreditierungs-Logo angegeben werden soll) sind in eine Grafikdatei zusammenzufassen.
6.2.3 Sektion Überweisungsgrund
Die optionale Sektion Überweisungsgrund enthält die vom Auftraggeber bestimmte und dem Labor übermittelte Auftrag- oder Verdachtsdiagnose oder die Fragestellung. Siehe Kapitel Überweisungsgrund.
6.2.4 Bereiche (Specialities)
Jeder CDA–Laborbefund ist laut vorliegender Headerdefinition als „Multidisciplinary Report“ ausgewiesen (vgl. Kapitel), kann jedoch mehrere unterschiedliche Teilbefunde aus verschiedenen Bereichen im Body des Dokumentes beinhalten (z.B. Hämatologie oder Bakteriologie oder beide Arten gemeinsam). D.h. diese Teilbefunde bilden die erste Gliederungsebene des Bodys - die „Bereiche“ oder - in Anlehnung an die Definitionen der „IHE“ – „Specialities“ (vgl. [3]). Die nachfolgen Abbildung zeigt die mögliche Gliederung auf der ersten Ebene innerhalb des Bodys.
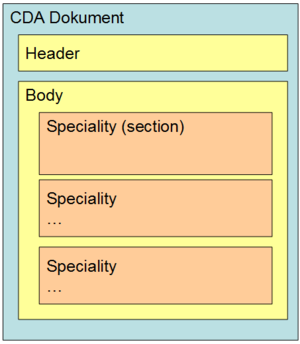
Abbildung 3: Gliederung nach Bereiche /Specialities
Die derzeit für den österreichischen Laborbefund definierten Specialities werden im Rahmen des hierarchisch organisierten Value Sets „ELGA_Laborstruktur“ definiert, wobei für Bereiche nur Einträge der Ebene 0 und 1 verwendet werden dürfen. Die nachfolgende Tabelle gibt einen auszugsweisen Überblick über die derzeit festgelegten Specialities. Die Anwendung der Bereiche ist optional. Es können auch alle Untersuchungen in einer Section unter dem Bereich „Allgemeiner Laborbefund“ zusammengefasst werden. Bei Verwendung der Bereiche ist die Reihenfolge gem. Value Set verpflichtend einzuhalten.
Für EIS „Enhanced“ ist die Codierung der Bereiche (als unterschiedliche section-Elemente) zwingend vorgeschrieben.
| Code | Bereich (Speciality) |
|---|---|
| 100 | Blutgruppenserologie |
| 200 | Blutgasanalytik |
| 300 | Hämatologie |
| 400 | Gerinnung/Hämostaseologie |
| 500 | Klinische Chemie/Proteindiagnostik |
| 600 | Hormone/Vitamine/Tumormarker |
| 900 | Toxikologie |
| 1000 | Medikamente |
| 1100 | Infektionsdiagnostik |
| 1300 | Autoimmundiagnostik |
| 1800 | Allergiediagnostik |
| 1400 | Urindiagnostik |
| 1500 | Stuhldiagnostik |
| 1600 | Liquordiagnostik |
| 2300 | Genetische Diagnostik |
| 2500 | Sonstige |
Tabelle 4: Liste der Bereiche, auszugsweise gem. ELGA Value Set „ELGA_Laborstruktur“, die sich auch in ELGA_Laborparameter widerspiegelt.
6.2.5 Gruppen (Befundgruppen)
Innerhalb dieser Bereiche erfolgt in der Regel eine Strukturierung und Gliederung der Ergebnisse zur besseren Lesbarkeit und Auffindbarkeit in „Befundgruppen“. Das ELGA Value Set „ELGA_Laborstruktur“ definiert zulässige Befundgruppen. Es besteht jedoch auch die Möglichkeit Ergebnisse ohne Befundgruppenstrukturierung zu übermitteln. Die nachfolgende Abbildung zeigt die möglichen Gliederungsarten.
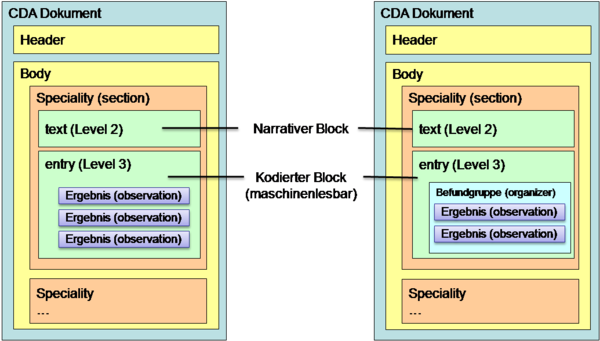
Abbildung 4: Strukturierungsmöglichkeiten Body
Die beiden nachfolgenden Abbildungen zeigen Ausschnitte aus Beispielen zu Laborbefunden mit Befundgruppen und den entsprechenden medizinischen Inhalten. Der „Allgemeine Laborbefund“ enthält die Bereiche „Hämatologie“ und „Hämostaseologie“ mit darunter liegenden Befundgruppen; der „Bakteriologische Befund“ enthält ein Bespiel für die Darstellung eines Antibiogrammes.
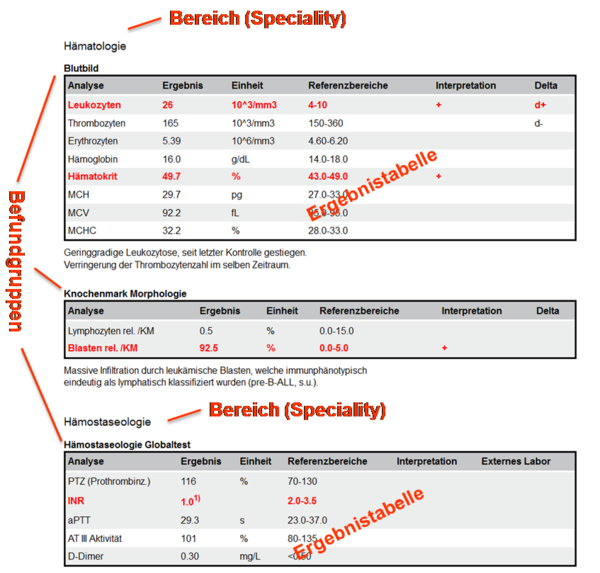
Abbildung 5: Ausschnitt Beispielbefund
Bereiche (Specialities) und Gruppen werden in CDA Level 3 in entsprechende Klassen umgesetzt und gemäß des hierarchischen Value Sets „ELGA_Laborstruktur“ codiert. Die Codierung der Bereiche erfolgt durch Elemente der ersten und zweiten Ebene (0 bzw. 1) und die der Befundgruppen durch Elemente der drittenValue Set Ebene (2). Die Reihenfolge der Bereiche bzw. Gruppen gem. Value Set ist verpflichtend einzuhalten.
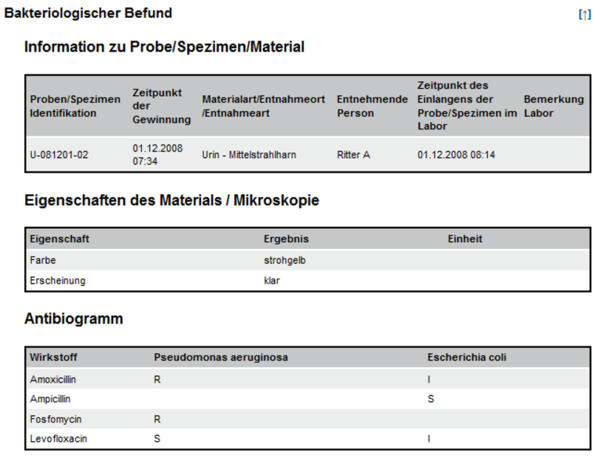
Abbildung 6: Ausschnitt Bakteriologie Beispielbefund
6.2.6 Zusätzliche medizinische Informationen
Unter Umständen ist es von Bedeutung und Interesse in dem Befund zusätzliche medizinische Informationen anzugeben. Dies betrifft z.B. die Aufnahmediagnose oder die medizinische Fragestellung bei der Auftragserteilung an das Labor. Diese Informationen können parallel zu den Befundarten als eigene Sections im CDA-Dokument angegeben werden. Die Codierung der Informationen innerhalb dieser Sections hat jedoch gemäß den Vorgaben des IHE „Patient Care Coordination“ Framework (PCC) [6] zu erfolgen!
6.2.7 Allgemeine Strukturrichtlinien für Body-Elemente
Die Gliederung eines Laborbefundes wurde bereits in Kapitel Aufbau des Body ausführlich dargestellt. Die Definitionen der Elemente werden von den Vorgaben der IHE ([3]) übernommen. Demgemäß entspricht ein Bereich einem anzugebenen Template:
<templateId root="1.3.6.1.4.1.19376.1.3.3.2.1"/>
Eine Ausnahme besteht für den Bereich (section) Probeninformation, in welchem nicht die IHE templateId „1.3.6.1.4.1.19376.1.3.3.2.1“ zu codieren ist, da diese Sektion nicht IHE konform ist.
Die nachfolgende Tabelle zeigt die abzubildenden Elemente:
| Feld | Element | Details/Codierung |
|---|---|---|
| Id | structuredBody/component/ section/id | Angabe einer Identifikation auf der Basis eines lokalen Nummernkreises |
| Code | structuredBody/component/section/code | Definition des Bereichs. Codierung nach „ELGA_Laborstruktur“ (Entsprechend der Werte der Tabelle mit Level 1). Siehe auch Tabelle 4 in 6.2.4 |
| Title | structuredBody/component/section/title | Angezeigter Titel der Befundart |
| Text | structuredBody/component/section/text | Narrativer Text (Gliederung nach den Werten der Tabelle mit Level 2) (siehe 6.3.3) |
| Entry | structuredBody/component/section/entry | Laboratory Report Data Processing Entry (siehe 6.4.3) |
Tabelle 5: Elemente einer Befundart
<component>
<section>
<templateId root="1.3.6.1.4.1.19376.1.3.3.2.1"/>
<id extension="P-body" root="2.16.840.1.113883.3.933.1.1"/>
<code code="1" codeSystem="1.2.40.0.34.5.11" codeSystemName="ELGA_LaborparameterErgaenzung" displayName="Allgemeiner Laborbefund"/>
<title>Allgemeiner Laborbefund</title>
<!-- start level 2 -->
:
<text>
</text>
<!-- start level 3 -->
<entry typeCode="DRIV">
:
</entry>
</section>
</component>
6.2.8 Narrativer Block
Jedes CDA-Dokument enthält verpflichtend einen narrativen Text (component/section/text). Die inhaltlichen Vorgaben in Bezug auf den Laborbefund betreffen die verpflichtend anzuführenden Felder, deren mögliche Ausprägungen und Grobstruktur in der die Daten im Level 2 darzustellen sind. Die Vorgaben finden sich in den nachfolgenden Kapiteln. Die Vorgaben für die Darstellung der Befunde sind in Kapitel Spezifikation der Befunddarstellung Level 2 beschrieben.
6.2.8.1 Strukturbeispiel
<!-- Start Level 2 --> <text> <paragraph styleCode="xELGA_h3">Blutbild</paragraph> <!-- Ergebnistabelle Blutbild --> <table> <thead> <tr> <th>Analyse</th> <th>Ergebnis</th> <th>Einheit</th> <th>Referenzbereiche</th> <th>Interpretation</th> <th>Delta</th> </tr> </thead> <tbody> <tr ID="OBS-1-1" styleCode="xELGA_red"> <td>Leukozyten</td> <td>26.42</td> <td>10^3/mm3</td> <td ID="OBSREF-1-1">4.4-11.3</td> <td>+</td> <td>d+</td> </tr> <tr ID="OBS-1-2"> <td>Thrombozyten</td> <td>165</td> <td>10^3/mm3</td> <td ID="OBSREF-1-2">150-360</td> <td/> <td>d-</td> </tr> </tbody> </table> <paragraph> <content ID="haematologyComment">Geringgradige Leukozytose, seit Letzter Kontrolle gestiegen. <br/> Verringerung der Thrombozytenzahl im selben Zeitraum. </content> </paragraph>
6.2.9 CDA Entry Level („Level 3“)
In den „Level 3“-konformen Teilen des Dokuments werden die maschinenlesbaren, codierten Daten zu den zuvor in Level 2 dargestellten Laborwerten abgebildet. Die erste Gruppierungsebene ist verpflichtend und stellt die Befundart (Speciality) dar. Die Abbildung der Befundarten erfolgt dabei über entsprechende component/section Strukturen. Jede dieser section-Elemente beinhaltet genau einen Entry Block, welcher genau einem spezifischen Template folgt und als „Laboratory Report Data Processing Entry“ bezeichnet wird (siehe Kapitel Laboratory Report Data Processing Entry). Das entry-Element besitzt genau ein einziges act-Element als Subelement – den sogenannten „Specimen-Act“ (siehe Kapitel Der Spezimen-Act). Das bedeutet, dass im entry-Block eines section-Elements nur ein einziges direktes Subelement abgebildet ist unter dem alle weiteren Strukturen gegliedert sind. Darunter werden unter anderem optional die Befundgruppen mittels organizer-Elementen abgebildet, welche wiederum die Einzeluntersuchungen („Observations“ observation) beinhalten. Das Codebeispiel in der nachfolgenden Abbildung zeigt die Strukturierung des Befundes aus der Abbildung "Ausschnitt Beispielbefund". Eine detaillierte Beschreibung der Strukturen erfolgt in Kapitel Spezifikation des Body Level 3.

Abbildung 7: Codefragment Beispielbefund
6.2.9.1 Ableitung Level 2 aus Level 3
Im Falle der Definition des ELGA-Labor Befundes ist eine vollständige Konstruktion des narrativen Teils des CDA-Dokuments (Level 2) aus der maschinenlesbaren, strukturierten Darstellung des Level 3 möglich! Dieses Faktum wird durch das Attribut typeCode=“DRIV“ des entry-Elementes ausgedrückt.
6.2.9.2 Referenz von Level 3 auf Level 2
In manchen Fällen ist es notwendig aus dem codierten Level 3 Teil des CDA-Dokuments auf Teile des Level 2 Teiles zu verweisen (z.B. bei Kommentaren um sich eine doppelte Angabe längerer Textpassagen zu ersparen). Dabei werden die zu referenzierenden Teile in Level 2 mit einer ID versehen (z.B. mit dem Attribute id=“refID“ im content-Element). Auf diese ID kann dann aus dem Level 3 mittels eines text-Elementes mit einem reference-Subelement (<reference value=“#refID“>) referenziert werden. Nachfolgende Beispiele zeigen eine Referenz auf einen Kommentar (siehe auch Bemerkungen/Kommentare und Spezifikation Antibiogramm) bzw. eine Referenz auf eine ganze Tabellenzeile (Analyseergebnis, siehe auch Kapitel Laborergebnisse).
… <text> … <paragraph> <content ID="haematologyComment">Geringgradige Leukozytose, seit letzter Kontrolle gestiegen. <br/>Verringerung der Thrombozytenzahl im selben Zeitraum. </content> </paragraph> … </text> <entry> … <component typeCode="COMP"> <act classCode="ACT" moodCode="EVN"> <templateId root="1.2.40.0.34.11.4.3.2"/> <templateId root="2.16.840.1.113883.10.20.1.40"/> <templateId root="1.3.6.1.4.1.19376.1.5.3.1.4.2"/> <code code="48767-8" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Annotation Comment"/> <text> <reference value="#haematologyComment"/> </text> <statusCode code="completed"/> </act> </component> … </entry> … <text> … <tbody> <tr ID="OBS-1-1"> <td>Hämoglobin</td> <td>16.0</td> <td>g/dL</td> <td ID="OBSREF-1-1">14.0-18.0</td> <td/> <td/> </tr> … </tbody> … </text> <entry> <observation classCode="OBS" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.6"/> <code code="718-7" codeSystem="2.16.840.1.113883.6.1" codeSystemName="LOINC" displayName="Hämoglobin"/> <text> <reference value="#OBS-1-1"/> </text> … </observation> … </entry> …
6.2.9.3 Dokumentenbasis
Die Umsetzung des Laborbefundes erfolgt in Anlehnung an das IHE Laboratory Technical Framework (vgl. [3]).
6.2.10 Harmonisierung des Befundaufbaus – Value Set „ELGA_Laborparameter“
Im Rahmen der Arbeiten zum vorliegenden Dokument wurde in der Expertengruppe die grundsätzliche Übereinkunft getroffen, auch die Befundgruppen und die damit verbundene Testzuordnung entsprechend österreichweit abzustimmen. Die Strukturierung eines Laborbefundes wurde in Form des hierarchischen Value Sets „ELGA_Laborparameter“ festgelegt.
Strukturierung, Reihenfolge der Parameter sowie die Bezeichnung der Parameter sind durch das Value Set ELGA Laborparameter verpflichtend vorgegeben!
Eine Hilfestellung zum Mapping der lokalen Codes auf die vorgeschriebenen Codes des Value Sets bietet der „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
6.3 Spezifikation der Befunddarstellung Level 2
6.3.1 Überblick
Die nachfolgende Tabelle gibt einen Überblick über die im lesbaren Text anzugebenden und in Level 2 (unter component/section) zu anzugebenden medizinischen Inhalte. Die Optionalität bezieht sich auf die Darstellung des jeweiligen Elements in der Tabelle. Die Befüllung ergibt sich aus den Vorgaben für Level 3 (z.B. ist die „Bemerkung Labor“ in dieser Übersicht mit [R] angegeben, d.h. das Tabellenelement ist verpflichtend anzugeben, befüllt muss es nur werden, wenn tatsächlich eine Bemerkung vorhanden ist).
Die Reihenfolge der Elemente innerhalb einer Gruppe ist zu beachten.
Die Angabe der Sektion Brieftext ist im Laborbefund ERLAUBT (Siehe Allgem. Leitfaden [4] TemplateID: 1.2.40.0.34.11.1.2.1).
| Feld | Opt | Darstellung | Details | |
|---|---|---|---|---|
| Befundbereiche | <section/title>Name des Befundbereichs</section/title>
Der Name des Befundbereichs wird in <section/title> codiert und nicht innerhalb des <section/text> Elements | |||
| <Component/section/text> Inhalt | ||||
| Allgemeine Befundinformationen | O | |||
| 1 | Auftragsdiagnose (Zuweiser-diagnose) | O [0..*] |
<paragraph> </paragraph> |
|
| 2 | Fragestellung | O [0..1] |
<paragraph> </paragraph> |
|
| 3 | Befundtext | O | < table> </ table> |
|
| Spezimeninformation | < table> pro Spezimen eine Zeile < tr> </ tr>
Sollte ein Befund aus mehreren Sections bestehen, wird die Spezimeninformation ausschließlich in einer eigenen Section angegeben und als erste Section geführt.Generell gilt, dass die Angabe von Informationen zu Proben/Spezimen/Material vorgeschrieben ist.
| |||
| 1 | Material-ID | O | <td></td> | Identifikator der Probe |
| 2 | Probenentnahme | R | <td></td> | Zeitpunkt der Probebentnahme, muss nicht angegeben werden bzw darf „unbekannt“ sein. Format: dd.MM.yyyy hh24:mi (6.4.5.3.3.4) |
| 3 | Untersuchtes Material | R | <td></td> | Materialart [R] (6.4.5.3.3.7) und Entnahmeort [O] (6.4.5.3.3.5) (Freitext ist zulässig) |
| 4 | Probenentnahme durch | O | <td></td> | Für Probenentnahme zuständige Person und ggf Organisation [O] (6.4.5.3.3.6) |
| 5 | Probeneingang | R | <td></td> | Probeneingang im Labor, Format: dd.MM.yyyy hh24:mi |
| 6 | Bemerkung Labor | R | <td></td> | Allfällige Bemerkungen zur Probenqualität sollen angegeben werden |
| Befundgruppen | <paragraph styleCode="xELGA_h3"> Name der Gruppe</paragraph> | |||
| Gruppierung / Befundgruppen (Organizer) | ||||
| Ergebnistabelle (Observations)4 | < table> je Test eine Zeile <tr></tr> | |||
| 1 | Analyse | M | <td></td> | Bezeichnung der Analyse (entsprechen dem displayName in Value Set ELGA-Laborparameter) |
| 2 | Ergebnis | M | <td></td> | Ergebnis der Analyse5, siehe 6.3.5.2 |
| 3 | Einheit | M | <td></td> | Einheit (UCUM printName), siehe 6.3.5.3 |
| 4 | Referenzbereiche | R2 | <td></td> | Mehrere Referenzbereiche können angegeben werden, getrennt durch Zeilenumbruch im Text6 |
| 5 | Interpretation | R2 | <td></td> | Codiert! Siehe 6.3.5.4 sowie Kapitel Tabelle 7 und Tabelle 8 |
| 6 | Externes Labor | R2 | <td></td> | Angabe von „E“, wenn die Analyse von einem externen Dienstleister gemessen wurde |
| Eigenschaften des Materials / Mikroskopie | < table> pro Eigenschaft eine Zeile <tr></tr> | |||
| 1 | Eigenschaft | M [1..1] |
<td></td> | |
| 2 | Ergebnis | M [1..1] |
<td></td> | |
| 3 | Einheit | O [0..1] |
<td></td> | |
| Kultureller Erregernachweis | < table> pro Erreger eine Zeile<tr></tr> | |||
| 1 | Erreger | M [1..1] |
<td></td> | |
| 2 | Methode | R2 [0..1] |
<td></td> | Mögliche Werte vgl. Tabelle 12: Beispiele für Codes für Erregernachweis-Methodik |
| 3 | Keimzahl | M [1..1] |
<td></td> | |
| Antibiogramm | < table> je Antibiotikum Zeile <tr></tr> | |||
| 1 | Name des Erregers | M [1..1] |
<th></th> | Darstellung als Spaltenüberschriften |
| 2 | Wirkstoff | M | <td></td> | Antibiotischer Wirkstoff |
| 3 | Resistenzkennung | M | <td></td> | Codiert! Siehe Tabelle 13. (Am Schnittpunkt von Erreger (Spalte) und Wirkstoff (Zeile)) |
| minimale Hemmkonzentration | < table> je Antibiotikum Zeile <tr></tr> | |||
| 1 | Name des Erregers, sowie Einheit der Konzentration | M [1..1] |
<th></th> | Darstellung als Spaltenüberschriften |
| 2 | Wirkstoff | M | <td></td> | Antibiotischer Wirkstoff |
| 3 | Konzentration | M | <td></td> | Schnittpunkt von Erreger (Spalte) und Wirkstoff (Zeile) |
| Testergebnisse / Molekularer Erregernachweis | < table> je Analyse/Erreger eine Zeile <tr></tr> | |||
| 1 | Analyse / Erreger / Methode | M [1..1] |
<td></td> | |
| 2 | Ergebnis | M | <td></td> | |
| 3 | Einheit | O [0..1] |
<td></td> | |
| 4 | Referenzbereich / Nachweisgrenze / Linearitätsbereich | O [0..1] |
<td></td> | |
| 5 | Interpretation | R2 | <td></td> | Codiert: Siehe Tabelle 7 und Tabelle 8 |
Tabelle 6: Übersicht Medizinische Inhalte Level 2
4 Spezialuntersuchungen, die nicht in das angegebene Schema passen (z.B Molekulare Diagnostik, Allergiediagnostik etc.), können bei Bedarf auch anders dargestellt werden. Ensprechende Beispieldokumente stehen zur Verfügung.
5 Es wird EMPFOHLEN, bei Dezimalzahlen einen Punkt als Dezimaltrennzeichen zu verwenden – gleich wie im maschinenlesbaren Teil.
6 Es wird EMPFOHLEN, bei Dezimalzahlen einen Punkt als Dezimaltrennzeichen zu verwenden – gleich wie im maschinenlesbaren Teil
6.3.2 Formatierung von Datums- und Zeitangaben
Datums- und Zeitangaben sind im lesbaren Teil im Format „dd.MM.yyyy“ bzw. „dd.MM.yyyy hh24:mi“ anzugeben. Dabei gilt:
| dd | Tag |
| MM | Monat als zweistellige Zahl |
| yyyy | Jahr |
| hh24 | Stunden im 24 Stunden Format |
| mi | Minuten |
6.3.3 Level 2 Befundstruktur
Bei der Darstellung der Befunde ist die Struktur gemäß der nachfolgenden Abbildung verpflichtend abzubilden.
| Spezimen Bereich | Spezimen Section: enthält Tabelle mit Spezimen in <text> | ||
| Befundbereich (Section) | Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| Befundgruppe | Befundgruppenbezeichnung | ||
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| .. | .. | ||
| Befundbereich (Section) | Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| Befundgruppe | Befundgruppenbezeichnung | ||
| Ergebnistabelle Befundgruppe | |||
| Bemerkung zur Befundgruppe | |||
| .. | .. | ||
| .. | ... | ||
| Befund Bemerkung Bereich | Befundbemerkung Section enthält: Bemerkung zu Befund in <text> | ||
Abbildung 8: Befundstruktur Level 2 mit mehreren Sections
Enthält ein Befund nur genau einen Bereich (Section) kann eine vereinfachte Darstellung mit folgender Befundstruktur verwendet werden:
| Tabelle mit Spezimen | ||
| Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | ||
| Bemerkung zur Befundgruppe | ||
| Befundgruppe | Befundgruppenbezeichnung | |
| Ergebnistabelle Befundgruppe | ||
| Bemerkung zur Befundgruppe | ||
| ... | ... | |
| Bemerkung zur Befundart | ||
Abbildung 9: Befundstruktur Level 2 mit einer Section
6.3.4 Probeninformation
Der Inhalt dieser Sektion enthält sämtliche Information über das zu befundende Material, inklusive, soweit sinnvoll, der Lokalisation, der Entnahmeart, des Entnahmegeräts, der Person, welche die Entnahme durchgeführt hat, sowie Zeitpunkt der Materialentnahme und der Materialannahme.
Abbildung 10: Probeninformation, vollständig.
Abbildung 11: Probeninformation, minimal.
Menschenlesbare Informationen zum Spezimen MÜSSEN angegeben werden, wenn bekannt.
In dem folgenden Strukturbeispiel ist die Codierung der Informationen in einer Tabelle ersichtlich. Die einzelnen Zeilen, welche jeweils ein Spezimen codieren, können mit Identifikatoren gekennzeichnet werden um auf diese im weiteren CDA Befund referenzieren zu können. Die Optimierung der Spaltenbreiten kann im ELGA Referenz-Stylesheet durch die ELGA-Stylecodes „xELGA_colw:nn“ erfolgen.
Die Abbildung der Spezimeninformation kann auf zwei Arten erfolgen:
- Enthält ein Befund nur einen Bereich, so kann die Codierung gemäß IHE LAB TF-3 innerhalb der einen Befundsektion erfolgen
ODER
- Bei Verwendung von mehreren Bereichen (vgl. Anforderung) in einem Laborbefund kann es zu Überschneidungen der Spezimeninformationen kommen (ein spezielles Spezimen kann in zwei Bereichen analysiert werden). Die Level 3 Codierung eines Spezimens darf jedoch nur einmal im gesamten Laborbefund erfolgen. Daher sind die Informationen zu den Spezimen in einer eigenen führenden Probeninformation Section mit dem Code „10“ und der TemplateID 1.2.40.0.34.11.4.2.1 zu codieren.
| Id | 1.2.40.0.34.11.4.2.1 ref elgabbr- | Gültigkeit ab | 2013‑11‑07 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpezimenSection | Bezeichnung | Spezimen-Section | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.1 Spezimen-Section (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.3.5 Vorgaben zur Darstellung einzelner Elemente
6.3.5.1 Analysen
Analysen (bzw Laborwerte, Laborleistungen oder Labormessgrößen) MÜSSEN in der einheitlichen Schreibweise angegeben sein, die im Value Set „ELGA_Laborparameter“ vorgegeben wird („Begriff“ bzw „display name“ im Value Set). Das erleichtert das Lesen und speziell für Patienten die Recherche von Laborwerten im Gesundheitsportal (www.gesundheit.gv.at). Siehe dazu auch den „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
Ein Beispiel zur Darstellung findet sich in Abbildung 12. Die Tabelle besteht aus mindestens fünf und maximal sechs Spalten. Für jede Gruppe wird ein Block angelegt, Bereichsüberschriften entsprechen Kapitelüberschriften. Zusätzlich kann eine Spalte mit „Extenes Labor“ notwendig sein. Sollen genauere Angaben zur Methode gemacht werden, als durch den Namen der Analysen bereits hervorgeht, soll dies über einen Analysenkommentar umgesetzt werden (siehe 6.3.8.1).
Abbildung 12: Beispiel einer ausführlichen Laborwerte-Ergebnistabelle
6.3.5.2 Ergebnis
Dieses Element enthält ein numerisches, nominales, ordinales oder narratives Ergebnis der Analyse zu diesem Testcode. Da in der Definition des CDA-Schemas keinerlei Längenbeschränkung vorgegeben ist, kann dieses Feld auch größere Textmengen fassen um große verbale Beurteilungen zu ermöglichen.
6.3.5.3 Einheit
Zu jedem Ergebnis MUSS eine passende Einheit angegeben werden. Bevorzugt zu verwenden sind die Einheiten, die im Value Set „ELGA_Laborparameter“ vorgeschlagen werden.
Es wird EMPFOHLEN, anstelle von Einheitenpräfixen („Giga“, „Mega“, „Milli“, „Mikro“ etc.) eine Potenzschreibweise zu wählen, vor allem, wenn die Groß/Klein-Schreibung eine Rolle spielt und Verwechslungen möglich sind (z.B. „G/L“=Giga pro Liter vs. „g/L“=Gramm/Liter). Also '10^6 ' statt 'M' (Mega), '10^9 ' statt 'G ' (Giga) usw.
6.3.5.4 Befundinterpretation
Es ist in Laborbefunden üblich, eine codierte Bewertung zu jedem Ergebnis anzugeben. Häufig wird eine Notierung mit +/- verwendet.
Folgende Tabelle 7 ist ein Auszug aus dem Value Set „ELGA_ObservationInterpretation“ und zeigt die normative Befundinterpretation für numerische Ergebnisse, Tabelle 8 (ebenfalls aus dem gleichen Value Set) die Kennzeichnung für nicht numerische Ergebnisse.
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| ++ | HH | Oberhalb des Referenzbereiches und über einer oberen Warngrenze |
| + | H | Oberhalb des Referenzbereiches |
| N | Normal (innerhalb des Referenzbereiches) | |
| - | L | Unterhalb des Referenzbereiches |
| -- | LL | Unterhalb des Referenzbereiches und unter einer unteren Warngrenze |
Tabelle 7: Befundinterpretation numerischer Ergebnisse
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| N | Normal (innerhalb des Referenzbereiches) | |
| * | A | Abnormal |
| ** | AA | Abnormal Warngrenze |
Tabelle 8: Befundinterpretation nicht numerischer Ergebnisse (nominal, ordinal, narrativ)
Zur Interpretation von Ergebnissen der Allergiediagnostik wurden zusätzlich RAST-Klassen als Klassifikation erlaubt, siehe Kapitel Empfehlungen für die Darstellung der Allergiediagnostik.
6.3.5.5 Empfehlungen für die Darstellung der Allergiediagnostik
In der Allergiediagnostik gibt es gegebenenfalls Abweichungen zur normalen Struktur des Laborbefundes. Die Angabe der getesteten Allergene bei Globalmarkern oder die zusätzliche Angabe von RAST-Klassen machen eine alternative Darstellung notwendig.
Folgende Darstellung wird dazu EMPFOHLEN:

Abbildung 13: Empfohlene Darstellung von Globalmarkern und Angabe der RAST-Klasse als Interpretation eines numerischen Ergebnisses. Sofern die RAST-Klasse angegeben wird, ist Option 3 empfohlen.
Folgendes Codebeispiel zeigt die Befunddarstellung der Globalmarker im narrativen Text:
<table>
<thead>
<tr>
<th styleCode="xELGA_colw:80">Analyse</th>
<th styleCode="xELGA_colw:10">Ergebnis</th>
<th styleCode="xELGA_colw:10">Interpretation</th>
</tr>
</thead>
<tbody>
<tr ID="OBS-1-1">
<td>sx1 Inhalatives Screening<br/>
<content styleCode="italics">Lieschgras, Roggen, Birke, Beifuß, Dermatophagoides pteronyssinus,
Katzenschuppen, Hundeschuppen, Cladosporium herbarum</content>
</td>
<td>negativ</td>
<td></td>
</tr>
<tr ID="OBS-1-2" styleCode="xELGA_red">
<td>mx1 Schimmelpilzemix 1<br/>
<content styleCode="italics">Alternaria alternata, Aspergillus fumigatus, Cladosporium herbarum,
Penicillium notatum</content></td>
<td>positiv</td>
<td>A</td>
</tr>
</tbody>
</table>
6.3.6 Stylecodes
Für die spezifische grafische Darstellung und bessere optische Aufbereitung stehen verschiedene definierte Stylecodes zur Verfügung. Tabelle 9 zeigt einen Überblick.
| Stylecode | Primäre Verwendung in Element | Nutzung |
|---|---|---|
| xELGA_h1 | <paragraph> | Überschriften gem. HTML < h1> |
| xELGA_h2 | <paragraph> | Überschriften gem. HTML < h2> |
| xELGA_h3 | <paragraph> | Überschriften gem. HTML < h3> |
| xELGA_red | <tr> | Kennzeichnung pathologischer Messwerte (ganze Ergebniszeile) |
Tabelle 9: Level 2 Stylecodes
6.3.7 Bemerkungen/Kommentare
Es gibt vier Arten von Bemerkungen:
- zu einem einzelnen Analyseergebnis
- zu einer Befundgruppe
- zu einem Bereich
- zum gesamten Befund, über alle Bereiche
6.3.7.1 Bemerkungen zu Analysen oder Analyseergebnissen
Existiert zu einer Analyse oder einem Analyseergebnis eine Bemerkung (z.B. um die Analyse oder das Ergebnis näher zu beschreiben), so wird die Analyse oder das Ergebnis mit einer Fußnotenreferenz versehen und die eigentliche Bemerkung im Footer der Ergebnistabelle dargestellt.
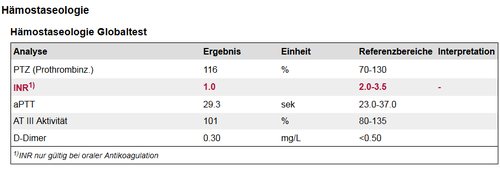
Abbildung 14: Darstellung einer Bemerkung zu einer Analyse
Die Fußnotenreferenzen werden fortlaufend nummeriert und durch einen sup-Tag hochgestellt. Der Text wird unter tfoot-Element mit dem footnote-Tag gekennzeichnet. Die ID gibt eine eindeutige Referenz auf den Text einer Fußnote.
<table>
<thead>
...
</thead>
<tfoot>
<tr>
<td>
<footnote ID="fn1">
<sup>1)</sup>INR nur gültig bei oraler Antikoagulation
</footnote>
</td>
</tr>
</tfoot>
<tbody>
...
<tr ID="OBS-2-2" styleCode="xELGA_red">
<td>INR<sup>1)</sup></td>
<td>1.0</td>
<td></td>
<td ID="OBSREF-2-2">2.0-3.5</td>
<td>-</td>
</tr>
...
<tbody>
</table>
6.3.7.2 Bemerkungen zu Befundgruppen
Bemerkungen zu Befundgruppen werden als eigener Absatz (paragraph-Element) nach der entsprechenden Ergebnistabelle codiert. Um den Text der Bemerkung aus Level 3 referenzierbar zu machen, MUSS dieser von einem content-Tag mit einer eindeutigen ID eingeschlossen werden (vgl. Kapitel Referenz von Level 3 auf Level 2).
<!-- Befundgruppe Blutbild --> <caption styleCode="xELGA_h2">Blutbild</caption> <table> ... </table> <paragraph> <content ID="BB_Comment">Das ist eine Bemerkung für die Gruppe Blutbild</content> </paragraph>
6.3.7.3 Bemerkungen zu einem Befundbereich
Bemerkungen zu einer Befundart werden am Ende der Codierung des Befundbereichs(Speciality) als Tabelle codiert. Um den Text der Bemerkung aus Level 3 referenzierbar zu machen, MUSS dieser von einem content-Tag mit einer eindeutigen ID eingeschlossen werden (vgl. Referenz von Level 3 auf Level 2).
<table>
<thead>
<tr>
<th>Befundbewertung</th>
</tr>
</thead>
<tbody>
<tr>
<td><paragraph><content ID="commonComment1">Das ist die Bewertung für den
"Allgemeinen Laborbefund". Diese kann auch sehr lange ausfallen.
</content></paragraph>
</td>
</tr>
</tbody>
</table>
6.3.7.4 Bemerkung zum gesamten Befund über alle Bereiche
Bemerkungen oder Kommentare, welche für den gesamten Befund von Bedeutung sind, werden in einer eigenen Sektion am Befundende geführt. Der menschenlesbare Text im <text> Element ist mit einer ID zu versehen, um auf diesen Text im Level 3 entry-Element referenzieren zu können. Die Spezifikation dieses Elements ist in Kapitel Bereichsübergreifende Befundbewertung ersichtlich.
6.3.8 Eigenschaften des Materials/Mikroskopie

Abbildung 16: Eigenschaften des Materials/Mikroskopie
Die Tabellendarstellung zeigt eine Eigenschaft des zu untersuchenden Materials mit dem zugehörigen Ergebnis sowie, wenn anwendbar, einer physikalischen Einheit.
6.3.8.1 Spezifikation
| Id | 1.2.40.0.34.11.4.2.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | MikroskopieSektion | Bezeichnung | Sektion Mikroskopie | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Eigenschaften des Materials/Mikroskopie | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.3 Sektion Mikroskopie (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.3.9 Kultureller Erregernachweis
Der Erregernachweis enthält Ergebnisse, welche mit Hilfe von Kulturen erlangt werden, und repräsentiert diese als Tabelle. Jede Zeile dieser Tabelle enthält die Bezeichnung des Erregers, die Methodik der Untersuchungsdurchführung sowie die Keimzahl. Vorgeschlagene Methodiken wären zum Beispiel:
- Kultur (nach Bedarf anaerob/aerob)
- Pilzkultur
- …
Sollte kein Erreger nachweisbar sein (ggf. aber apathogene Keime), wird folgende Formulierung EMPFOHLEN: „Erreger nicht nachweisbar“.
Sollten gar keine Keime (oder Mikroorganismen) nachweisbar sein, wird wird folgende Formulierung EMPFOHLEN: „Keime (oder Mikroorganismen) nicht nachweisbar“.
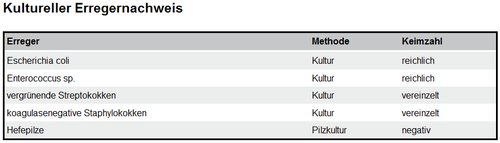
Abbildung 17: Kultureller Erregernachweis
6.3.9.1 Strukturbeispiel
:
<title>Kultureller Erregernachweis</title>
<text>
<table>
<thead>
<tr>
<th>Erreger</th>
<th>Methode</th>
<th>Keimzahl</th>
</tr>
</thead>
<tbody>
<tr ID="OBS-2-3">
<td>Escherichia coli</td>
<td>Kultur</td>
<td>reichlich</td>
</tr>
<tr ID="OBS-2-4">
<td>Enterococcus sp.</td>
<td>Kultur</td>
<td>reichlich</td>
</tr>
:
</tbody>
</table>
:
</text>
6.3.10 Antibiogramm
Das Antibiogramm wird bei Vorliegen von mehreren Antibiogrammen im Befund als Matrix dargestellt. Falls die Matrixdarstellung bei zu vielen Antibiogrammen zu unübersichtlich wird, können die einzelnen Antibiogramme jeweils als dem Erreger nachgereihte Tabelle angegeben werden. Die folgende Abbildung zeigt ein Beispiel mit zwei Erregern als Matrixdarstellung.
6.3.10.1 Strukturbeispiel
<table> <thead> <tr> <th>Wirkstoff</th> <th>Pseudomonas aeruginosa</th> <th>Escherichia coli</th> </tr> </thead> <tbody> <tr ID="AB-1-1"> <td>Amoxicillin</td> <td>R</td> <td>I</td> </tr> <tr ID="AB-2-1"> <td>Ampicillin</td> <td></td> <td>S</td> </tr> <tr ID="AB-3-1"> <td>Fosfomycin</td> <td>R</td> <td></td> </tr> </tbody> </table>
6.3.11 Minimale Hemmkonzentration
Die minimale Hemmkonzentration (MHK) wird im Befund als Matrix angezeigt. Die folgende Abbildung zeigt ein Beispiel für die Bildschirmdarstellung der minimalen Hemmkonzentration.

Abbildung 19: Minimale Hemmkonzentration
6.3.11.1 Strukturbeispiel
<table> <thead> <tr> <th>Wirkstoff</th> <th>Pseudomonas aeruginosa<br/>Abs.Wert[ug/mL]</th> <th>Escherichia coli<br/>Abs.Wert[ug/mL]</th> </tr> </thead> <tbody> <tr ID="MIC-1-1"> <td>Amoxicillin</td> <td>4</td> <td>2</td> </tr> <tr ID="MIC-2-1"> <td>Ampicillin</td> <td></td> <td>0.5</td> </tr> <tr ID="MIC-3-1"> <td>Fosfomycin</td> <td>16</td> <td></td> </tr> <tr ID="MIC-4-1"> <td>Levofloxacin</td> <td>0.25</td> <td>4</td> </tr> </tbody> </table>
6.3.12 Testergebnisse/Molekularer Erregernachweis
Die Ergebnisse werden in einer Tabelle angeführt, welche strukturell einer Ergebnistabelle ähnelt. Abbildung 20 zeigt ein Beispiel der Tabellenstruktur. In die Spalte „Analyse/Erreger/Methode“ wird der Erreger eingetragen, sowie die Methodik vermerkt, mit der der Erreger untersucht wurde. Das Value Set „ELGA_Laborparameter“ definiert gültige Bezeichnungen für die Spalte „Analyse/Erreger/Methode“. Die Umsetzung erfolgt analog zur Level 2 Befundstruktur (siehe Kapitel Level 2 Befundstruktur).
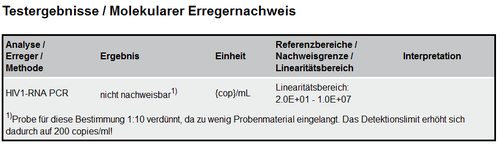
Abbildung 20: Testergebnisse/Molekularer Erregernachweis
6.3.13 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012
Die Vorgaben dieses Implementierungsleitfadens erlauben die Erzeugung von Befunden gemäß ISO 15189:2012 "Medizinische Laboratorien - Anforderungen an die Qualität und Kompetenz" [10], speziell in Hinblick auf die dort angegebenen Kapitel 5.8 (Befundberichte) und 5.9 (Freigabe der Ergebnisse). Für akkreditierte Laboratorien sind neben [10] folgende Hinweise zu beachten:
6.3.14 Angabe des Akkreditierungs-Logos
Das Akkreditierungs-Logo kann neben dem Logo des Labors angegeben werden. Technisch erfolgt das über die Section Brieftext, das Logo ist ggf. gemeinsam mit dem Logo des Labors in einer Grafikdatei anzugeben (6.2.2).

Abbildung 21: Angabe des Akkreditierungs-Logos im Briefkopf
Ein Labor muss nicht zwingend für alle Analysen, die es durchführen kann, akkreditiert sein. Das Akkreditierungs-Logo kann angegeben werden, sobald es akkreditierte Analysen gibt; wenn „nicht akkreditierte Analysen“ am Befund erscheinen, soll bei diesen angegeben werden können, dass das Labor für diese Analyse nicht akkreditiert ist. Für die entsprechend Markierung wird die Verwendung von Anmerkungszeichen (wie z.B. *) und Endnoten empfohlen.
6.3.15 Angabe des Untersuchungs- bzw Messverfahrens
Wenn der Name der Analysen keinen Rückschluss auf die Methode erlaubt, aber Untersuchungs- bzw Messverfahren dennoch angegeben werden sollen ([10], Vorgabe 5.8.3 a)), soll dies als Kommentar zur Analyse erfolgen (siehe Bemerkungen zu Analysen oder Analyseergebnissen).
6.3.16 Vorgaben für den Befunddruck
Einige Vorgaben von ISO 15189:2012 beziehen sich auf Qualitätsmerkmale für gedruckte Befunde ([10], Vorgabe 5.8.3 d „Identifizierung des Patienten und den Aufenthaltsort des Patienten auf jeder Seite“ und Vorgabe 5.8.3 p „Seitenzahl zur Gesamtzahl der Seiten“). Dieser Leitfaden definiert ein elektronisches Format, das diese Anforderungen grundsätzlich unterstützt. Am ELGA-Portal (Zugriff für Bürger) werden Tools zur Darstellung eingesetzt, die diese Vorgaben unterstützen. Diese Tools werden auch von der ELGA GmbH zum Download bereigestellt (Referenzstylesheet, CDA2PDF auf http://www.elga.gv.at/CDA).
6.4 Spezifikation des Body Level 3
6.4.1 Überblick
| Feld | Opt | Darstellung | Details |
|---|---|---|---|
| Allgemeine Befundinformationen | |||
| Auftragsdiagnose und Fragestellung | ClinicalDocument/component/structuredBody/component/section/.. | O [0..*] |
Link |
| Spezimeninformation | |||
| Abnahmeinformationen (Specimen Collection) | ../entry/act/entryRelationship/procedure <template root=”1.3.6.1.4.1.19376.1.3.1.2”> | R2 [0..*] |
Link |
| Annahmeinformationen (Specimen Received) | ../entry/act/entryRelationship/procedure/entryRelationship/act <template root=”1.3.6.1.4.1.19376.1.3.1.3”> | R2 [0..*] |
Link |
| Befundgruppen | |||
| Befundgruppen (Laboratory Battery Organizer) | ../entry/act/entryRelationship/organizer | O [0..*] |
Link |
| Laborergebnisse (Laboratory Observation) | ../entry/act/entryRelationship/organizer/component/observation/ <templateId root="1.3.6.1.4.1.19376.1.3.1.6"> | ||
| Analyse: Identifikation/Codierung | ../id und ../code | M [1..1] |
Link |
| Ergebnis und Einheit | ../value | M [1..1] |
Link |
| Referenzbereiche | ../referenceRange | R2 [0..*] |
Link |
| Befundinterpretation | ../interpretationCode | R2 [0..*] |
Link |
| Kommentar zu einer Analyse | ../entryRelationship/act | 0 [0..1] |
Link |
| Externes Labor | ../performer | C [0..1] |
Link |
| Kultureller Erregernachweis | ../entry/act/entryRelationship/organizer | ||
| Erregernachweis mit Definition der Methodik | ../component/observation | R2 [0..*] |
Link |
| Antibiogramm und minimale Hemmkonzentration | ../entry/act/entryRelationship/organizer | ||
| Antibiogramm und minimale Hemmkonzentration | ../component/organizer | R2 [0..*] |
Link, Link |
| Testergebnisse / Molekularer Erregernachweis | ../entry/act/entryRelationship/organizer | ||
| Testergebnisse und Molekularer Erregernachweis | ../component/observation | R2 [0..*] |
Link |
| Significant Pathogens | ../entry/act/entryRelationship/organizer | ||
| Significant Pathogens | ../component/organizer | C [0..1] |
Link |
6.4.2 Überweisungsgrund
Der Überweisungsgrund enthält die dem Labor übermittelte Auftrags- oder Verdachtsdiagnose bzw. Fragestellung.Die Angabe erfolgt in einer Section im Body des CDA-Dokuments.
6.4.2.1 Überblick
| EIS „Enhanced“ und „Full Support“ | |
|---|---|
| Template ID | ELGA: 1.2.40.0.34.11.4.2.4 |
| Parent Template ID | - |
| Titel der Sektion | Überweisungsgrund |
| Definition | Der Grund für eine Gesundheitsdienstleistung (hier: Laborbefund). Enthält eine narrative Beschreibung des Grundes für den Auftrag (Beschreibung aus der Sicht des Gesundheitsdiensteanbieters) und/oder die eigene Beschreibung des Patienten (z.B. Hauptsymptom des Patienten) |
| Codierung | LOINC: 46239-0, „Chief complaint+Reason for visit“ |
| Konformität | [O] |
| Konformität Level 3 | [NP] |
6.4.2.2 Spezifikation
| Id | 1.2.40.0.34.11.4.2.4 ref elgabbr- | Gültigkeit ab | 2015‑09‑24 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Ueberweisungsgrund | Bezeichnung | Überweisungsgrund | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.4 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.4 Überweisungsgrund (2015‑09‑24) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.3 Laboratory Report Data Processing Entry
Die Angabe eines entry-Eintrages im Rahmen der Codierung einer Befundart ist Pflicht. Dieses Element wird gem. [3] als „Laboratory Report Data Processing Entry“ bezeichnet und folgt einem spezifischen Template.
<templateId root="1.3.6.1.4.1.19376.1.3.1" extension="Lab.Report.Data.Processing.Entry"/>
Der entry-Eintrag ist mit dem Attribute typeCode=“DRIV“ zu versehen, um anzuzeigen, dass der Level 2 vollständig aus dem Level 3 erzeugt werden kann.
Das entry-Element enthält genau ein act-Subelement – den sogenannten „Spezimen-Act“.
6.4.4 Der Spezimen-Act
Wie bereits in Kapitel CDA Entry Level („Level 3“) angeführt, erfolgt die Codierung der Ergebnisse zu einer Befundart immer auf oberster Ebene unter genau einem act-Element – dem „Spezimen–Act“. Damit befindet sich unter dem component/section/entry-Element immer genau ein Unterelement. Alle weiteren Elemente - sowohl Spezimen als auch Befundgruppen, Untersuchungen etc. - werden in der Hierarchie unter dem Spezimen-Act codiert. Der Act MUSS zumindest eine Untersuchung beinhalten.
6.4.4.1 Spezifikation
| Id | 1.2.40.0.34.11.30020 ref elgabbr- | Gültigkeit ab | 2017‑02‑22 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpezimenActEntryAllgemein | Bezeichnung | ELGA Spezimen-Act-Entry Allgemein | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30020 ELGA Spezimen-Act-Entry Allgemein (2017‑02‑22) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.5 Probeninformationen (Specimen-Section)
6.4.5.1 Überblick
In der aktuellen Version des „Laboratory Technical Framework Volume 3 – Revision 3.0“ (LAB TF-3) wurde die Vorgangsweise zur Codierung des Spezimen grundlegend geändert. Die zum Teil noch verbreitete Variante der Spezimen-Codierung laut „Laboratory Technical Framework Volume 3 – Revision 2.1“ sah vor, dass man ein oder mehrere Specimen/Proben mittels des specimen-Elementes innerhalb des Specimen-Act codieren konnte. In Version 3.0 des LAB TF-3 kann ein Spezimen/Probe nur über ein entryRelationship als Specimen-Collection angegeben werden.
Die Codierung von Informationen zum Spezimen ist für Befunde der ELGA Interoperabilitäts Stufe „Full support“ verpflichtend. Diese Codierung erfolgt bei Befunden, welche aus mehreren Bereichen bestehen in einer eigenen Sektion „Probeninformation“. Bei Befunden, welche nur aus einer Sektion bestehen kann die Codierung der Information zum Spezimen auch in dieser Sektion geschehen.
6.4.5.2 Spezimen-Section
6.4.5.2.1 Spezifikation
Specimen Section
| Id | 1.2.40.0.34.11.4.2.1 ref elgabbr- | Gültigkeit ab | 2013‑11‑07 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpezimenSection | Bezeichnung | Spezimen-Section | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.1 Spezimen-Section (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Specimen Entry
| Id | 1.2.40.0.34.11.4.3.1 ref elgabbr- | Gültigkeit ab | 2013‑02‑10 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratorySpecimenEntry | Bezeichnung | Laboratory Specimen Entry | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.5.3 Abnahmeinformationen (Specimen Collection)
6.4.5.3.1 Überblick
Abnahmeinformationen werden analog zu den Vorgaben der IHE ([3]) als „Specimen Collection“ Block unter dem Spezimen-Act codiert. Die Darstellung erfolgt über ein act-Element, welches über eine entryRelationship Verbindung mit dem Spezimen-Act verbunden ist (../entry/act/entryRelationship/act).
6.4.5.3.2 Spezifikation
| Id | 1.2.40.0.34.11.30021 ref elgabbr- | Gültigkeit ab | 2014‑03‑04 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpecimenCollection | Bezeichnung | Abnahmeinformationen (Specimen Collection) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30021 Abnahmeinformationen (Specimen Collection) (2014‑03‑04) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.5.4 Annahmeinformationen (Specimen Received)
6.4.5.4.1 Überblick
Informationen zur Probenannahme werden analog zu den Vorgaben der IHE ([3]) als „Specimen Received“ Block unter dem Spezimen-Act codiert. Die Darstellung erfolgt über ein act-Element, welches über eine entryRelationship Verbindung mit dem Spezimen-Act verbunden ist (../entry/act/entryRelationship/act).
6.4.5.4.2 Spezifikation
| Id | 1.2.40.0.34.11.30022 ref elgabbr- | Gültigkeit ab | 2014‑03‑04 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | SpecimenReceived | Bezeichnung | Annahmeinformationen (Specimen Received) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30022 Annahmeinformationen (Specimen Received) (2014‑03‑04) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.5.4.3 Allgemeine Anmerkungen des Labors zur Spezimenqualität
Anmerkungen zur Spezimenqualität werden als Annotation-Act unter dem act-Element über eine Verknüpfung durch ein entryRelationship-Element implementiert (vgl. Kommentar zu einer Analyse).
6.4.6 Befundgruppen (Laboratory Battery Organizer)
6.4.6.1 Überblick
Innerhalb einer Befundart kann auf zweiter Ebene die Strukturierung nach Befundgruppen erfolgen. Diese werden in Form von Laboratory Battery Organizer (vgl. [3]), welche eine Gruppierung von Ergebnissen ermöglichen, dargestellt. Die Implementierung erfolgt über einen organizer, welcher mittels entryRelationship mit dem Spezimen-Act verbunden ist. Die Struktur entspricht einem Template, welches verpflichtend anzugeben ist.
<templateId root="1.3.6.1.4.1.19376.1.3.1.4"/>
Die Untersuchungsergebnisse werden als component unter dem Organizer abgebildet.
Für die Codierung des code-Elementes sind Codes der Ebene 2 der hierarchischen Liste „ELGA_Laborstruktur“ zu verwenden.
6.4.6.2 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.1.4 ref elgabbr- | Gültigkeit ab | 2017‑02‑23 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryBatteryOrganizer | Bezeichnung | Befundgruppen (Laboratory Battery Organizer) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.4 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.4 Befundgruppen (Laboratory Battery Organizer) (2017‑02‑23) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.6.2.1 Laborergebnis
| Id | 1.3.6.1.4.1.19376.1.3.1.6 ref elgabbr- | Gültigkeit ab | 2020‑06‑15 08:50:28 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryObservation | Bezeichnung | Laborergebnisse (Laboratory Observation) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.6 Laborergebnisse (Laboratory Observation) (2015‑03‑26) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.6.2.2 Befundtext (Anmerkungen und Kommentare)
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.7 Laborergebnisse (Laboratory Observation)
6.4.7.1 Überblick
Ergebnisse einer Laboruntersuchung werden als observation-Block codiert. Jede Observation stellt das Ergebnis zu genau einer Laboruntersuchung dar; entweder als Einzeluntersuchung direkt unter dem Spezimen-Act oder als Teil einer Befundgruppe (Laboratory Battery Organizer). Dies entspricht einem spezifischen Template welches verpflichtend als Element anzuführen ist.
<templateId root="1.3.6.1.4.1.19376.1.3.1.6"/>
6.4.7.2 Spezifikation
| Id | 1.3.6.1.4.1.19376.1.3.1.6 ref elgabbr- | Gültigkeit ab | 2020‑06‑15 08:50:28 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryObservation | Bezeichnung | Laborergebnisse (Laboratory Observation) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.6 Laborergebnisse (Laboratory Observation) (2015‑03‑26) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.7.2.1 Durchführende Instanz / externes Labor (observation/performer)
| Id | 1.2.40.0.34.11.4.3.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryPerformer2 | Bezeichnung | Laboratory Performer 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Element zur Kennzeichnung einer Analyse, die in einem externen Labor durchgeführt wurde. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.3 Laboratory Performer 2 (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.7.2.2 EntryRelationship (observation/entryRelationship)
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.7.3 Analyse: Identifikation/Codierung
Die Angabe der Laboruntersuchungen (Analyse, Test) hat prinzipiell codiert zu erfolgen. Das entsprechende Element ist das code-Element (das id-Feld stellt eine interne Codierung dar und ist optional). Siehe dazu auch den „Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund“ [9].
6.4.7.3.1 Strukturbeispiel
<id extension="OBS-1-3" root="2.16.840.1.113883.2.16.1.99.3.1"/> <code code="26453-1" codeSystem="2.16.840.1.113883.6.1!" codeSystemName="LOINC" displayName="Erythrozyten"/>
6.4.7.3.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| code | CE CWE |
0..1 | C | Codierung der Analyse / des Tests | |
| Konditionale Konformität: EIS „Enhanced“ EIS „Basic“ |
1..1 0..1 |
R O |
Ein maschinenlesbares Element. NullFlavor siehe 6.4.7.4.3 Maschinenlesbares Element optional Ist kein Code für eine zu codierende Analyse verfügbar, ist laut Kapitel Laborergebnisse ohne passenden Code vorzugehen. | ||
| @code | cs | 1..1 | M | Code aus Value Set ELGA_Laborparameter | |
| @displayName | st | 0..1 | R2 | Displayname des Code-Werts aus dem Value Set ELGA_Laborparameter | |
| @codeSystem | uid | 1..1 | M | Parent-OID aus Value Set ELGA_LaborParameter (1.2.40.0.34.10.44) | |
| @codeSystemName | st | 0..1 | R2 | Parent-Codesystemname aus Value Set ELGA_LaborParameter | |
6.4.7.3.3 Laborergebnisse ohne passenden Code
Sollte in dem Value Set „ELGA_Laborparameter“ kein Code für die Laboranalyse verfügbar sein, kann die Analyse dennoch maschinenlesbar hinterlegt werden mit der Kennzeichnung, dass der Wert nicht aus dem Value Set stammt. Das gilt auch für den Fall, dass ein passender LOINC Code exisitiert, aber nicht im aktuellen Value Set „ELGA_Laborparameter“ enthalten ist.Es wird gebeten, dass benötigte Codes umgehend an ELGA gemeldet werden um diese im Zuge von Reviewzyklen in die Codelisten und Value Sets einzupflegen.
Für die Befunddarstellung solcher Analysen wird empfohlen, dass diese jeweils am Ende der thematisch passendsten Gruppe einzureihen sind, solange es noch keine andere Vorgabe oder Empfehlung gibt.
6.4.7.3.3.1 Strukturbeispiel
<id extension="OBS-1-3" root="2.16.840.1.113883.2.16.1.99.3.1"/> <code nullFlavor="OTH"> <translation code="alternativerCode" codeSystem="alternativeCodeSystem" displayName="klarTextDarstellung" codeSystemName="NameDesCodeSystems"/> </code>
6.4.7.3.3.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |||
|---|---|---|---|---|---|---|---|
| code | CE CWE |
1..1 | C | ||||
| Konditionale Konformität:Anzugeben wenn im Value Set „ELGA_Laborparameter“ kein passender Code für die Laboranalyse verfügbar ist. | |||||||
| @nullFlavor | cs | 1..1 | M | Fester Wert: OTH | |||
| translation | CE CWE |
1..1 | M | Codierung der Analyse in einem alternativen Codesystem
Die Verwendung von LOINC Codes wird empfohlen. | |||
| @code | cs | 1..1 | M | Code aus einem alternativen Codesystem | |||
| @codeSystem | uid | 1..1 | M | Identifikation des alternativen Codesystems | |||
| @displayName | st | 0..1 | R2 | Displayname des Codes | |||
| @codeSystemName | st | 0..1 | R2 | Codesystemname | |||
6.4.7.4 Ergebnis und Einheit
Die Angabe des Ergebnisses einer Laboruntersuchung erfolgt durch das value-Element. Die Codierung erfolgt gemäß dem Datentyp, welcher durch das xsi:type-Attribut ausgedrückt wird, hinter dem sich eine fixe Liste möglicher Datentypen verbirgt. Numerische Ergebnisse werden in der Regel als „physical quantity“ PQ dargestellt, was die Angabe einer UCUM codierten Einheit erforderlich macht. Es MUSS die „case sensitive“ Variante (c/s) der maschinenlesbaren Form des UCUM verwendet werden. Die bevorzugte Einheit für jede Analyse wird Value Set ELGA_Laborparameter vorgeschlagen, jeweils in der „print“ Variante (für die Darstellung) und in der maschinenlesbaren Form.
Es wird EMPFOHLEN, anstelle von Einheitenpräfixen („Giga“, „Mega“, „Milli“, „Mikro“ etc.) eine Potenzschreibweise zu wählen, vor allem, wenn die Groß/Klein-Schreibung eine Rolle spielt und Verwechslungen möglich sind (z.B. „G/L“=Giga pro Liter vs. „g/L“=Gramm/Liter). Also '10^6 ' statt 'M' (Mega), '10^9 ' statt 'G ' (Giga) usw.
6.4.7.4.1 Strukturbeispiele
Die Dokumentation eines numerischen Ergebniswertes erfolgt in diesem Fall als Attribut.
<value xsi:type="PQ" value="49.7" unit="%"/>
Die Codierung von textuellen Ergebnissen erfolgt in der Regel durch den “ST” Datentyp. Die Angabe des Ergebnisses erfolgt hier als Wert des Elementes.
<value xsi:type="ST">strohgelb</value>
Im narrativen Block MUSS derselbe Text wie im Entry dargestellt werden.
Auch für dimensionslose Einheiten wird in UCUM häufig eine Einheit angegeben, wie z.B. "[ph]" für den pH-Wert. Wenn keine UCUM-Einheit vorgeschlagen ist, können dimensionslose Einheiten auch mit @unit="1" dargestellt werden, hier für INR:
<value xsi:type="PQ" value="1.1" unit="1"/>
Für Verhältnisangaben, wie sie etwa für Titer verwendet werden (z.B. „1:128“) steht der Datentyp RTO (Ratio) zur Verfügung. Ein Anwendungsbeispiel:
<value xsi:type="RTO"> <numerator value="1" xsi:type="INT"/> <denominator value="128" xsi:type="INT"/> </value>
Intervalle können mit dem Datentyp IVL angegeben werden, z.B. „20-30 mg/L“:
<value xsi:type="IVL_PQ" > <low value="20" unit="mg/dl" inclusive="true"/> <high value="30" unit="mg/dl" inclusive="true"/> </value>
Das Attribut inclusive gibt mit true/false an, ob die Intervallgrenze im Intervall enthalten ist oder nicht (offenes oder geschlossenes Intervall)
6.4.7.4.2 Spezifikation
Für numerische Werte gilt:
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| value | PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ | 0..1 | O | ||
| @unit | cs | 1..1 | C | Physikalisch Einheit des Messwertes. UCUM Codierung empfohlen (siehe [7]) | |
| Konditionale Konformität: Bei EIS „Basic“ Bei EIS „Enhanced“ und „Full Support“ |
1..1 1..1 |
R2 M |
Angabe der Einheit erforderlich Angabe der Einheit nach UCUM (c/s) erforderlich. | ||
| @value | real | 1..1 | M | Größe des Messwertes | |
| @xsi:type | cs | 1..1 | M | Datentyp: für numerische Werte PQ | |
6.4.7.5 Befundinterpretation
Die Befundinterpretation wird als Subelement interpretationCode unter der observation codiert. Je Bereich darf nur eine entsprechend codierte Bewertung angegeben werden (nur eine Befundinterpretation). Die Codierung erfolgt gem. ELGA Value Set „ELGA_ObservationInterpretation“. Folgende Tabelle 10 zeigt die normative Befundinterpretation für numerische Ergebnisse, Tabelle 11 die Kennzeichnung für nicht numerische Ergebnisse, die nominal, ordinal und narrativ sein können.
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| ++ | HH | Oberhalb des Referenzbereiches und über einer oberen Warngrenze |
| + | H | Oberhalb des Referenzbereiches |
| N | Normal (innerhalb des Referenzbereiches) | |
| - | L | Unterhalb des Referenzbereiches |
| -- | LL | Unterhalb des Referenzbereiches und unter einer unteren Warngrenze |
Tabelle 10: Befundinterpretation numerischer Ergebnisse
| Darstellung Level 2 | Codierung Level 3 | Beschreibung |
|---|---|---|
| N | Normal (innerhalb des Referenzbereiches) | |
| * | A | Abnormal |
| ** | AA | Abnormal Warngrenze |
Tabelle 11: Befundinterpretation nicht numerischer Ergebnisse
6.4.7.5.1 Strukturbeispiel
Beispiel für numerische Ergebnisse
<interpretationCode code="H" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation" displayName="High"/>
Beispiel für nicht-numerische Ergebnisse
<interpretationCode code="AA" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation" displayName="Abnormal Alert"/>
6.4.7.5.2 Spezifikation
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| interpretationCode | CE CNE | 0..1 | CE CNE | ||
| Konditionale Konformität: EIS „Enhanced“ EIS „Basic“ |
1..1 0..1 |
M O |
Ein maschinenlesbares Element Ein maschinenlesbares Element | ||
| @code | cs | 1..1 | M | Code aus Value Set „ELGA_ObservationInterpretation“ | |
| @codeSystem | uid | 1..1 | M | Fester Wert: „2.16.840.1.113883.5.83“ | |
| @codeSystemName | st | 0..1 | R2 | Fester Wert: „HL7:ObservationInterpretation“ | |
| @displayName | st | 0..1 | R2 | Klartext-Darstellung des Codes | |
6.4.7.6 Validator
Zu jedem Ergebnis kann optional die validierende Person angegeben werden. Die Codierung erfolgt unter der Observation als participant mit dem Attribut typeCode=“AUTHEN“ und folgt einem spezifischen Template, welches diesen Participant als Validator kennzeichnet. Das Template ist verpflichtend anzugeben.
<templateId root="1.3.6.1.4.1.19376.1.3.3.1.5"/>
Weiters sind bei jeder Personenangabe die Elemente telecom und addr verpflichtend anzuführen, können jedoch mit einem nullFlavor versehen werden.
Wird zu einem Ergebnis eine validierende Person gelistet, ist diese auch im Header als authenticator anzuführen.
6.4.7.6.1 Strukturbeispiel
<participant typeCode="AUTHEN">
<templateId root="1.3.6.1.4.1.19376.1.3.3.1.5"/>
<time>
<low value="20130123211000.007-0500"/>
<high nullFlavor="UNK"/>
</time>
<participantRole>
<id extension="332" root="1.3.6.1.4.1.19376.1.3.4"/>
<addr nullFlavor"UNK"/>
<telecom value="tel: 312.555.5555"/>
<playingEntity>
<name>Susanne Hecht</name>
</playingEntity>
</participantRole>
</participant>
6.4.7.6.2 Spezifikation
6.4.7.6.2.1 Validator - Allgemein (observation/participant)
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| participant | POCD_MT000040.Participant | 0..* | O | ||
| @typeCode | cs | 1..1 | M | Fester Wert: AUTHEN | |
6.4.7.6.2.2 TemplateId (participant/templateId)
| Element/Attribut | DT | Kard | Konf | Beschreibung | |
|---|---|---|---|---|---|
| templateId | II | 1..1 | M | Template zur Codierung einer validierenden Person | |
| @root | uid | 1..1 | M | Fester Wert: „1.3.6.1.4.1.19376.1.3.3.1.5“ | |
6.4.7.6.2.3 TemplateId (participant/templateId)
| Element/Attribut | DT | Kard | Konf | Beschreibung |
|---|---|---|---|---|
| time | IVL_TS | 1..1 | M | Zeitpunkt der Validierung: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ |
6.4.7.6.2.4 Angaben zur validierenden Person (participant/participantRole)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||
|---|---|---|---|---|---|---|
| participantRole | POCD_MT000040.ParticipantRole | 1..1 | M | |||
| id | II | 1..1 | M | Identifikation der Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ | ||
| addr | AD | 1..1 | R | Adresse der Person/Organisation: Identifikation der Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ Zugelassene nullFlavor: UNK | ||
| telecom | TEL | 1..* | R | Kontaktdaten zur Person/Organisation:Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ Zugelassene nullFlavor: UNK | ||
| playingEntity | POCD_MT000040.PlayingEntity | 1..1 | R | |||
| name | PN | 1..1 | M | Name der validierenden Person: Es gelten die Vorgaben des entsprechenden Kapitels des „Allgemeinen Implementierungsleitfadens“ | ||
6.4.7.7 Referenzbereiche
Für die Bewertung der Laborergebnisse werden Referenzbereiche herangezogen, welche im Befund zu dokumentieren sind. Die Angabe erfolgt als referenceRange-Block unter der observation. Die Werte werden darunter in einem Block observationRange als Element value abgelegt. Die Ausprägung des Elementes erfolgt wiederum gem. einem Datentyp, welcher durch das Attribut xsi:type angegeben wird. Für numerische Werte wird der Referenzbereich in den meisten Fällen ein Intervall physikalischer Größen „IVL_PQ“ sein, welches in der Regel durch einen low und einen high Wert angegeben wird. Nachfolgendes Beispiel zeigt die Verwendung des referenceRange-Blocks mit einem Referenzbereich für normale Werte.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-1-5"> <td>Hämatokrit</td> <td>47.9</td> <td>G/l</td> <td ID="OBSREF-1-5">43.0 - 49.0</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-1-5"/> </text> <value xsi:type="IVL_PQ"> <low value="43.0" unit="%"/> <high value="49.0" unit="%"/> </value> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation"/> </observationRange> </referenceRange>
Im Falle eines einseitig unbeschränkten Intervalls wie z.B. bei „>40“ kann entweder nur der low, bzw. high Wert angegeben werden, wobei auf der Seite, der die Intervallgrenze fehlt, einen NullFlavor angegeben werden MUSS.
Ein „kleiner als“ Referenzbereich wie z.B. „<17“ SOLL als Intervall von 0 bis 17 beschrieben werden.
Im text-Bereich MUSS „>“ durch „& gt;“ und „<“ durch „& lt;“ ersetzt werden.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-3-19"> <td>HDL-Cholesterin</td> <td>0.30</td> <td>mg/dl</td> <td ID="OBSREF-3-19>>60</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-3-19"/> </text> <value xsi:type="IVL_PQ"> <low value="6 0.0" unit=" mg/dL" inclusive="false"/> <high nullFlavor="PINF"/> </value> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83" codeSystemName="HL7:ObservationInterpretation"/> </observationRange> </referenceRange>
Da oftmals die Kriterien für die Bewertung von Laborergebnissen nicht vollständig vorliegen, muss für einen Laborbefund die Angabe mehrerer möglicher Referenzbereiche möglich sein, welche sich durch unterschiedliche Vorbedingungen (preconditions) unterscheiden. Leider ist die Angabe solcher unter dem referenceRange laut CDA Rel.2 Definition nicht möglich. Deshalb MUSS an dieser Stelle eine Angabe in Textform erfolgen. Nachfolgendes Beispiel zeigt die Verwendung des 'referenceRange-Blocks mit mehreren Referenzbereichen mit Preconditions.
: <!-- Narrativer Block mit Analyse --> <tr ID="OBS-4-7"> <td>Östron</td> <td>165</td> <td>pg/ml</td> <td ID="OBSREF-4-7">Zyklus<br/> Follikelphase: 37-138<br/> Ovulationspeak: 60-230<br/> Lutealphase: 50-114</td> </tr> : <!-- Level 3 --> : <referenceRange typeCode="REFV"> <observationRange classCode="OBS" moodCode="EVN.CRT"> <!-- text: reference range with preconditions --> <text> <reference value="#OBSREF-4-7"/> </text> <interpretationCode code="N" codeSystem="2.16.840.1.113883.5.83"/> </observationRange> </referenceRange>
6.4.7.7.1 Spezifikation
6.4.7.7.1.1 Referenzbereich (observation/referenceRange)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||||
|---|---|---|---|---|---|---|---|---|
| referenceRange | POCD_MT000040.ReferenceRange | 0..1 | O | |||||
| @typeCode | cs | 1..1 | M | Fester Wert: REFV | ||||
| observationRange | POCD_MT000040.ReferenceRange | 1..1 | M | |||||
| @classCode | cs | 1..1 | M | Fester Wert: OBS | ||||
| @moodCode | cs | 1..1 | M | Fester Wert: EVN.CRT | ||||
| text | ED | 1..1 | M | Referenz auf den Referenzbereich im Narrativen Text | ||||
| reference | 1..1 | M | ||||||
| @value | 1..1 | M | Referenz auf Referenzbereich im narrativen Block (vgl. 6.2.9.2) | |||||
| value | PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ | 0..1 | O | Wert des Kriteriums | ||||
| interpretationCode | CE CNE | 1..1 | M | Fester Wert: N Analog zu Kapitel 6.4.7.3.8 mit der Einschränkung code=“N“ | ||||
6.4.7.7.1.2 Werte des Referenzbereichs (referenceRange/value)
| Element/Attribut | DT | Kard | Konf | Beschreibung | ||
|---|---|---|---|---|---|---|
| value | IVL_PQ | 0..1 | O | |||
| @xsi:type | cs | 1..1 | M | Fester Wert: IVL_PQ (für physical quantity) | ||
| low | PQ | 1..1 | R | Unterer Grenzwert Zugelassene nullFlavor: NINF (negativ unendlich), NA (nicht anwendbar) | ||
| @value | cs | 1..1 | M | Wert des unteren Grenzwerts | ||
| @unit | cs | 1..1 | M | Physikalische Einheit des unteren Grenzwerts (MUSS ident der Einheit des oberen Grenzwertes sein) | ||
| @inclusive | BL | 0..1 | O | Offene oder abgeschlossene Intervallgrenze
| ||
| high | PQ | 1..1 | R | Oberer Grenzwert Zugelassene nullFlavor: PINF (positiv unendlich), NA (nicht anwendbar) | ||
| @value | cs | 1..1 | M | Wert des oberen Grenzwerts | ||
| @unit | cs | 1..1 | M | Physikalische Einheit des oberen Grenzwerts (MUSS ident der Einheit des unteren Grenzwertes sein) | ||
| @inclusive | BL | 0..1 | O | Offene oder abgeschlossene Intervallgrenze | ||
6.4.7.8 Externes Labor
Die Codierung erfolgt gemäß observation/performer auf Ebene „Laboratory Observation“ (Siehe IHE-Labor Template 1.3.6.1.4.1.19376.1.3.1.6).
Gemäß der Abstimmung der medizinischen Inhalte ist es nicht notwendig, das konkrete externe Labor zu kennzeichnen. Demgemäß kann die ID des Labors mittels nullFlavor angegeben werden. Der code gibt an, dass es sich um ein externes bzw. „Fremdlabor“ handelt. Der code wurde mit „E“ fixiert.
6.4.7.8.1 Spezifikation
| Id | 1.2.40.0.34.11.4.3.3 ref elgabbr- | Gültigkeit ab | 2014‑12‑06 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryPerformer2 | Bezeichnung | Laboratory Performer 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Element zur Kennzeichnung einer Analyse, die in einem externen Labor durchgeführt wurde. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.3 Laboratory Performer 2 (2014‑12‑06) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.8 Kultureller Erregernachweis
Für die Codierung des Erregernachweises findet der „Laboratory Isolate Organzier“ (organizer) Verwendung. Dieses organizer-Element, welches über ein entryRelationship in den Specimen-Act (vgl. Kapitel Der Spezimen-Act) gebunden ist, codiert in dem code-Element die Methodik, welche für den Erregernachweis Verwendung findet. Die folgende Tabelle enthält Beispiele für Codes für die Methodik wie sie zum Beispiel in LOINC enthalten sind.
| @code | @displayName | code/originalText |
|---|---|---|
| 6463-4 | Bacteria XXX Cult | Kultur |
| 634-6 | Bacteria XXX Aerobe Cult | Aerobe Kultur |
| 635-3 | Bacteria XXX Anaerobe Cult | Anaerobe Kultur |
| 580-1 | Fungus XXX Cult | Pilzkultur |
Tabelle 12: Beispiele für Codes für Erregernachweis-Methodik entnommen aus LOINC
Für die Codierung der Methode können auch andere, hier nicht näher spezifizierte, LOINC Codes verwendet werden.LOINC-codierte Methoden für den kulturellen Erregernachweis sind mit der Methode „culture“ gekennzeichnet. Suche auf http://search.loinc.org mit Eingabe des entsprechenden Suchbegriffes method:culture.
6.4.8.1 Spezifikation
| Id | 1.2.40.0.34.11.30025 ref elgabbr- | Gültigkeit ab | 2017‑02‑23 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | KulturellerKeimnachweis | Bezeichnung | Kultureller Keimnachweis (Laboratory Isolate Organzier) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30025 Kultureller Keimnachweis (Laboratory Isolate Organzier) (2017‑02‑23) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.9 Antibiogramm (Laboratory Isolate Organizer)
Um das Antibiogramm in Level 3 darstellen zu können, wird das Antibiogramm als „Cluster“-Organizer zusammengefasst. Darin findet sich immer ein Isolat als Probenmaterial (specimen) an dem die Empfindlichkeitstests durchgeführt werden.
<organizer classCode="CLUSTER" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.5"/>
Sind mehrere Erreger im Befund vorhanden, wird für jeden ein „Isolat-Cluster“ angelegt. Für jeden Erreger ist eine eindeutige Nummer (ID) anzugeben. Die OID-Root stammt von der einsendenden Organisation.
Die durchgängige Codierung der Isolate bzw. Erreger ist momentan nicht durchführbar. Die Empfindlichkeitstests werden als „Battery“-Cluster angeführt.
<organizer classCode="BATTERY" moodCode="EVN"> <templateId root="1.3.6.1.4.1.19376.1.3.1.4"/>
Innerhalb des Organizers werden die einzelnen Antibiotika-Resistenztests zum Isolat wie „normale“ Laboranalysen gehandhabt.
Für die Codierung des Antibiogramms im Organizer ist der LOINC 29576-6 „Bacterial susceptibility panel“ vorgeschrieben.
Die einzelnen Antibiotika-Empfindlichkeitstests sind als LOINC anzugeben. Z.B.: 18993-6 steht für einen Tetracyclin-Empfindlichkeitstest.
Die Interpretation erfolgt über die entsprechenden Codes aus „ELGA_ObservationInterpretation“. Tabelle 13 zeigt einen Ausschnitt.
| Codierung | Resistenz |
|---|---|
| R | Resistent |
| I | Intermediär (intermediate) |
| S | Sensibel (susceptible) |
Tabelle 13: Codierung der Resistenzen
6.4.9.1 Spezifikation
| Id | 1.2.40.0.34.11.30026 ref elgabbr- | Gültigkeit ab | 2014‑04‑15 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Antibiogram | Bezeichnung | Antibiogram (Laboratory Isolate Organzier) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.30026 Antibiogram (Laboratory Isolate Organzier) (2014‑04‑15) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.10 Minimale Hemmkonzentration
Die Angabe der erforderlichen Daten für die minimale Hemmkonzentration erfolgt in Level 2 und Level 3 in unterschiedlicher Struktur. In Level 2 (vgl. Kapitel Minimale Hemmkonzentration) werden die Werte in eine eigene Tabelle geschrieben. Die Codierung für Level 3 erfolgt jedoch gemeinsam mit der Codierung eines Antibiogramms (vgl. Kapitel Kultureller Erregernachweis). Der Absolutwert wird innerhalb von organizer/component/observation/value als „Physical Quantity“ codiert. Das interpretationCode-Element hingegen codiert die, für das Antibiogramm notwendige, Information über die Suszeptibilität (R, I, oder S).
6.4.11 Testergebnisse/Molekularer Erregernachweis
Die Level 3 Codierung von „Testergebnissen/Molekularer Erregernachweis“ erfolgt analog der Codierung von Laborergebnissen (vgl. Laborergebnisse). Eine Gruppierung kann mit Hilfe von „Befundgruppen“ (vgl. Befundgruppen) erfolgen.
6.4.12 Significant Pathogens (Notifiable Conditions)
Wichtige Erreger können in Level 3 codiert werden. Diese Erreger sind in der Codeliste „ELGA_SignificantPathogens“ (1.2.40.0.34.5.45) aufgelistet. Diese Liste enthält etwa die meldepflichtigen Krankheiten. Die Level 3-Codierung erfolgt über einen „Notification Organizer“ (organizer-Element) mit „Notifiable Condition“ als observation-Element.
6.4.12.1 Spezifikation Notification Organizer
| Id | 1.3.6.1.4.1.19376.1.3.1.1 ref elgabbr- | Gültigkeit ab | 2013‑09‑09 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | NotificationOrganizer | Bezeichnung | Notification Organizer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.1 Notification Organizer (2013‑09‑09) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.12.2 Spezifikation Notifiable Condition
| Id | 1.3.6.1.4.1.19376.1.3.1.1.1 ref elgabbr- | Gültigkeit ab | 2013‑09‑09 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | NotifiableCondition | Bezeichnung | Notification Condition | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.3.6.1.4.1.19376.1.3.1.1.1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.3.6.1.4.1.19376.1.3.1.1.1 Notification Condition (2013‑09‑09) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.13 Befundtext: Anmerkungen und Kommentare
Die Codierung von Anmerkungen und Kommentaren erfolgt in jedem Fall gem. IHE als sogenannter „Annotation-Act“. Die Codierung erfolgt als act-Element, welches mittels entsprechender Beziehung (entryRelationship oder component) an das übergeordnete Element gebunden wird. Die Elemente templateId und code sind fix vorbelegt. Das einzige veränderbare Element ist der text-Block. Dieser SOLL eine Referenz auf ein Element innerhalb der Level 2 Codierung enthalten (vgl. Kapitel Referenz von Level 3 auf Level 2: Beziehung von Level 3 über den Referenz Verweis reference-Element mit Attributevalue=“refID“ auf die ID eines Elements in Level 2 wie z.B. content ID=“refID“).
6.4.13.1 Spezifikation
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.13.2 Bereichsübergreifende Befundbewertung
Im Falle einer Gliederung eines Laborbefundes in zwei Hierarchieebenen (Bereiche und Befundgruppen) besteht die Notwendigkeit einer bereichsübergreifenden Befundbewertung/eines Befundkommentars. Die Abbildung derartiger bereichsübergreifender Befundbewertungen erfolgt über eine eigene Annotation Section (siehe [4]).
6.4.13.2.1 Spezifikation
| Id | 1.2.40.0.34.11.4.2.2 ref elgabbr- | Gültigkeit ab | 2013‑02‑10 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | LaboratoryReportCommentSection | Bezeichnung | Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.2.2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.2.2 Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) (2013‑02‑10) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.13.2.2 Spezifikation Befundtext
| Id | 1.2.40.0.34.11.4.3.2 ref elgabbr- | Gültigkeit ab | 2015‑01‑30 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | Annotation | Bezeichnung | Befundtext (Anmerkungen und Kommentare) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.11.4.3.2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Offen (auch andere als die definierten Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.11.4.3.2 Befundtext (Anmerkungen und Kommentare) (2015‑01‑30) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
6.4.14 Multimedia Content
Im Laborbefund sind folgende Mulitmedia Formate zulässig: eingebettete PDF/A-Dateien („application/pdf“) sowie Grafiken im Format „image/jpeg“, „image/gif“ oder „image/png. Alle Grafiken und Bilder sind inline Base64 zu codieren und zu übertragen. Referenzen auf externe Grafiken sind NICHT ERLAUBT.
<value mediaType="image/jpeg" representation="B64">
Die Codierung von Multimedia Inhalten erfolgt gem. „Allgemeinem Implementierungsleitfaden“, Kapitel Einbetten von Dokumenten/Multimedia-Dateien ([4]).
Alternativ zur allgemeingültigen Variante kann die Level 3 Codierung auch als component-Element auf Ebene direkt unter dem Bereich (Spezimen-Act) oder der Befundgruppe (siehe Laboratory Battery Organizer) erfolgen.
6.4.14.1 Spezifikation
Keine Versionen mit Status draft, active, review oder pending.
7 Technische Konformitätsprüfung
Die Prüfung einer XML-Instanz gegenüber Konformität zu diesem Leitfaden erfolgt gemäß dem entsprechenden Kapitel im „Allgemeinen Implementierungsleitfaden“ [4].
Dokumente, die mit diesem Leitfaden erstellt wurden, validieren gegebenenfalls nicht vollständig gegenüber Prüfroutinen, die auf IHE Laboratory Technical Framework Volume 3 (LABTF 3) basieren. Siehe z.B. Kapitel Laboratory Report Data Processing Entry.
8 Anhang
8.1 Referenzen
| [1] | VHitG: Arztbrief auf Basis der HL7 Clinical Document Architecture Release 2 für das Deutsche Gesundheitswesen Vers. 1.50, (Stand 12.05.2006) |
| [2] | VHitG: Addendum zum Arztbrief V1.50 auf der Basis der HL7 CDA Release 2 für das Deutsche Gesundheitswesen Darstellung Labor Vers.1.00, (Stand 02.07.2007) |
| [3] | IHE International: IHE Laboratory Technical Framework Volume 3 (LABTF 3) Revision 3.0, Final Text Version, 19.05.2011), |
| http://www.ihe.net/Technical_Framework/index.cfm | |
| [4] | ELGA GmbH (2015) HL7 Implementation Guide for CDA® R2: Allgemeiner Implementierungsleitfaden für ELGA CDA Dokumente. |
| ELGA CDA Implementierungsleitfäden (2.06) [OID 1.2.40.0.34.7.1.6], http://www.elga.gv.at/cda | |
| [5] | Schadow G, McDonald CJ et al: Units of Measure in Clinical Information Systems. JAMIA. 6(2); Mar/Apr 1999; p.~151--162. |
| Available from: URL: http://www.jamia.org/cgi/reprint/6/2/151, 26.05.2008 | |
| [6] | IHE International: IHE Patient Care Coordination (PCC)Technical Framework, Volume 2, Revision 6.0, Final Text, 30.08.2010, |
| http://www.ihe.net/Technical_Framework/index.cfm | |
| [7] | UCUM: Table of Example UCUM codes for Electronic Messaging 1.3, Release Date Sept. 26 2014, |
| https://loinc.org/usage/units | |
| [8] | Sabutsch, S. & C. Seerainer: Leitfaden zur Nutzung von ELGA-Terminologien, Version 1.1. |
| http://www.elga.gv.at/cda | |
| [9] | Sabutsch, S. & G. Weigl: Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund, Version 1.01 (22.07.2015), |
| http://www.elga.gv.at/cda | |
| [10] | ISO 15189:2012 "Medizinische Laboratorien - Anforderungen an die Qualität und Kompetenz" |
8.2 Revisionsliste
| Version | Datum | Änderungsgrund |
|---|---|---|
| 1.00 | 01.07.2009 | Release 1.0 |
| 1.3 | 05.08.2011 | Draft |
| 1.9 | 23.08.2011 | Überarbeitung, Release Candidate 1 |
| 2.00 | 10.10.2011 | Überarbeitung, Format Anpassung |
| 2.01 | 21.12.2012 | Überarbeitung, Format Anpassung, Typos |
| 2.01a | 05.02.2013 | „Keim“ ersetzt durch „Erreger“ |
| 2.01a | 15.02.2013 | Seite 17: Fußnote zur Erklärung des Begriffs „Erreger“ eingefügt |
| 2.01a | 04.03.2013 | Korrekturen in Zeile: 5: ebenso -> sowohl; 6,8 "und" ein-gefügt; 22: "diesem" eingefügt; ~60: LOINC Erklärung vorgezogen;201: die "Entlassungbrief", die -> den; 290-300 "human lesbar" -> "menschenlesbar"; 303: die Definitionen, "die" -> "den"; 321: "ELGA Portal" -> "ELGA Bürgerportal"; 414: "mit" gelöscht; 472: "jedoch" gelöscht; 525: "als" eingefügt; 530, 569 "sind" -> "ist"; 715: "ist" ->
"sind"; 806: "Kapitel" eingefügt; 960: "Teiles" eingefügt; 1035: "ist" -> "sind"; 1913: "anzugeben" eingefügt Änderungen in Beispielen: Beispiel in 4.4.13.3.1 Korrektur <entryRelationship> Beispiel in 4.4.12.4.1 Example -> Beispiel Änderungen in Tabellen: Tabelle in 1.3.1 Datum und Zeit des der Probenannahme im Labor, "des" gelöscht Tabelle in 4.3.1, erster gelber Bereich: "in" eingefügt Tabelle 7 und 12. Oberhalb des Referenzbereiches und über einer "oberen" Warngrenze, oberhalb/unterhalb des Referenzbereiches |
| 2.01a | 03.04.2013 | Anpassung der Formatierung und Verweise |
| 2.01a | 08.04.2013 | Kapitel 3.4.1.2 (Spezifikation Auftraggeber): Titel analog zu Allgemeinem Leitfaden geändert, Beschreibung in Tabelle korrigiert: Auftraggeber, Optionalität korrigiert: R, templateID an richtige Stelle gerückt: 2. Stelle |
| 2.01a | 09.04.2013 | In Strukturbeispielen 3.3.4.1. und 3.4.1.1. telecom use="PUB" durch "WP" ersetzt |
| 2.01a | 03.05.2013 | 4.4.7.5.2:.UCUM Codierung bei EIS „Basic“ von [M] auf [R2] korrigiert |
| 2.01a | 06.05.2013 | 4.4.9.2.1. Antibiogramm-Allgemein: Konformität von [M] auf [R2] korrigiert |
| 2.02 | 09.07.2013 | 3.2.2. Verwendung von IHE templateID für Lab entfernt 3.4.1. Konformität von Einweisenden Arzt auf [NP] 1.6. Kapitel umformuliert 4.4.12.2. Falsche Konformität in Spezifikationstabelle ausge-bessert 3.3.5.2. Konformität und Kardinalität von 1..1 [M] auf 0..* [O] ausgebessert 3.3.5.1. Kommentar in Strukturbeispiel entfernt 4.3.6.4. Kapitel Level 2 Befundbewertung ergänzt 4.4.5.2.1 Strukturbeispiel um <text> Element erweitert 4.3.3.1. Kapitel gelöscht (Beispiel nicht aussagekräftig) 4.3.4. Kapitel Probeninformation hinzugefügt |
| 2.02 | 15.07.2013 | Reihenfolge der Kapitel „Dokumentenklasse“ und „Dokumententitel“ geändert 3.2.3.2 DisplayName von „laboratory report.total“ auf „LABORATORY REPORT.TOTAL” geändert |
| 2.02 | 24.07.2013 | 3.4.2.2: Konformität des Ordering Provider von O auf R geändert und Text angepasst. |
| 2.02 | 24.07.2013 | 3.4.2.2: Zugelassenen NullFlavor UNK für den Auftraggeber spezifiziert |
| 2.02 | 05.08.2013 | 2. Anwendungsfälle: Bestimmungen zu genetischen Befunden präszisiert, Verweis auf Protokoll der AG-Sitzung gestrichen. |
| 2.02 | 12.08.2013 | informationRecipient aus Kapitel 3.3.2 (Elemente ohne speziellen Einschränkungen) gestrichen, da Einschränkungen in in Kapitel 3.3.4 getroffen werden. |
| 2.02 | 19.08.2013 | Kapitel 4.4.5 Spezimen-Information in Probeninformation (Specimen-Section) umbenannt Änderung der Spezifikation in Kapitel 4.4.5.3.3.4. effectiveTime\low und effectiveTime\high durch effectiveTime@value ersetzt |
| 2.02 | 20.08.2013 | Kapitel „Empfänger (ClinicalDocument/informationRecipient)“ gelöscht, da vorhandene Einschränkungen durch IHE im Widerspruch mit dem Allgemeinen Implementierungsleitfaden standen. Kapitel 3.3.2: Aufzählung um „Beabsichtigte Empfänger des Dokuments (informationRecipient)“ ergänzt |
| 2.02 | 21.08.2013 | 3.4.1 Spezifikationstabelle des Elements „Einweisender/Zuweisender/Überweisender Arzt“ entfernt. Im Text präzisiert, dass das entsprechende Element Participant TypeCode REF mit templateId 1.2.40.0.34.11.1.1.2) nicht erlaubt ist. |
| 2.02 | 22.08.2013 | Spezifikationstabellen des Validators in Kapitel 3.3.4.2 eingefügt |
| 2.02. | 22.08.2013 | 4.3.9. Kultureller Erregernachweis: Eingefügt: "Sollte kein Erreger nachweisbar sein, wird folgende Formulierung EMPFOHLEN: 'Erreger nicht nachweisbar'" |
| 2.02. | 27.08.2013 | 4.4.5.3.3.8. Kapitel ergänzt Tabelle 6 überarbeiten nach den konsolidierten Beispielbefunden 4.3.4 Typo in Überschrift ausgebessert und Hinweis auf verpflichtende Angabe zur Spezimeninformation 4.4.5.1 Hinweis auf verpflichtende Angabe zur Spezimeninformation für Level 3 bei EIS „full support“. |
| 2.02. | 28.08.2013 | 4.4.7.4.2 Hinweis, wie mit Analysen ohne Codes umzugehen ist hinzugefügt 4.4.7.4.3 Kapitel „Laborergebnisse ohne passenden Code“ hinzugefügt Layout von Spezifikationstabellen angeglichen (Fester Wert:) 4.2.5 Kapitel umbenannt (von „Struktur“ auf „Allgemeine Strukturrichtlinie für Body-Elemente“) und Hinweis hinzugefügt, dass für Probeninformationsektion keine IHE templateId anzugeben ist 4.3.7.3 Kapitel umbenannt (von „Bemerkung zu einer Befundart“ in „Bemerkung zu einem Befundbereich“). Sowie notwendige Anpassungen im Kapiteltext 4.3.8.1 Kapitel „Strukturbeispiel“ für Mikroskopie hinzugefügt 4.4.1 Übersichtstabelle: Ändern der Pfade von Abnahmeinformation und Annahmeinformation sowie löschen der Referenz auf Kapitel „Analyse: Identifikation/Codierung“ da kein eilenumbruch in Tabellenfeld erfolgte 4.4.5.3.2 Strukturbeispiel überarbeitet |
| 2.02 | 11.09.2013 | 4.4.5.3.3.4 Titel von "Zeitpunkt der Abnahme" auf "Zeit der Abnahme" geändert, Beschreibungstext : "Zeitpunkt oder Zeitintervall der Specimengewinnung" |
| 2.02 | 12.09.2013 | 4.4.7.5.2:.Beschreibung der Konditionalen Konformität geändert: Statt „Codierung der Einheit“ nun „Angabe der Einheit“ @value Datentyp auf „real“ geändert (vorher PQ) |
| 2.02 | 17.09.2013 | Typos, Formatierung und Seitenumbrüche ausgebessert |
| 2.02a | 28.01.2014 | Tabelle 2: Konformität des Auftraggebers (IHE „Ordering Provider“) korrigiert – jetzt konsistent mit Spezifikation 3.4.2.2.: R [1..1] |
| 2.02a | 13.02.2014 | 4.4.5.2.2.2 Laboratory Specimen Entry Spezifikation korrigiert. <templateId> nun als child von <act> definiert (war parent von <act>). Fehlendes Element <statusCode> ergänzt. |
| 2.02a | 27.03.2014 | 3.4.2.2. Spezifikationstabelle: TemplateID war doppelt angegeben |
| 2.02a | 10.06.2014 | 4.4.5.3.3.7 Beschreibung der Codierung der Art des Spezimens nachgetragen (hat gefehlt) |
| 2.02a | 27.06.2014 | 4.4.7.2.1. Strukturbeispiel für ein Laborergebnis mit Cut-off-Wert (> 500 mg/dl) hinzugefügt. |
| 2.02a | 27.06.2014 | 4.4.7.9.1.2 Werte des Referenzbereichs (referenceRange/value) Erlaubte NullFlavor für High hinzugefügt. |
| 2.02a | 27.06.2014 | 4.4.7.2. Strukturbeispiel Verweis auf narrativen Text hinzugefügt |
| 2.02a | 27.06.2014 | 4.4.7.3.12. Ergänzt: Angabe des Text-Elements mit Verweis auf narrativen Text (observation/text) |
| 2.02a | 27.06.2014 | 4.4.7.10 performer/assignedEntity/id wurde auf [R] gesetzt, erlaubter NullFlavor "NI" |
| 2.02a | 27.06.2014 | 4.3.5.1. Vorgabe zur Darstellung und Schreibweise der Analysen hinzugefügt |
| 2.02a | 27.06.2014 | 4.3.5.3. Vorgabe zur Darstellung und Schreibweise der Einheiten hinzugefügt |
| 2.02a | 27.06.2014 | Bei allen konditionalen Vorgaben für EIS „Enhanced“ auch EIS „Full Support“ (Enhanced-Vorgaben gelten auch für Full Support) |
| 2. 02a | 27.06.2014 | 4.4.7.10.1.Strukturbeispiel von externem Labor korrigiert |
| 2. 02a | 30.06.2014 | 4.4.7.10.2.1 Laboratory Performer-Allgemein (observation/performer) Definition für Code externes Labor hinzugefügt |
| 2. 02a | 30.06.2014 | Zugelassene nullFlavor hinzugefügt: 3.3.4.2.1. Authenticator.Time 3.3.4.2.2. authenticator/assignedEntity 3.4.2.2. participant.Time, participant.Addr 4.4.7.3.6. Zeitpunkt des Laborergebnisses 4.4.7.8.2.4 Angaben zur validierenden Person 4.4.7.10.2.1 Laboratory Performer-Allgemein - 4.9.2.1. Antibiogramm-Allgemein 4.4.7.9.1.2 Werte des Referenzbereichs für LOW +HIGH |
| 2. 02a | 30.06.2014 | 4.4.5.3.3.4 Zeit der Abnahme: Definition korrigiert ([R] statt [M], damit NullFlavor UNK verwendet werden kann) |
| 2. 02a | 01.07.2014 | 4.4.8.2. Kultureller Erregernachweis Fehlende Spezifikation für EffectiveTime hinzugefügt |
| 2. 02a | 15.07.2014 | 4.4.2.1. Überweisungsgrund als Vorschlag hinzugefügt |
| 2. 02a | 15.07.2014 | 4.4.13.1.2.1 Spezifikation des Kommentars: StatusCode ergänzt (hat gefehlt) |
| 2. 02a | 15.07.2014 | 3.5.2. Durchführende Labors: Beschreibung der Semantik des Elementes time hinzugefügt. |
| 2. 02a | 15.08.2014 | Ergänzung (4.2.2 und 4.3.1): Die Verwendung der Sektion Brieftext ist erlaubt |
| 2. 02a | 26.08.2014 | Seite 2: Absatz „Weitere unterstützene Dokumente“ eingefügt Dokumenteninformation auf Seite 5: Haftungsausschuss gelöscht, Hinweis zur Verbindlichkeit eingefügt , LOINC-Lizenzinformationen geändert |
| 2. 02a | 29.08.2014 | 4.4.4.1.1. in der Spezifikationstabelle die "Notifiable Conditions" erwähnt |
| 2. 02a | 29.08.2014 | 4.4.7.4.3.1 und 4.4.7.4.3.2 Verwendung des OriginalText bei "unbekannten Analysen" entfernt, Beschreibung ergänzt. |
| 2. 02a | 29.08.2014 | 4.4.8.2. Spezifikation um fehlende Elemente ergänzt |
| Version 2.05 (Hauptversion) | ||
| 2.05 | 12.03.2014 | Seite 4: Formulierung zur Verbindlichkeit aktualisiert |
| 2.05 | 27.11.2014 | Typos und verwaiste dokumentinterne Verweise korrigiert |
| 2.05 | 20.11.2014 | Anwendungsfall „Blutgruppenserologie und Transfusionsmedizin“ umformuliert |
| 2.05 | 20.11.2014 | LOINC für Dokumentenklasse Laborbefund 11502-2: Der Common Name wurde im LOINC auf „Laboratory report“ geändert (war LABORATORY REPORT.TOTAL), betrifft 3.2.3.1, 3.2.3.2 und 3.2.4.1: |
| 2.05 | 25.11.2014 | 3.3.3, 3.3.4 und 3.3.5: Die Rollen Medizinischer Validator, Validator und Autor klarer beschrieben |
| 2.05 | 27.11.2014 | 4.2.1. Strukturierter Body: Korrektur der Benennung der EIS |
| 2.05 | 27.11.2014 | 4.2.3. Bereiche in Tabelle 4 nach neuer Struktur von Value Set ELGA_Laborparameter aktualisiert |
| 2.05 | 18.02.2015 | 4.2.6: Angaben in Tabelle 5 verbessert |
| 2.05 | 23.02.2015 | 4.2.7.1. Strukturbeispiel: Referenz für Referenzbereiche ergänzt |
| 2.05 | 23.02.2015 | 4.2.8.2. Referenz von Level 3 auf Level 2: Abbildung neu |
| 2.05 | 12.11.2014 | 4.3.1 Überblick der Darstellung: Präzisierung der Elemente in der Tabelle |
| 2.05 | 03.03.2015 | 4.3.1. Überblick der Darstellung der Ergebnistabelle: Überschriften bei Probeninformation geändert. |
| 2.05 | 25.11.2014 | 4.3.4. Probeninformation: Im Beispiel die TemplateID im „specimen Collection“ entfernt |
| 2.05 | 03.03.2015 | 4.3.4. Probeninformation: Abbildung 10 geändert und 11 hinzugefügt, Strukturbeispiel angepasst. |
| 2.05 | 25.11.2014 | 4.3.4. Probeninformation: Im Beispiel die TemplateID im „specimen Collection“ entfernt |
| 2.05 | 12.03.2014 | 4.3.4.1. Spezimen-Section eingefügt und überarbeitet: das Entry ist nun [C] mit Angabe der Optionen |
| 2.05 | 25.11.2014 | 4.3.8.2. Eigenschaften des Materials/Mikroskopie: Spezifikationstabelle hinzugefügt |
| 2.05 | 12.03.2014 | 4.4.5.1 Überblick Spezimen Textteil verschoben nach 4.3.4 |
| 2.05 | 11.02.2015 | 4.4.5.2.1. Strukturbeispiel geändert (Entry Attribute, StatusCode) |
| 2.05 | 12.03.2014 | 4.4.5.2.2.1 Spezimen-Sektion verschoben nach 4.3.4.1 |
| 2.05 | 11.02.2015 | 4.4.5.2.2.2 Spezifikation für "Laboratory Specimen Entry" korrigiert (@typeCode, @statusCode, Tabellenformatierung) |
| 2.05 | 23.02.2015 | 4.4.5.3.2. Strukturbeispiel Abnahmeinformation: Person hinzugefügt |
| 2.05 | 26.01.2015 | 4.4.7.3.4. Analyse/Testcode: Dokumentinterner Querverweis korrigiert |
| 2.05 | 17.10.2014 | 4.4.7.3.5. Status des Laborergebnisses (observation/statusCode) von [O] auf [M] gesetzt sowie die Kardinalität von [0..1] auf [1..1] geändert (entsprechend IHE XD Lab) |
| 2.05 | 12.11.2014 | 4.4.7.3.10. Dokumeninterne Verweise korrigiert |
| 2.05 | 23.02.2015 | 4.4.7.9.Strukturbeispiele und Spezifikation für Referenzbereiche: Im Level 3 muss eine Referenz auf den narrativen Text angegeben werden, nicht der Text selbst. |
| 2.05 | 17.10.2014 | Kapitel 4.4.7.10.1 und 4.4.7.10.2.1 (performer), neue templateId: 1.2.40.0.34.11.4.3.3 (alt:1.3.6.1.4.1.19376.1.3.3.1.7) sowie verschieben des code-Elements in dem Strukturbeispiels als auch in der Spezifikation |
| 2.05 | 25.11.2014 | 4.4.8. Kultureller Erregernachweis: Angabe, welche LOINC-Codes für den kulturellen Erregernachweis angegeben werden können. |
| 2.05 | 25.11.2014 | 4.4.9.2.1. Antibiogramm-Allgemein: Angabe, wie welche Antibiotika angegeben werden können. |
| 2.05 | 23.02.2015 | 4.4.13. Befundtext Anmerkungen und Kommentare: Im Entry MUSS immer die Referenz auf den Kommentar im narrativen Text angegeben werden. 4.4.13.1.1. Strukturbeispiel: Angepasst |
| 2.05 | 23.01.2015 | 4.4.13.1.1 Neue templateId 1.2.40.0.34.11.4.3.2 für Kommentare zu einer Analyse (Annotation Comment) hinzugefügt, entsprechend in allen Strukturbeispielen |
| 2.05 | 25.11.2014 | 4.4.13.3.1. Strukturbeispiel: Position der TemplateId unter <act> verschoben |
| 2.05 | 25.11.2014 | 4.4.13.4.1. Strukturbeispiel: Position der TemplateId unter <act> verschoben |
| 2.05 | 27.11.2014 | 4.4.14.2.1. Typo in den erlaubten Werte für @mediaType |
| 2.05 | 11.02.2015 | Revisionsliste überarbeitet und umgeordnet |
| Version 2.06 | ||
| 2.06 | 10.09.2015 | Buchstabendreher korrigiert für (richtig) POCD_MT000040 |
| 2.06 | 12.10.2015 | Neu organisiert: Dokumententeninformation, Harmonisierung, Hinweise zur Nutzung des Leitfadens, Verbindlichkeit, Hinweis auf verwendete Grundlagen, Danksagung, Bedienungshinweise und Inhaltsverzeichnis |
| 2.06 | 27.04.2015 | 2. Anwendungsfälle: Formulierung zu genetischen Analysen aktualisiert. |
| 2.06 | 20.07.2015 | 3.3.4. Medizinischer Validator („ClinicalDocument/legalAuthenticator“): Korrekturen, Hinweis auf verpflichtende Angabe hinzugefügt |
| 2.06 | 29.09.2015 | 3.3.5.1 Struktubeispiel: bei <country> Österreich durch AUT ersetzt |
| 2.06 | 29.09.2015 | 3.3.5.2.2 authenticator.assignedEntity: Fehlende zugelassene nullFlavor UNK für id und addr ergänzt |
| 2.06 | 17.07.2015 | 3.3.6. Weitere Beteiligte („participants“): Hinzugefügt, Empfehlung zur Angabe des fachlichen Ansprechpartners |
| 2.06 | 17.07.2015 | 4.2.3. Sektion „Überweisungsgrund“ hinzugefügt. |
| 2.06 | 28.09.2015 | 4.2.3. OID für „Überweisungsgrund“ ist 1.2.40.0.34.11.4.2.4 |
| 2.06 | 05.11.2015 | 4.2.8 Nachkommastellen im Strukturbeispiel eingefügt |
| 2.06 | 22.10.2015 | 4.2.10 Verweis auf den Leitfaden zum LOINC-Mapping [9] |
| 2.06 | 05.05.2015 | 4.3.1. Überblickstabelle:
|
| 2.06 | 05.11.2015 | 4.3.1 Fußnote hinzugefügt: Empfehlung für Punkt als Dezimaltrenmzeichen im narrativen Block |
| 2.06 | 24.08.2015 | 4.3.5.4. Befundinterpretation: N (für Normal) auch in der Tabelle 8 für nicht-numerische Ergebnisse ergänzt. RAST-Klassen für Allergiediagnostik erwähnt. |
| 2.06 | 17.07.2015 | Kapitel 4.3.6. hinzugefügt: „Empfehlungen für die Darstellung der Allergiediagnostik“ |
| 2.06 | 17.07.2015 | 4.3.9. Kultureller Erregernachweis: Formulierungsvorschlag für "Keime (oder Mikroorganismen) nicht nachweisbar" hinzugefügt |
| 2.06 | 29.09.2015 | 4.4.1 Verweise korrigiert |
| 2.06 | 17.07.2015 | 4.4.2 Sektion „Allgemeine Befundinformation“ in „Überweisungsgrund“ umbenannt, präzisiert und spezifiziert |
| 2.06 | 31.08.2015 | Strukturbeispiele 4.3.8.2., 4.3.9.1. Strukturbeispiel, 4.3.10.1.: überflüssiges <paragraph> Element entfernt |
| 2.06 | 29.09.2015 | 4.4.5.3.2 Struktubeispiel: bei <country> Österreich durch AUT ersetzt |
| 2.06 | 30.09.2015 | 4.4.6.2 Befundgruppen Strukturbeispiel: bei <component> den fehlenden verpflichtenden typeCode COMP ergänzt |
| 2.06 | 01.06.2015 | 4.4.7.3.7 Ergebnis der Analyse: Datentyp ANY eingeschränkt auf PQ, IVL_PQ, INT, IVL_INT, BL, ST, CV, CD, RTO, RTO_QTY_QTY, RTO_PQ_PQ |
| 2.06 | 22.10.2015 | 4.4.7.4 Verweis auf den Leitfaden zum LOINC-Mapping [9] |
| 2.06 | 14.09.2015 | 4.4.7.5. Ergebnis und Einheit: Präzisiert: Die "case sensitive" Variante des UCUM (c/s) ist zu verwenden. |
| 2.06 | 17.07.2015 | 4.4.7.5.1. Strukturbeispiel für Textergebnisse: Erklärung hinzugefügt |
| 2.06 | 30.09.2015 | 4.4.7.6, Tabelle 12: „N“ zur Bewertung nicht-numerischer Ergebnisse hinzugefügt |
| 2.06 | 22.10.2015 | 4.4.7.9. Referenzbereiche: Bessere Beschreibung der Angabe von unbeschränkten Intervallen |
| 2.06 | 30.09.2015 | 4.4.12.3. Spezifikation Notifiable Condition: Elemente <id> und <effectiveTime> ergänzt |
| 2.06 | 17.07.2015 | 4.4.14. Multimedia Content zusätzlich PDF-Attachments zugelassen: application/pdf Präzisierung des Textes – klare Beschreibung, dass es zwei Varianten für Multimedia-Dateien gibt |
| 2.06 | 30.09.2015 | 4.4.14.1. Strukturbeispiel Multimediacontent: <id> entfernt |
| Version 2.06.1 (Nebenversion) x …betrifft Implementierung (erste Spalte) | ||
| 21.01.2016 | 3.3.6 Fachlicher Ansprechpartner: Die angegebene Kombination 1..* und [R2] ist ungültig, korrigiert auf Kard 0..1 und Konf [R2]. | |
| Version 2.06.2 (Nebenversion) | ||
| 01.08.2016 | Kapitel Verbindlichkeit: Definition der Angabe verbindlicher Vorgaben. | |
| 01.08.2016 | Kapitel Harmonisierung: Arbeitszeitraum der Arbeitsgruppen hinzugefügt. Ergänzende Korrektur der Liste | |
| 19.08.2016 | 2.4 Anwendungsfall „Update von Laboranalysen“ hinzugefügt | |
| 19.12.2016 | 3.1 und 3.6.: Informationen zum Patientenkontakt (ClinicalDocument/componentOf/encompassingEncounter) war als NP angegeben, ist nun [O] | |
| 11.08.2016 | 3.3.3. Autor: Verbot der Angabe einer Software als Autor entfernt (damit die erstellende Software angegeben werden kann), jedoch muss mindestens eine Person muss als Autor vorhanden sein. | |
| 12.09.2016 | 3.4.2. Auftraggeber/„Ordering Provider“: Verhalten bei nullFlavor präzisiert, Strukturbeispiel hinzugefügt | |
| 25.03.2016 | 4.1.1 Ergänzung der Definition für EIS Basic und Structured | |
| 30.01.2016 | 4.2.2. Sektion Brieftext: Präzisierung bei der Angabe des Logos. | |
| 19.12.2016 | 4.3.9.2 Spezifikationstabelle Sektion Mikroskopie: Sektion ist korrekterweise [O] und 0..1, war [M] und 0..1. | |
| 30.01.2017 | 4.3.14 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012 | |
| 19.12.2016 | 4.4.1. Überblick: Inkonsistente Kardinalitäten in der Übersichtstabelle korrigiert: "Erregernachweis mit Definition der Methodik", "Antibiogramm und minimale Hemmkonzentration" und "Testergebnisse und Molekularer Erregernachweis" sind mit Opt R2 jetzt mit Kard [0..*] (statt 1..*) angegeben. | |
| 08.03.2016 | 4.4.4.1.1. Spezifikation ELGA Spezimen-Act-Entry Allgemein: Verweis auf Multimedia Content (4.4.14) hinzugefügt 4.4.14. Multimedia Content: Angabemöglichkeit für Multimedia im Bereich (Spezimen-Act 4.4.4) ermöglicht. Strukturbeispiel hinzugefügt. | |
| 19.12.2016 | 4.4.7.9.1.1 Die Beschreibung zu @value wurde korrigiert. Anstelle auf einen "Referenzbereich" wurde auf einen "Kommentar" im Freitext verwiesen. | |
| 05.04.2016 | 4.4.5.3. Abnahmeinformationen (Specimen Collection) 4.4.5.4. Annahmeinformationen (Specimen Received) Tippfehler in „entryRelationship“ verbessert | |
| 16.11.2016 | 4.4.5.3.3.4 Zeit der Abnahme (procedure/effectiveTime): Einschränkung auf Datentyp TS im value-Attribut entfernt, da das Element IVL_TS und TS zulässt. | |
| 26.04.2016 | 3.4.2.2. Auftraggeber/„Ordering Provider“ - Spezifikation: associatedPerson statt [M] nunmehr [R], zugelassener NullFlavor "UNK". telecom statt [M] nunmehr [R], zugelassener NullFlavor "UNK“. | |
| 30.01.2017 | AG Laborbefund: Vorgaben für den Deltacheck entfernt, da nicht benötigt: 4.3.1, 4.3.5.5, 4.4.7.6, 4.4.7.7, etc. | |
| 18.08.2016 | 4.3.1 Richtigstellung der Vorgaben für die Interpetation der Optionalitäten in der Tabellendarstellung. | |
| 18.08.2016 | 4.3.2 Präzisierung der Beschreibung von Datums- und Zeitangaben im lesbaren Teil | |
| 30.01.2017 | 4.3.5.1. Analysen: Beschreibung, wie nähere Angaben zur Methode gemacht werden können. Siehe auch 4.3.8.1. Bemerkungen zu Analysen | |
| 10.08.2016 | 4.3.5.3. Einheit 4.4.7.5. Ergebnis und Einheit Für UCUM Einheiten Empfehlung hinzugefügt, anstelle von Einheitenpräfixen („Giga“, „Mega“, „Milli“, „Mikro“ etc.) eine Potenzschreibweise zu wählen, also '10^6 ' statt 'M' (Mega), '10^9 ' statt 'G ' (Giga) usw. | |
| 30.01.2017 | 4.3.8.1. Bemerkungen zu Analysen oder Analyseergebnissen: Beschreibung verallgemeinert und Abbildung aktualisiert. | |
| 30.01.2017 | 4.4.5.2.2.1 Laboratory Specimen Entry: Differenzierte Angabe der Kardinalität und Konformität nach EIS Basic, Enhanced und Full Support | |
| 19.08.2016 | Analysen mit „Wert folgt“ ermöglicht: 4.4.7.2.2. Strukturbeispiel für ein in Arbeit befindliches Laborergebnis („Wert folgt“) hinzugefügt | |
| 09.01.2017 | 4.4.7.3.4. Analyse/Testcode (observation/code) und 4.4.7.4.2. Spezifikation: Code ist wg. Ausnahme "Laborergebnis ohne passenden Code" [R] und nicht [M] | |
| 19.12.2016 | 4.4.7.3.7. Ergebnis der Analyse / des Tests: Datentyp TS (Timestamp) ist kein sinnvoller Datentyp, daher entfernt | |
| 28.11.2016 | 4.4.7.4.3. Laborergebnisse ohne passenden Code. Hinweis zur Einreihung solcher Analysen am Befund | |
| 19.12.2016 | 4.4.7.5.1. Strukturbeispiele für ein dimensionsloses Laborergebnis (PQ) und ein Laborergebnis mit Datentyp RTO (Ratio), z.B. für Titer und ein Intervall (Datentyp IVL) hinzugefügt | |
| 24.06.2016 | 4.4.7.5.2. Spezifikation für numerische Werte: Value von ANY auf PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ eingeschränkt 4.4.7.9.1.1 Referenzbereich (observation/referenceRange) Datentyp für Value von ANY auf PQ, IVL_PQ, INT, IVL_INT, RTO, RTO_QTY_QTY, RTO_PQ_PQ korrigiert 4.4.7.9.1.2 Werte des Referenzbereichs (referenceRange/value) Datentyp für Value von ANY auf IVL_PQ korrigiert | |
| 03.08.2016 | 3.2.4.2, 3.5.2, 4.2.1, 4.3.5.3, 4.3.8.2, 4.3.8.3, 4.4.4, 4.4.7.5.1, 4.4.7.9, 4.4.7.9, 4.4.7.9.1.2, 4.1.1, 4.3.1, 3.4.1, 4.4.14 Korrektur der Großschreibung bei normativen Vorgaben | |