Labor- und Mikrobiologiebefund (Version 3.0.0)
| [unmarkierte Version] | [unmarkierte Version] |
(→IHE PaLM TF-3 Konformität) |
(→Zweck des Dokuments) |
||
| Zeile 172: | Zeile 172: | ||
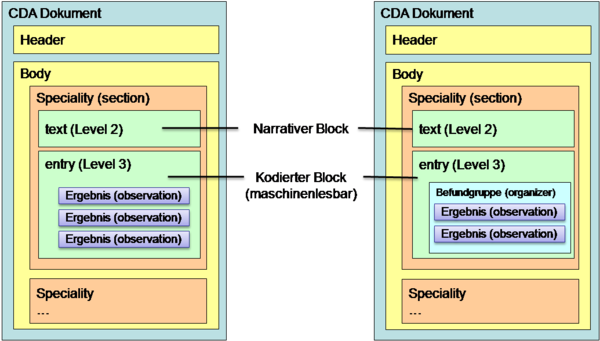
Die medizinisch relevanten Anteile sind im so genannten "Body" enthalten. Die vorliegende Spezifikation der laborspezifischen inkl. mikrobiologische Inhalte eines Labordokuments in ELGA wurde von der Expertengruppe beruhend auf einer Liste mit Vorgaben der österreichischen Gesellschaft für Labormedizin und klinische Chemie (ÖGLMKC) erstellt. | Die medizinisch relevanten Anteile sind im so genannten "Body" enthalten. Die vorliegende Spezifikation der laborspezifischen inkl. mikrobiologische Inhalte eines Labordokuments in ELGA wurde von der Expertengruppe beruhend auf einer Liste mit Vorgaben der österreichischen Gesellschaft für Labormedizin und klinische Chemie (ÖGLMKC) erstellt. | ||
| − | Als technische Basis dient das "Laboratory Technical Framework Volume 3 ( | + | Als technische Basis dient das "Pathology and Laboratory Medicine (PaLM) Technical Framework Volume 3 (PaLM TF-3) Revision 10.0, 2019"<ref name="IHEPaLMTF3" /> der "Integrating the Healthcare Enterprise" (IHE). |
Das Verständnis eines "Laborbefundes" erstreckt sich in diesem Dokument über das gesamte Spektrum der laboranalytisch ermittelten Befunde. Die vorliegende Version definiert grundlegende Anforderungen für die Erstellung von Laborbefunden als CDA Dokumente. Insbesondere wurden Laborbefunde aus der Klinischen Chemie, Hämatologie, Immunchemie und Mikrobiologie/Bakteriologie in die Überlegungen mit einbezogen. Die gewählten Strukturen ermöglichen prinzipiell eine Übermittlung des gesamten Befundspektrums des Laborbereiches, jedoch sind die einzelnen Detailbereiche in folgenden Arbeiten detailliert zu analysieren, abzustimmen und für weitere Laborbefundarten zu definieren. Es existieren vielmehr auch dezidierte Bereiche - wie z.B. die Transfusionsmedizin – für die die Definitionen dieses Leitfadens aufgrund fehlender Strukturen und nicht definierter Codelisten nicht ausreichend sind. Dieser Leitfaden verwendet "Analysen" als Sammelbegriff für Laboruntersuchungen, Laborleistungen und Labormessgrößen. | Das Verständnis eines "Laborbefundes" erstreckt sich in diesem Dokument über das gesamte Spektrum der laboranalytisch ermittelten Befunde. Die vorliegende Version definiert grundlegende Anforderungen für die Erstellung von Laborbefunden als CDA Dokumente. Insbesondere wurden Laborbefunde aus der Klinischen Chemie, Hämatologie, Immunchemie und Mikrobiologie/Bakteriologie in die Überlegungen mit einbezogen. Die gewählten Strukturen ermöglichen prinzipiell eine Übermittlung des gesamten Befundspektrums des Laborbereiches, jedoch sind die einzelnen Detailbereiche in folgenden Arbeiten detailliert zu analysieren, abzustimmen und für weitere Laborbefundarten zu definieren. Es existieren vielmehr auch dezidierte Bereiche - wie z.B. die Transfusionsmedizin – für die die Definitionen dieses Leitfadens aufgrund fehlender Strukturen und nicht definierter Codelisten nicht ausreichend sind. Dieser Leitfaden verwendet "Analysen" als Sammelbegriff für Laboruntersuchungen, Laborleistungen und Labormessgrößen. | ||
Version vom 9. April 2021, 13:12 Uhr
|
|
Diese Seite oder Abschnitt ist derzeit ein Entwurf und kann sich noch ändern. This article was last edited by Kleinoscheg (talk| contribs) 4 years ago. This article or section is in the middle of an expansion or major restructuring. This article was last edited by Kleinoscheg (talk| contribs) 4 years ago. |
|
|
Dieses Dokument gibt wieder:
Implementierungsleitfaden Labor- und Mikrobiologiebefund (3.0.0), OID: 1.2.40.0.34.7.4.9.3, Datum: 2021.xx.xx, Status: Normativ. Die Teilmaterialien gehören der Kategorie ILF an. |
Implementierungsleitfäden
Labor- und Mikrobiologiebefund
Gesundheitswesen [1.2.40.0.34.7.4.9.3]
Inhaltsverzeichnis
- 1 Zusammenfassung
- 2 Informationen über dieses Dokument
- 3 Einleitung
- 4 Leitfadenerstellungs- und Harmonisierungsprozess
- 5 Technischer Hintergrund
- 6 Allgemeine Richtlinien für ELGA CDA-Implementierungsleitfäden
- 7 Konformitätsprüfung
- 8 Datentypen
- 9 Vorgaben zum medizinischen Inhalt
- 10 Funktionale Anforderungen
- 11 Anwendungsfälle
- 11.1 Anwendungsfall LAB01: "Laboruntersuchung eines niedergelassenen Labors"
- 11.2 Anwendungsfall LAB02: "Laboruntersuchung im Rahmen eines stationären Aufenthalts in einem Spital"
- 11.3 Anwendungsfall LAB03: "Teilweise externe Vergabe von Laboruntersuchungen"
- 11.4 Anwendungsfall LAB04: "Update von Laborbefunden"
- 12 Dataset des Labor- und Mikrobiologiebefunds
- 13 Technische Spezifikation
- 13.1 Übersichtstabelle der CDA Strukturen des Headers
- 13.2 Übersichtstabelle der Header-Elemente für dokumenten-relevante Zeitpunkte/Zeitspannen
- 13.3 Übersichtstabelle der CDA Strukturen des Bodys
- 13.4 CDA Templates
- 13.4.1 IHE PaLM TF-3 Konformität
- 13.4.2 Document Level Templates
- 13.4.3 Header Level Templates
- 13.4.4 Section Level Templates
- 13.4.4.1 Brieftext
- 13.4.4.2 Überweisungsgrund - optional codiert
- 13.4.4.3 Angeforderte Untersuchungen - optional codiert
- 13.4.4.4 Probeninformation (Specimen Section)
- 13.4.4.5 Laboratory Specialty Section
- 13.4.4.6 Laboratory Specialty Section (Mikroskopie)
- 13.4.4.7 Laboratory Specialty Section (Kultureller Erregernachweis)
- 13.4.4.8 Laboratory Specialty Section (Molekularer Erregernachweis)
- 13.4.4.9 Laboratory Specialty Section (Infektionsserologie)
- 13.4.4.10 Befundbewertung
- 13.4.4.11 Beilagen
- 13.4.4.12 Abschließende Bemerkung
- 13.4.5 Entry Level Template
- 13.4.5.1 Probeninformation (Specimen Entry)
- 13.4.5.2 Specimen Collection
- 13.4.5.3 Specimen Received
- 13.4.5.4 Laboratory Report Data Processing Entry
- 13.4.5.5 Notification Organizer
- 13.4.5.6 Notifiable Condition
- 13.4.5.7 Laboratory Isolate Organizer
- 13.4.5.8 Laboratory Battery Organizer
- 13.4.5.9 Laboratory Observation
- 13.4.5.10 Eingebettetes Objekt Entry
- 13.4.5.11 Comment Entry
- 13.4.6 Weitere CDA Fragmente
- 13.5 Terminologien
- 14 Anhang
Dieses Dokument bildet den vollständigen Implementierungsleitfaden des Labor- und Mikrobiologiebefundes ab und richtet sich an Softwareentwickler und Berater. Zum besseren Verständnis empfehlen wir Ihnen, den zusammenfassenden Guide im Vorfeld zu lesen.
1 Zusammenfassung
Der Implementierungsleitfaden "Labor- und Mikrobiologiebefund" beschreibt die Inhalte, die für den Austausch von fertiggestellten, und fachärztlich vidierten Befunden innerhalb und zwischen Einrichtungen des österreichischen Gesundheitswesens, notwendig sind.
Der Leitfaden enthält Festlegungen, Einschränkungen und Bedingungen auf Grundlage des internationalen Standards ISO/HL7 27932:2009 HL7 Clinical Document Architecture, Release 2.0 (CDA) und ist ein nationaler Standard der HL7 Austria.
Die Grundlage der Datenaustauschformate ist der internationale CDA-Standard, der sich in ELGA bewährt hat. Er erlaubt es Sender und Empfänger, sich ohne vorherige Absprache zu verstehen. Der Standard hat zum Ziel, einen umfassenden Austausch von semantisch interoperablen Informationen zwischen allen beteiligten Akteuren bei der Behandlung von Patienten zu ermöglichen. Der Datenaustausch findet hierbei nicht nur innerhalb einer Einrichtung, sondern auch zwischen kooperierenden Einrichtungen und über Sektorengrenzen hinaus statt. Die Empfänger der Dokumente sollen die Inhalte benutzen und weiterverwenden können, ohne sich vorher mit dem Ersteller absprechen zu müssen.
TODO: Standard XDLAB, FullSupport, status active/completed
Der "Labor- und Mikrobiologiebefund" basiert auf den Vorgaben des Allgemeinen Implementierungsleitfadens. Darin werden die notwendigen Datentypen, Dokument-Metadaten (Header), die Möglichkeiten der Textstrukturierung, grundlegende Vorgaben für die Anwendung von Terminologien, einige allgemein genutzten Inhaltsstrukturen (Sections) sowie Codebeispiele und praktische Implementierungshilfen gezeigt. Alle weiteren, für diesen Leitfaden benötigten Elemente werden hier erklärt. Die Notation der Spezifikation der Datenaustauschformate folgt der "Art-Decor"-Schreibweise, die auf einer eigenen Seite (Art-Decor-Tabellen verstehen) erläutert wird.
Der vorgesehene Ablauf des Datenaustausches wird im Kapitel Anwendungsfälle beschrieben.
Übersichtstabellen für Header und Body-Strukturen
- Übersichtstabelle der CDA Strukturen des Headers (administrative Daten)
- Übersichtstabelle der CDA Strukturen des Bodys (medizinische Inhalte)
Auf der Diskussionsseite werden die Fehler und Änderungswünsche an dieser Version dokumentiert.
2 Informationen über dieses Dokument
2.1 Impressum
Medieneigentümer, Herausgeber, Hersteller, Verleger:
ELGA GmbH, Treustraße 35-43, Wien, Österreich. Telefon: +43.1.2127050
Internet: www.elga.gv.at
Email: cda@elga.gv.at
Geschäftsführer: DI Dr. Günter Rauchegger, DI(FH) Dr. Franz Leisch
Redaktion, Projektleitung, Koordination:
Mag.Dr. Stefan Sabutsch, stefan.sabutsch@elga.gv.at
Abbildungen: © ELGA GmbH
Nutzung: Das Dokument enthält geistiges Eigentum der Health Level Seven® Int. und HL7® Austria, Franckstrasse 41/5/14, 8010 Graz; www.hl7.at.
Die Nutzung ist ohne Lizenz- und Nutzungsgebühren zum Zweck der Erstellung medizinischer Dokumente ausdrücklich erlaubt. Andere Arten der Nutzung und auch auszugsweise Wiedergabe bedürfen der Genehmigung des Medieneigentümers.
Download unter www.gesundheit.gv.at und www.elga.gv.at/cda
2.2 Haftungsausschluss
Die Arbeiten für den vorliegenden Leitfaden wurden von den Autoren gemäß dem Stand der Technik und mit größtmöglicher Sorgfalt erbracht und über ein öffentliches Kommentierungsverfahren kontrolliert. Die Nutzung des vorliegenden Leitfadens erfolgt in ausschließlicher Verantwortung der Anwender. Aus der Verwendung des vorliegenden Leitfadens können keinerlei Rechtsansprüche gegen die Autoren, Herausgeber oder Mitwirkenden erhoben und/oder abgeleitet werden. Ein allfälliger Widerspruch zum geltenden Recht ist jedenfalls nicht beabsichtigt und von den Erstellern des Dokumentes nicht gewünscht.
2.3 Sprachliche Gleichbehandlung
Soweit im Text Bezeichnungen nur im generischen Maskulinum angeführt sind, beziehen sie sich auf Männer, Frauen und andere Geschlechtsidentitäten in gleicher Weise. Unter dem Begriff "Patient" werden sowohl Bürger, Kunden und Klienten zusammengefasst, welche an einem Behandlungs- oder Pflegeprozess teilnehmen als auch gesunde Bürger, die derzeit nicht an einem solchen teilnehmen. Es wird ebenso darauf hingewiesen, dass umgekehrt der Begriff Bürger auch Patienten, Kunden und Klienten mit einbezieht.
2.4 Lizenzinformationen
Die von HL7 Austria erarbeiteten Standards und die Bearbeitungen der Standards von HL7 International stellen Werke im Sinne des österreichischen Urheberrechtsgesetzes dar und unterliegen daher urheberrechtlichem Schutz.
HL7 Austria genehmigt die Verwendung dieser Standards für die Zwecke der Erstellung, des Verkaufs und des Betriebs von Computerprogrammen, sofern nicht anders angegeben oder sich die Standards auf andere urheberrechtlich oder lizenzrechtlich geschützte Werke beziehen.
Die vollständige oder teilweise Veröffentlichung der Standards (zum Beispiel in Spezifikationen, Publikationen oder Schulungsunterlagen) ist nur mit einer ausdrücklichen Genehmigung der HL7 Austria gestattet. Mitglieder von HL7 Austria sind berechtigt, die Standards vollständig oder in Auszügen ausschließlich organisationsintern zu publizieren, zu vervielfältigen oder zu verteilen. Die Veröffentlichung eigener Anpassungen der HL7-Spezifikationen (im Sinne von Lokalisierungen) oder eigener Leitfäden erfordert eine formale Vereinbarung mit der HL7 Austria.
HL7® und CDA® sind die eingetragenen Marken von Health Level Seven International. Die vollständigen Lizenzinformationen finden sich unter https://hl7.at/nutzungsbedingungen-und-lizenzinformationen/. Die Lizenzbedingungen von HL7 International finden sich unter http://www.HL7.org/legal/ippolicy.cfm
2.4.1 Urheber- und Nutzungsrechte von anderen Quellen ("Third Party IP")
Third Party Intellectual Property
Der Nutzer dieses Dokuments (bzw. der Lizenznehmer) stimmt zu und erkennt an, dass HL7 Austria nicht alle Rechte und Ansprüche in und an den Materialien besitzt und dass die Materialien geistiges Eigentum von Dritten enthalten und / oder darauf verweisen können ("Third Party Intellectual Property (IP)").
Die Anerkennung dieser Lizenzbestimmungen gewährt dem Lizenznehmer keine Rechte in Bezug auf Third Party IP. Der Lizenznehmer allein ist für die Identifizierung und den Erhalt von notwendigen Lizenzen oder Genehmigungen zur Nutzung von Third Party IP im Zusammenhang mit den Materialien oder anderweitig verantwortlich.
Jegliche Handlungen, Ansprüche oder Klagen eines Dritten, die sich aus einer Verletzung eines Third Party IP-Rechts durch den Lizenznehmer ergeben, bleiben die Haftung des Lizenznehmers.
2.4.2 SNOMED CT
Dieser Leitfaden enthält Material, das durch SNOMED International urheberrechtlich geschützt ist. Jede Verwendung von SNOMED CT in Österreich erfordert eine aufrechte Affiliate Lizenz oder eine Sublizenz. Die entsprechende Lizenz ist kostenlos, vorausgesetzt die Verwendung findet nur in Österreich statt und erfüllt die Bedingungen des Affiliate License Agreements. Affiliate Lizenzen können über das Member Licensing and Distribution Service (MLDS) direkt beim jeweiligen NRC beantragt werden: MLDS für Österreich.
2.4.3 Weitere Terminologien
Im Folgenden finden Sie eine nicht-exhaustive Liste von weiteren Terminologien, die eine solche separate Lizenz erfordern können:
| Terminologie | Eigentümer, Kontaktinformation |
|---|---|
| Logical Observation Identifiers Names & Codes (LOINC) [1] | Regenstrief Institute, Inc. [2] |
| Unified Code for Units of Measure (UCUM) [3] | Regenstrief Institute, Inc. [2] |
| International Classification of Diseases (ICD) [4] | World Health Organization (WHO) [5] |
| ICD-10 BM*G*[6] | Für Gesundheit zuständiges Bundesministerium www.sozialministerium.at |
| Anatomical Therapeutic Chemical Classification System (ATC) [7] | World Health Organization (WHO)[5] |
| Pharmazentralnummer (PZN) | ARGE Pharma im Fachverband der chemischen Industrie Österreichs (FCIO) der Wirtschaftskammern Österreichs (WKO) [8] |
| EDQM-Codes | Europäisches Direktorat für die Qualität von Arzneimitteln [9] |
| Medical Device Communications (MDC) vom ISO/IEEE 11073 Standard | MDC wird als Substandard 10101 "Nomenclature" in "Health informatics - Medical / health device communication standards", kurz 11073, geführt und werden mit einem Copyright bei IEEE SA am österreichischen Termserver bereitgestellt. [10], [11] |
Die Terminologien werden am österreichischen Terminologieserver zur Verfügung gestellt.
2.5 Verwendete Grundlagen und Bezug zu anderen Standards
Grundlage dieses Implementierungsleitfadens ist der internationale Standard "HL7 Clinical Document Architecture, Release 2.0" (CDA ©), für die das Copyright © von Health Level Seven International[12] gilt. 2009 wurde die Release 2.0 als ISO-Standard ISO/HL7 27932:2009 publiziert[13].
CDA definiert die Struktur und Semantik von "medizinischen Dokumenten" zum Austausch zwischen Gesundheitsdiensteanbietern und Patienten. Es enthält alle Metadaten zur Weiterverarbeitung und einen lesbaren textuellen Inhalt und kann diese Informationen auch maschinenlesbar tragen. Das Datenmodell von CDA und seine Abbildung in XML[14] folgen dem Basisstandard HL7 Version 3[15] mit seinem Referenz-Informationsmodell (RIM). Dieser Leitfaden verwendet das HL7-Template-Austauschformat zur Definition der "Bausteine" (Templates) und ART-DECOR® [16] als Spezifikationsplattform.
- HL7 Clinical Document Architecture (CDA) [17]
- HL7 Referenz-Informationsmodell (RIM)[18]
- HL7 V3 Datentypen [19]
- HL7 Template-Austauschformat Specification and Use of Reusable Information Constraint Templates, Release 1[20]
Die HL7 Standards können über die HL7 Anwendergruppe Österreich (HL7 Austria)[21], die offizielle Vertretung von Health Level Seven International in Österreich bezogen werden (www.HL7.at). Alle auf nationale Verhältnisse angepassten und veröffentlichten HL7-Spezifikationen können ohne Lizenz- und Nutzungsgebühren in jeder Art von Anwendungssoftware verwendet werden.
Der Labor- und Mikrobiologiebefund basiert auf den Vorgaben des Allgemeinen Implementierungsleitfadens (Version 3).
Für die Modellierung der technischen Spezifikation diente IHE XD-LAB 2019-08 [TODO].
- IHE Integrationsprofile Patient Care Coordination [22]
- IHE Pharmacy Technical Framework Supplement Community Medication Administration (CMA) Rev. 1.1 – Trial Implementation
- HL7 CDA® R2 Implementation Guide: Personal Healthcare Monitoring Report, Release 1
TODO: Grafik anpassen + Referenz anpassen
2.6 Verbindlichkeit
Die Verbindlichkeit und die Umsetzungsfrist dieses Leitfadens sind im Gesundheitstelematikgesetz 2012, BGBl.I Nr.111/2012 sowie in den darauf fußenden ELGA-Verordnungen geregelt.
Der Leitfaden in seiner jeweils aktuell gültigen Fassung sowie die aktualisierten Terminologien sind vom zuständigen Minister auf www.gesundheit.gv.at zu veröffentlichen. Der Zeitplan zur Bereitstellung der Datenaustauschformate wird durch das Gesundheitstelematikgesetz 2012 und darauf basierenden Durchführungsverordnungen durch den zuständigen Bundesminister vorgegeben. Hauptversionen, also Aktualisierungen des Implementierungsleitfadens, welche zusätzliche verpflichtende Konformitätskriterien enthalten ("Mandatory" (M), "Required" (R) und "Fixed" (F)), sind mit ihren Fristen zur Bereitstellung per Verordnung kundzumachen. Andere Aktualisierungen (Nebenversionen) dürfen auch ohne Änderung dieser Verordnung unter www.gesundheit.gv.at veröffentlicht werden.
Die Anwendung dieses Implementierungsleitfadens hat im Einklang mit der Rechtsordnung der Republik Österreich und insbesondere mit den relevanten Materiengesetzen (z.B. Ärztegesetz 1998, Apothekenbetriebsordnung 2005, Krankenanstalten- und Kuranstaltengesetz, Gesundheits- und Krankenpflegegesetz, Rezeptpflichtgesetz, Datenschutzgesetz 2000, Gesundheitstelematikgesetz 2012) zu erfolgen. Technische Möglichkeiten können gesetzliche Bestimmungen selbstverständlich nicht verändern, vielmehr sind die technischen Möglichkeiten im Einklang mit den Gesetzen zu nutzen.
Die Einhaltung der gesetzlichen Bestimmungen liegt im Verantwortungsbereich der Ersteller der CDA-Dokumente.
2.7 Wichtige unterstützende Materialien
Auf der Website Labor- und Mikrobiologiebefund Guide werden unter anderem folgende Materialien zur Verfügung gestellt:
- die PDF-Version dieses Leitfadens
- Beispieldokumente
- ein erweitertes CDA-Schema
- Schematron-Prüfregeln
Die im weiteren angeführten Templatespezifikationen wurden im Art-Decor Projektrepository Labor- und Mikrobiologiebefund erstellt und können dort eingesehen werden.
Gemeinsam mit diesem Leitfaden werden auf der Website der ELGA GmbH (www.elga.gv.at/CDA) weitere Dateien und Dokumente zur Unterstützung bereitgestellt:
- Beispieldokumente
- Referenz-Stylesheet (Tool zur Darstellung im Browser - Konvertierung in HTML)
- CDA2PDF Suite (Tool zur Erzeugung einer PDF-Datei zur Ausgabe am Drucker)
- Schematron-Dateien für die Prüfung der Konformität ("Richtigkeit") von CDA Dateien
- Vorgaben zur Registrierung von CDA-Dokumenten (Leitfaden für XDS-Metadaten)
- Hinweise für die zu verwendenden Terminologien
- Leitfaden zur richtigen Verwendung von Terminologien
Fragen, Kommentare oder Anregungen für die Weiterentwicklung können an cda@elga.gv.at gesendet werden. Weitere Informationen finden Sie unter www.elga.gv.at/CDA.
2.8 Bedienungshinweise
2.8.1 Farbliche Hervorhebungen und Hinweise
Themenbezogene Hinweise zur besonderen Beachtung:
Hinweis:
Es dürfen keine Elemente oder Attribute verwendet werden, die nicht vom allgemeinen oder einem speziellen ELGA-Implementierungsleitfaden definiert wurden
Hinweis auf anderen Implementierungsleitfaden:
Verweis
Verweis auf den Allgemeinen Leitfaden:…
Themenbezogenes CDA Beispiel-Fragment im XML Format:
<BEISPIEL> <languageCode code="de-AT" />
Nutzen Sie die bereitgestellten Links im Dokument (z.B. im Inhaltsverzeichnis), um direkt in der PDF-Version dieses Dokuments zu navigieren. Folgende Tastenkombinationen können Ihnen die Nutzung des Leitfadens erleichtern:
- Rücksprung: Alt + Pfeil links und Retour: Alt + Pfeil rechts
- Seitenweise blättern: "Bild" Tasten
- Scrollen: Pfeil nach oben bzw. unten
- Zoomen: Strg + Mouserad drehen
- Suchen im Dokument: Strg + F
3 Einleitung
[TODO überarbeiten]
3.1 Ausgangslage und Motivation
Die Elektronische Gesundheitsakte (ELGA) ermöglicht den vom ELGA-Gesetz berechtigten Personen, entsprechend ihren Rollen, den Zugriff auf relevante Gesundheitsdaten, die in bedarfsgerecht elektronisch aufbereiteter Form online zur Verfügung gestellt werden.
Die zentrale Anwendung von ELGA ist die Bereitstellung von medizinischen Dokumenten (e Befunde) der ELGA-Teilnehmer, die in vielen unterschiedlichen Informationssystemen der verschiedenen ELGA-Gesundheitsdiensteanbieter erstellt werden. Diese Dokumente sollen nicht nur von Benutzern gelesen, sondern auch wieder in die IT-Systeme integriert und dort weiterverwendet werden können ("Semantische Interoperabilität"). Beispielsweise können für den Arzt aus ELGA-Dokumenten automatisch Warnungen, Erinnerungen und Zusammenfassungen generiert und weitere Informationen berechnet sowie kontextbezogen angezeigt werden.
Um dieses Ziel zu erreichen, wird für Dokumente in ELGA der internationale Standard "Clinical Document Architecture, Release 2.0" (CDA) von HL7 eingesetzt.
Der CDA-Standard wird für die Verwendung in ELGA im Detail ausspezifiziert. Vorgaben für einheitliche Dokumentation und Codierung der Information werden festgelegt und in implementierbaren Leitfäden veröffentlicht.
3.2 Zweck des Dokuments
Das vorliegende Dokument enthält die Definition der Inhalte des "Laborbefundes" für das Österreichische Gesundheitswesen. Diese Spezifikation ist das Resultat einer Harmonisierungsarbeit mit dem Ziel medizinische Befunde, innerhalb der derzeit im Aufbau befindlichen österreichischen "Elektronischen Gesundheitsakte" (ELGA), als abgestimmte und einheitlich strukturierte Dokumente darzustellen. Das Dokument wurde von einer Arbeitsgruppe von Vertretern der Österreichischen Ärztekammer, von mehreren Krankenhausträgern und Spitälern, Universitäten und Fachgesellschaften, des österreichischen Normeninstitutes, von der Health Level 7 (HL7) Anwendergruppe Österreich, sowie Personen aus der Wirtschaft erstellt. Sowohl angestellte als auch niedergelassene Labormediziner waren massiv an der Erarbeitung beteiligt.
Die Abstimmung erfolgte gemeinsam mit anderen Arbeitsgruppen, die gleichzeitig an den Inhalten für den "Entlassungsbrief" und den "Befund bildgebende Diagnostik" arbeiten. Vor allem die Informationen über die betroffenen und handelnden Personen, Zeitangaben, Dokumentart und ähnliches im so genannten "Header" wurden eng abgestimmt und im Rahmen eines zentralen Dokumentes "Allgemeiner Implementierungsleitfaden für ELGA CDA Dokumente [OID Root 1.2.40.0.34.7.1]" [4] definiert.
Der Header enthält zum einen administrative Daten (allgemeine Angaben zum Dokument, Daten zum Patienten, usw.) und dient zum anderen zum Teil auch als Quelle für die Metadaten, die bei der Registrierung des Dokuments in ELGA verwendet werden. Der Header wurde über alle Anwendungsbereiche der ELGA einheitlich abgestimmt.
Die medizinisch relevanten Anteile sind im so genannten "Body" enthalten. Die vorliegende Spezifikation der laborspezifischen inkl. mikrobiologische Inhalte eines Labordokuments in ELGA wurde von der Expertengruppe beruhend auf einer Liste mit Vorgaben der österreichischen Gesellschaft für Labormedizin und klinische Chemie (ÖGLMKC) erstellt.
Als technische Basis dient das "Pathology and Laboratory Medicine (PaLM) Technical Framework Volume 3 (PaLM TF-3) Revision 10.0, 2019"[23] der "Integrating the Healthcare Enterprise" (IHE).
Das Verständnis eines "Laborbefundes" erstreckt sich in diesem Dokument über das gesamte Spektrum der laboranalytisch ermittelten Befunde. Die vorliegende Version definiert grundlegende Anforderungen für die Erstellung von Laborbefunden als CDA Dokumente. Insbesondere wurden Laborbefunde aus der Klinischen Chemie, Hämatologie, Immunchemie und Mikrobiologie/Bakteriologie in die Überlegungen mit einbezogen. Die gewählten Strukturen ermöglichen prinzipiell eine Übermittlung des gesamten Befundspektrums des Laborbereiches, jedoch sind die einzelnen Detailbereiche in folgenden Arbeiten detailliert zu analysieren, abzustimmen und für weitere Laborbefundarten zu definieren. Es existieren vielmehr auch dezidierte Bereiche - wie z.B. die Transfusionsmedizin – für die die Definitionen dieses Leitfadens aufgrund fehlender Strukturen und nicht definierter Codelisten nicht ausreichend sind. Dieser Leitfaden verwendet "Analysen" als Sammelbegriff für Laboruntersuchungen, Laborleistungen und Labormessgrößen.
3.3 Zielgruppe
Anwender dieses Dokuments sind Softwareentwickler und Berater, die allgemein mit Implementierungen und Integrationen im Umfeld der ELGA, insbesondere der ELGA-Gesundheitsdaten, betraut sind. Eine weitere Zielgruppe sind alle an der Erstellung von CDA-Dokumenten beteiligten Personen, einschließlich der Endbenutzer der medizinischen Softwaresysteme und der Angehörigen von Gesundheitsberufen.
4 Leitfadenerstellungs- und Harmonisierungsprozess
Für die Ausgestaltung der Inhalte von "CDA Implementierungsleitfäden" ist eine breite Beteiligung der Stakeholder wesentlich, um die praktische Nutzbarkeit und die Akzeptanz durch die ELGA-Benutzer sicherzustellen. Für diese interdisziplinären Expertengruppen stehen nicht die technischen, sondern vor allem medizinisch-inhaltliche Aspekte im Vordergrund. Die technischen Inhalte werden großteils von den Redaktionsteams beigetragen.
Ein wesentlicher Schritt auf dem Weg zur Interoperabilität der IT-Systeme im Gesundheitswesen ist die Einigung auf Vorgaben für einheitliche Dokumentation und Codierung der Information. Diese durch die Arbeitsgruppen erreichte "Harmonisierung" etabliert neue nationale Qualitätsstandards der medizinischen Dokumentation. Die Leitfäden werden über ein reguläres Standardisierungsverfahren ("Ballot") durch die HL7 Anwendergruppe Österreich (HL7 Austria) zu einem nationalen HL7 Standard.
Weitere Details zum Vorgehensmodell sind im Allgemeiner Leitfaden - Kapitel Leitfadenerstellungs- und Harmonisierungsprozess - Vorgehensmodell zu finden.
Dieser Implementierungsleitfaden ist eine Weiterentwicklung des Laborbefundes 2.06.3 und entstand durch die Harmonisierungsarbeit der AG Labor- und Mikrobiologiebefund, die im Zeitraum von [TODO] Oktober 2020 bis November 2020 tagte. Die Teilnehmer der Arbeitsgruppe wurden durch ihre Organisation delegiert.
Die Arbeitsgruppe harmonisierte primär die inhaltlichen Vorgaben und soweit möglich die zu verwendenden Terminologien (Value Sets). Die Formulierung der technischen Spezifikation des CDA Implementierungsleitfadens Labor- und Mikrobiologiebefund erfolgte durch die ELGA GmbH parallel bzw. nach der inhaltlichen Festlegung.
Der Leitfaden wird in einem technischen Abstimmungsverfahren durch die HL7 Austria ("Ballot") zu einem österreichischen Standard. Die Verbindlichkeit zur Anwendung soll durch eine Novellierung des Gesundheitstelematikgesetzes 2012, BGBl.I Nr.111/2012 begründet werden.
4.1 Revision der Leitfäden
Neue und geänderte Anforderungen sowie Verbesserungen können neue Versionen der bestehenden Spezifikationen notwendig machen.
Der CDA-Koordinator evaluiert in regelmäßigen Abständen, ob und welche Änderungen (etwa durch neue medizinische oder gesetzliche Anforderungen) notwendig sind. Aufgrund des Berichtes des CDA-Koordinators empfiehlt die ELGA GmbH die Erstellung von Revisionsversionen der bestehenden Leitfäden. Die geplanten Änderungen sollen mit den maßgeblichen Stakeholdern abgestimmt werden.
Neue Versionen, die "verpflichtende Elemente" (Sections oder Entries) neu einführen oder entfernen, sind "Hauptversionen", die jedenfalls über eine Durchführungsverordnung verbindlich gemacht und veröffentlicht werden. Andere Versionen sind "Nebenversionen". Alle verbindlichen Versionen sind auf www.gesundheit.gv.at zu veröffentlichen.
4.2 Autoren und Mitwirkende
Dieser Implementierungsleitfaden entstand durch die Harmonisierungsarbeit der "Arbeitsgruppe Labor- und Mikrobiologiebefund" bestehend aus nachfolgend genannten Personen. Die Arbeiten für den vorliegenden Leitfaden wurden von den Autoren gemäß dem Stand der Technik und mit größtmöglicher Sorgfalt erbracht.
4.2.1 Autoren
Das Redaktionsteam bestand aus folgenden Personen:
| Name | Organisation | Rolle |
|---|---|---|
| Mag. Dr. Stefan Sabutsch | ELGA GmbH, HL7 Austria | Autor, Herausgeber |
| Gabriel Kleinoscheg, MSc | ELGA GmbH | Autor |
| DI Andrea Klostermann | ELGA GmbH | Autor |
| DI Nikola Tanjga | ELGA GmbH | Autor |
| DI Oliver Kuttin | ELGA GmbH | Autor |
Unter Mitwirkung von: Stephan Rainer-Sablatnig (ELGA GmbH), Nina Sjencic, B.A. (ELGA GmbH)
4.2.2 Mitwirkende
Teilnehmer der Arbeitsgruppe Labor- und Mikrobiologiebefund1
Christoph Arndt (Roche), Christoph Aspöck (Landesklinikum St. Pölten, Institut für Hygiene und Mikrobiologie), Jeroen de Bruin (Medexter Healthcare GmbH), Christa Freibauer (Institut für Pathologie LK Mistelbach; ÖGPath), Joseph Gappmayer (medilab GmbH), Milo Halabi (Institut für klinische Pathologie, Mikrobiologie und molekulare Diagnostik Krankenhaus der Barmherzigen Schwestern Ried; ÖGPath), Alexander Haushofer (ÖGLMKC; Klinikum Wels-Grieskirchen), Markus Hell (Medilab - Laboratorium Dr. Mustafa, Dr. Richter OG), Günter Igler (Analyse BioLab; KH Elisabethinen Linz), Heidrun Kerschner (Analyse BioLab; KH Elisabethinen Linz), Gabriel Kleinoscheg (ELGA GmbH), Andrea Klostermann (ELGA GmbH), Christoph Koidl (MedUni Graz, Institut für Hygiene, Mikrobiologie und Umweltmedizin; BFG Med. Mikrobiologie und Hygiene), Kristiane Kousek (NÖ Landesklinken Holding), Johannes Möst (Österreichische Gesellschaft für Hygiene, Mikrobiologie und Präventivmedizin), Johannes Möst (Österreichische Gesellschaft für Hygiene, Mikrobiologie und Präventivmedizin), Hans Georg Mustafa (Labor Dr. Hans Georg Mustafa, BFG Med. u. Chem. Labordiagnostik, ÖGLMKC), Michael Nöhammer (ÖÄK), Tina Prager (NÖ Landesklinken Holding), Elisabeth Presterl (Universitätsklinik für Krankenhaushygiene & Infektionskontrolle, Medizinische Universität Wien), Stephan Rainer-Sablatnig (ELGA GmbH), Stefan Sabutsch (ELGA GmbH, HL7 Austria), Ulrich Sagel (Universitätsklinik für Hygiene und Mikrobiologie), Tamara Savic (KAGes, Institut für Krankenhaushygiene und Mikrobiologie), Carina Seerainer (ELGA GmbH), Nina Sjencic (ELGA GmbH), Nikola Tanjga (ELGA GmbH), Gerhard Weigl (Inst. f. Labormedizin – Klinik Penzing, Wien), Birgit Willinger (AKH, MedUni Wien, Klin.Inst.f.Labormedizin)
[TODO fehlen noch welche? auch die erwähnen, die per E-Mail mitgeholfen haben (z.B. bei Value Sets)?]
1 Personen sind in alphabetischer Reihenfolge ohne Titel angegeben.
4.2.3 Autoren und Mitwirkende vergangener Leitfadenversionen
Die erste Version dieses Implementierungsleitfadens (2.06) entstand durch die Harmonisierungsarbeit der "Arbeitsgruppe Laborbefund" im Zeitraum zwischen 2008 und 2012, bestehend aus den unten genannten Personen2.
Herausgeber, Editor, CDA Koordinator
Stefan Sabutsch (ELGA GmbH)
Autoren, Fachkoordinatoren und Moderatoren
Matthias Frohner (Fachhochschule Technikum Wien), Alexander Mense (Fachhochschule Technikum Wien, HL7 Austria), Stefan Sabutsch (ELGA GmbH, HL7 Austria), Stefan Sauermann (Fachhochschule Technikum Wien)
AG Teilnehmer
Bernhard Böhm (Vinzenz Gruppe Krankenhausbeteiligungs- und Management GmbH), Franz Burghuber (Kurienversammlung der niedergelassenen Ärzte der OÖ Ärztekammer), Christian Cebulla (KAV Wien, Generaldirektion), Georg Endler (Wilhelminenspital der Stadt Wien, Zentrallabor, KAV Wien), Manuela Födinger (KFJ – Sozialmed. Zentrum Süd, Institut für Laboratoriumsdiagnostik), Helmuth Gamper (Max management Consulting GmbH), Ferenc Gerbovics (Fachhochschule Technikum Wien), Bernhard Göbl (act Management Consulting GmbH), Andrea Griesmacher (Univ.Klin. Innsbruck, Zentralinst. Labordiagnostik), Walter-Michael Halbmayer (ÖQUASTA; KH Hietzing + NZ Rosenhügel, Institut f. Labordiagnostik), Susanne Hauptlorenz (LKH Vöcklabruck, Institut f. Med.Chem. Labordiagnostik u. Blutdepot), Alexander Haushofer (Österreichische Ärztekammer, KH St. Pölten, Inst. für Laboratoriumsmedizin), Jörg Hofmann (Österreichische Ärztekammer, Wiener KAV, Sozialmedizinisches Zentrum Ost - Donauspital, Institut für Labormedizin), Gerhard Holler (Österreichische Ärztekammer, ON-K 238), Konrad Hölzl (Wiener Krankenanstaltenverbund, KAV-IT), Wolfgang Hübl (KAV Wien, Wilhelminenspital, Zentrallabor, ÖGLMKC), Christof Jungbauer (Rotes Kreuz, Blutspendezentrale Wien), Christian Kampenhuber (GESPAG Gesundheitsinformatik-Bereichsleiter), Harald Kessler (Medizinische Universität Graz, Institut für Hygiene, Mikrobiologie und Umweltmedizin), Christian Kraml (Systema), Michael Krausenbaum (vision4health Deutschland GmbH & Co. KG), Walter Krugluger (Sozialmedizinisches Zentrum Ost), Thomas Leitha (Sozialmedizinisches Zentrum Ost), Herbert Matzenberger (Systema), Susanna Michalek (Initiative-ELGA), Helmut Mittermayer (Elisabethinen Linz), Georg Mustafa (Österreichische Ärztekammer, Bundesfachgruppe Labor), Georg Paucek (Medicon Medical Consulting), Johann Perné (Medizinisches Labor Perné), Gerald Regenfelder (KABEG), Dietmar Reiter (Tilak, Informationstechnologie/IT-Abteilung), Hans Richter (Labatech Handelsgesellschaft m.b.H.), Harald Rubey (LK Weinviertel Mistelbach, Laborinstitut, NÖ LK-Holding), Dieter Schwartz (Med. Uni. Wien, Klinik f. Blutgruppenserologie u. Transfusionsmedizin), Wolfgang Sischka (Assista Laborelectronics GmbH), Thomas Szekeres (Österreichische Ärztekammer), Beate Tiran (Kages Zentrallabor), Christoph Unfried (HCS, Health Communication Service), Philipp Urbauer (Fachhochschule Technikum Wien)
Patronanz, Akkordierung, Ergänzungen, Zustimmung
Clemens Auer (Bundesministerium für Gesundheit), Michael Danninger (Labene), Hubert Eisl (ELGA GmbH), Peter Fraunberger (Medizinisches Zentrallaboratorium GmbH), Josef Galler (Steiermärkische Krankenanstalten-ges.m.b.H.), Gerhard Gretzl (Solve Consulting), Ulrike Gruber-Mösenbacher (Landeskrankenhaus Feldkirch, Institut für Pathologie), Milo Halabi (Krankenhaus der Barmherzigen Schwestern Ried, Inst. f. Pathologie), Elisabeth Haschke-Becher (A.ö. Krankenhaus der Elisabethinen Linz, Institut für Medizinische und Chemische Labordiagnostik), Susanne Herbek (ELGA GmbH), Wolfgang Hiesl (Oö. Gesundheitsfonds / eHealth Management), Martin Hurch (ELGA GmbH), Stylianos Kapiotis (Med. Uni. Wien, Klinisches Institut für Medizinische und Chemische Labordiagnostik), Peter Konrath (B&S Zentrallabor), Oliver Kuttin (ELGA GmbH), Georg Lechleitner (Tilak, Abteilungsleiter Informationstechnologie/IT-Abteilung), Hubert Leitner (Steiermärkische Krankenanstalten-ges.m.b.H.), Helmut Lindorfer (Österreichische Agentur für Gesundheit und Ernährungssicherheit GmbH – AGES), Sabine Manhardt (Österreichische Ärztekammer, Sekretariat), Achim Mühlberger (GRZ IT Center Linz GmbH), Hans Georg Mustafa (Labor Dr. Hans Georg Mustafa, Fachgesellschaft Labormedizin), Michael Nebel (Gibodat EDV- und Organisationsberatungs GmbH), Susan Netzl (AUVA - Unfallkrankenhaus Meidling, Labor), Claudia Perndl (A.ö. Krankenhaus der Elisabethinen Linz, Institut für Medizinische und Chemische Labordiagnostik, EDV), Sven Plattner (BKH Hall in Tirol, EDV), Thomas Pöckl (NÖ Landeskliniken-Holding), Angelika Reiner-Concin (Sozialmedizinisches Zentrum Ost – Donauspital, Pathologisch-Bakteriologisches Institut), Alexander Schanner (NÖ Landesklinikenholding), Gerhard Schobesberger (Österreichische Ärztekammer, Labor Schobesberger), Peter Schöttel (Bartelt GmbH), Christian Schweiger (Medizinische Universität Wien / AKH Wien, klinische Abteilung für Medizinisch-chemische Labordiagnostik), Herbert Stekel (AKH Linz, Institut für Laboratoriumsmedizin), Romana Thiel (HCS, Health Communication Service), Peter Uher (Telekom Austria), Michael Weidenauer (Assista), Thomas Wrba (Medizinische Universität Wien)
Andere ELGA Arbeitsgruppen:
Entlassungsbrief Arzt und Pflege: Jürgen Brandstätter (CodeWerk Software Services and Development GmbH)
Befundbericht Radiologie: Andreas Lindner (Lindner TAC), Martin Weigl (AIMC)
AG Laborbefund 2017
Die Änderungen für Version 2.06.2 wurde von der AG Laborbefund am 12.1.2017 abgenommen. Teilnehmer der AG Laborbefund waren:
Maria Abzieher (Wiener Krankenanstaltenverbund), Robert Alscher (Humanomed IT Solutions Gmbh), Daniel Außerdorfer (Univ.Klin. Innsbruck, Zentralinstitut für Medizinische und Chemische Labordiagnostik (ZIMCL)), René Berger (Synlab), Barbara Dall (CGM), Zeljko Drljaca (Institut für medizinische und chemische Labordiagnostik Gesellschaft m.b.H), Daniela Eisner (Salzburger Landeskliniken ), Christian Fersterer (Salzburger Landeskliniken), Matthias Frohner (FH Technikum Wien), Josef Galler (Steiermärkische Krankenanstalten-ges. m.b.H.), Andrea Griesmacher (Univ.Klin. Innsbruck, Zentralinstitut für Medizinische und Chemische Labordiagnostik (ZIMCL)), Gernot Gruber (Institut für medizinische und chemische Labordiagnostik Gesellschaft m.b.H), Sylvia Handler (biomed austria - Österreichischer Berufsverband der Biomedizinischen AnalytikerInnen), Susanne Hauptlorenz (Salzkammergut-Klinikum Vöcklabruck, Institut für Med.Chem. Labordiagnostik und Blutdepot), Alexander Haushofer (ÖGLMKC; Klinikum Wels-Grieskirchen), Wolfgang Hießl (Oö. Gesundheitsfonds / eHealth Management), Michael Hubmann (Med. Zentrallaboratorium GmbH), Günter Igler (Analyse BioLab; KH Elisabethinen Linz), Sonja Jansen-Skoupy (KAV Wien, SMZ Süd), Michael Krausenbaum (CGM LAB Deutschland GmbH), Herwig Loidl (Carecenter Software GmbH), Birgit Luxbacher (biomed austria - Österreichischer Berufsverband der Biomedizinischen AnalytikerInnen), Clemens M. Sampl (BMGF), Herbert Matzenberger (CompuGroup Medical CEE GmbH), Alexander Mense (Fachhochschule Technikum Wien, HL7 Austria), Hans Georg Mustafa (Labor Dr. Hans Georg Mustafa, BFG Med. u. Chem. Labordiagnostik, ÖGLMKC), Stefan Mustafa (Labor Doz. Mag. DDr. Stefan Mustafa), Michael Nöhammer (Ärztekammer Österreich), Thomas Pöckl (NÖ Landeskliniken-Holding), Elisabeth Presterl (Universitätsklinik für Krankenhaushygiene & Infektionskontrolle, Medizinische Universität Wien), Sebastian Reimer (BMGF), Harald Rubey (LK Weinviertel Mistelbach, Laborinstitut, NÖ LK-Holding), Stefan Sabutsch (ELGA GmbH, HL7 Austria), Ulrich Sagel (Universitätsklinik für Hygiene und Mikrobiologie), Karin Salzmann (Univ. Klinik für Innere Medizin Innsbruck), Stefan Sauermann (FH Technikum Wien, Interoperabilitätsforum Österreich), Peter Schöttel (Bartelt GmbH), Christian Schweiger (Medizinische Universität Wien / AKH Wien, klinische Abteilung für Medizinisch-chemische Labordiagnostik), Carina Seerainer (ELGA GmbH), Josef Seier (Klinikum Wels-Grieskirchen), Wolfgang Sischka (Assista Laborelectronics GmbH), Herbert Stekel (Kepler Universitätsklinikum GmbH), Michael Svizak (AUVA Hauptstelle - Ärztliche Direktion), Gerhard Weigl (Inst. f. Labormedizin – Otto-Wagner-Spital Wien)
2 Personen sind in alphabetischer Reihenfolge ohne Titel angegeben.
5 Technischer Hintergrund
Der technische Hintergrund soll im allgemeinen Leitfaden nachgelesen werden.
6 Allgemeine Richtlinien für ELGA CDA-Implementierungsleitfäden
Die allgemeinen Richtlinien für CDA-Implementierungsleitfäden sollen beachtet werden.
7 Konformitätsprüfung
Ein zu diesem Implementierungsleitfaden konformes CDA-Dokument ist zunächst ein valides CDA Release 2.0 XML-Dokument mit Header und Body. Darüber hinaus erfüllt es alle in diesem Leitfaden festgelegten "Geschäftsregeln".
Dies spiegelt ein generelles Konzept im Umgang mit Dokumenten wieder: die Validierung in zwei Schritten. Im ersten Schritt stellt dies die Validierung gegen zugehörige W3C Schemas dar. Das verwendete Schema ist das geringfügig erweiterte offizielle CDA Release 2.0 Schema (siehe Schema-Prüfung). Darüber hinaus existieren eine Reihe von Schematron Regeln, die für einen zweiten Validierungsschritt genutzt werden und letztlich die Detailregelungen in diesem Leitfaden wiedergeben, sowie die Einhaltung der Geschäftsregeln (Optionalität, Kardinalität/Multiplizität, Datentypen, Wertebereiche, Abhängigkeiten) sicherstellen (siehe Schematron-Prüfung). Geschäftsregeln für Abschnitte oder Elemente werden auch technisch zu "Templates" zusammengefasst. Eine XML-Instanz, die kein valides CDA-Dokument ist oder sich nicht gegen das XSD-Schema validieren lässt oder im Widerspruch zu den angegebenen Geschäftsregeln steht, ist kein gültiges CDA-Dokument im Sinne dieses Implementierungsleitfadens.
Hinweis: Nicht alle Geschäftsregeln können mit Schema oder Schematron geprüft werden (etwa Inhalte von Multimedia-Attachments, Dokumentengröße). Zusätzliche Validierungsschritte sind gegebenenfalls notwendig, um alle Regeln zu überprüfen zu können.
Die Kapitel zu den technischen Konformitätsprüfungen von CDA-Dokumenten, gemäß diesem Dokumentleitfadens mittels Schema und Schematron, sind im allgemeinen Leitfaden unter den folgenden Links zu finden:
8 Datentypen
Im Kapitel Datentypen des allgemeinen Leitfadens werden nur die Datentypen beschrieben, die in ELGA CDA-Dokumenten wie diesem zur Anwendung kommen. Für weiterführende Informationen wird auf den zugrundeliegenden Standard Health Level Seven Version 3 (V3), Normative Edition verwiesen.
9 Vorgaben zum medizinischen Inhalt
9.1 Labor- und Mikrobiologiebefund
Die inhaltliche Definition beruht auf den Mindestvorgaben der österreichischen Gesellschaft für Labormedizin und klinischen Chemie (ÖGLMKC) und wurden weiter verfeinert. Die folgende Tabelle zeigt einen Überblick über die inhaltlich abzubildenden medizinisch relevanten Daten.
| Feld | Beschreibung | Bereich |
|---|---|---|
| Allgemeine Befundinformationen | ||
| Zeitpunkt der Auftragserfassung | Datum und Zeitpunkt, an dem das analysierende Labor die Anforderung vom Zuweiser in der Labor-EDV erfasst hat. | Header |
| Auftragsdiagnose (Zuweiserdiagnose) bzw. Überweisungsgrund | Vom Auftraggeber bestimmte und dem Labor übermittelte Verdachtsdiagnose bzw. der Überweisungsgrund | Body |
| Angeforderte Untersuchung bzw. Fragestellung | Vom Auftraggeber angeforderte Untersuchungen, das angeforderte Analysespektrum bzw. die Fragestellung | Body |
| Befundtext | Kommentar zum gesamten Befund | Body |
| Spezimeninformation | ||
| Zeitpunkt der Spezimengewinnung | Damit ist jenes Datum und Zeitpunkt gemeint, an dem das Spezimen zur Analyse gewonnen wurde. Die Dokumentation des Zeitpunkts der Spezimengewinnung ist in der Verantwortung der entnehmenden Person, die in vielen Fällen mit dem Befundersteller nicht identisch ist, weil meist Spezimen zur Analyse an Labors versendet werden. Daher ist der Zeitpunkt vielfach im Labor nicht feststellbar. | Body |
| Zeitpunkt des Einlangens des Spezimen | Datum und Zeit der Probenannahme im Labor | Body |
| Art des Spezimens (Specimen Type) | Art der Probe (=Materialart) | Body |
| Entnahmeort | Angabe der Körperstelle, von der das Spezimen stammt | Body |
| Entnahmeart (SpecimenCollectionProcedure) [TODO Wie wird diese dargestellt?] | Art der Gewinnung | Body |
| Specimen ID | Eindeutige Nummer des Spezimen | Body |
| Entnehmende Person (Performer) | Person, welche die Entnahme der Probe durchgeführt hat | Body |
| Kommentar zum Spezimen | Präanalytik pro Spezimen zur Spezimenqualität | Body |
| Allgemeine Anmerkungen des Labors zur Spezimenqualität | Textinformationen zur Spezimenqualität | Body |
| Allgemeine Laborergebnisse | ||
| Gruppierung / Befundgruppen (Organizer) | Analysengruppierung | Body |
| ID des Tests | Eindeutige Codierung des Tests | Body |
| Analysenbezeichnung | Bezeichnung der Analyse | Body |
| Ergebnis | Body | |
| Einheit | Body | |
| Referenzbereiche | Für die Beurteilung relevante Referenzwerte. | Body |
| Befundinterpretation | Codierte Bewertung des Ergebnisses | Body |
| Ergebniskommentar | Kommentar des Labors zu einem einzelnen Testergebnis | Body |
| Externes Labor | Kennzeichen ob ein Ergebnis extern ermittelt wurde | Body |
| Kulturergebnisse | ||
| Erreger1 (Isolat) | Der durch eine Kulturmethode ermittelte Erreger. | Body |
| Antibiogramm (inklusive MHK) | Ergebnis der Bestimmung der Empfindlichkeit bzw. Resistenz von Erregern gegenüber Antibiotika. Anlassbezogen wird das Ergebnis interpretiert (R, S, I) und/oder die minimale Hemmkonzentration (MHK) angegeben. | Body |
1 Erreger oder Krankheitserreger sind Stoffe oder Organismen, die in anderen Organismen potenziell gesundheitsschädigende Abläufe verursachen können.
9.2 Allgemeiner Laborbefund
9.2.1 Befundbereiche (Laboratory Specialty Section)
Der Laborbefund kann mehrere unterschiedliche Teilbefunde aus verschiedenen Bereichen im Body des Dokumentes beinhalten (z.B. Hämatologie oder Urindiagnostik oder beide Arten gemeinsam). Das heißt, diese Teilbefunde bilden die erste Gliederungsebene des Bodys - die "Befundbereiche" oder - in Anlehnung an die Definitionen der "IHE" - "Laboratory Specialty Section" (vgl. [TODO Referenz]). Folgende Grafik zeigt die mögliche Gliederung auf der ersten Ebene innerhalb des Bodys.
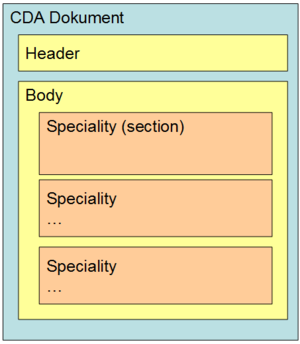
Die derzeit für den Laborbefund definierten Befundbereiche werden im Rahmen des hierarchisch organisierten Value Sets "ELGA_Laborstruktur" definiert, wobei für Befundbereiche nur Einträge der Ebene 1 verwendet werden dürfen. Die folgende Tabelle gibt einen auszugsweisen Überblick über die derzeit festgelegten Befundbereiche. Bei der Verwendung der Befundbereiche ist die Reihenfolge gemäß Value Set verpflichtend einzuhalten. Die Anwendung der Befundbereiche ist optional, denn es können auch alle Untersuchungen in einer einzelnen "Laboratory Specialty Section" unter dem Befundbereich "Allgemeiner Laborbefund" (Ebene 0 in Value Set "ELGA_Laborstruktur") zusammengefasst werden.
[TODO (GKL) Ist dieser Text obsolet, weil es nur mehr Full Support gibt?]
Für EIS "Enhanced" ist die Codierung der Bereiche (als unterschiedliche section-Elemente) zwingend vorgeschrieben.
| Code | Befundbereich (Laboratory Speciality Section) |
|---|---|
| 100 | Blutgruppenserologie |
| 200 | Blutgasanalytik |
| 300 | Hämatologie |
| 400 | Gerinnung/Hämostaseologie |
| … | … |
9.2.2 Befundgruppen
Innerhalb der Befundbereiche erfolgt in der Regel eine Strukturierung und Gliederung der Ergebnisse zur besseren Lesbarkeit und Auffindbarkeit in "Befundgruppen". Die dritte Ebene des ELGA Value Sets "ELGA_Laborstruktur" definiert zulässige Befundgruppen. Grundsätzlich ist die Reihenfolge der Befundgruppen gemäß Value Set verpflichtend einzuhalten. Es besteht jedoch auch die Möglichkeit, Ergebnisse ohne Befundgruppenstrukturierung zu übermitteln.
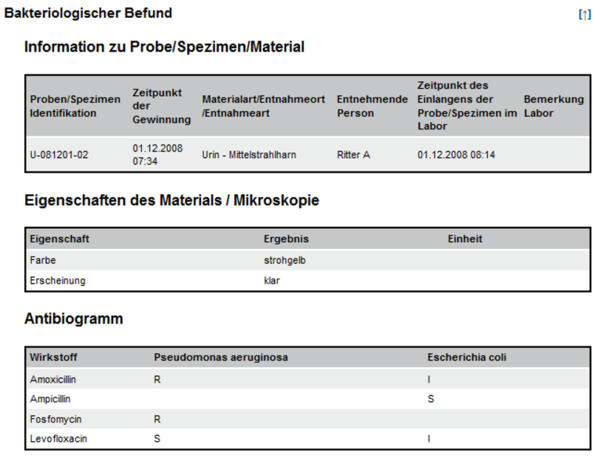
Der folgende Ausschnitt aus einem Laborbefunden enthält die Befundbereiche "Hämatologie" und "Hämostaseologie" sowie die dazugehörigen Befundgruppen "Blutbild", "Knochenmark Morphologie" bzw. "Hämostaseologie Globaltest".
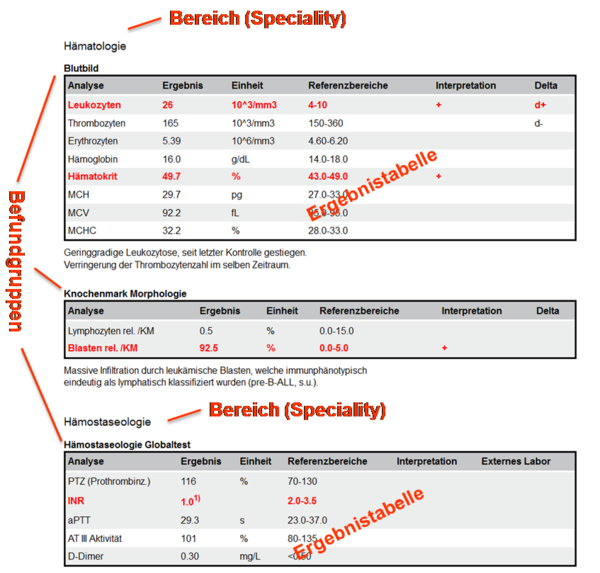
9.2.3 Harmonisierung des Befundaufbaus – Value Set "ELGA_Laborparameter"
Im Rahmen der Arbeiten zum vorliegenden Dokument wurde in der Expertengruppe die grundsätzliche Übereinkunft getroffen, auch die Befundgruppen und die damit verbundene Testzuordnung entsprechend österreichweit abzustimmen. Die Strukturierung eines Laborbefundes wurde in Form des hierarchischen Value Sets "ELGA_Laborparameter" festgelegt.
Strukturierung, Reihenfolge der Parameter sowie die Bezeichnung der Parameter sind durch das Value Set "ELGA_Laborparameter" verpflichtend vorgegeben!
Eine Hilfestellung zum Mapping der lokalen Codes auf die vorgeschriebenen Codes des Value Sets bietet der "Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund"[24].
9.3 Mikrobiologiebefund
Unter den Analysen des Laborbefundes finden sich viele aus dem Bereich der Mikrobiologie. Grundsätzlich können alle Analysen auch in der "klassischen" Struktur des Laborbefundes dargestellt werden (siehe Laborbefund). Allerdings entspricht die Struktur des Laborbefundes nicht dem eines üblichen Mikrobiologiebefundes, der einem bestimmten Muster folgt, welches den Untersuchungsverlauf widerspiegelt:
- Beschreibung des entnommenen Materials (z.B. Mittelstrahlharn) inklusive makroskopischer Beurteilung
- Mikroskopische Untersuchung des Materials (z.B. Erythrozyten, Leukozyten, grampositive Bakterien)
- Kultureller Erregernachweis
- Benennung der Reinkulturen (Isolate) mit Nennung der taxonomischen Bestimmung der Mikroorganismen (z.B. Streptococcus pyogenes) ggf. mit Angabe des Serovars/Pathovars.
- Angabe des Antibiogramms mit Interpretation (R, S, I) und/oder minimaler Hemmkonzentration (MHK)
- Molekulare Erregernachweise
- Infektionsserologie
Die Struktur des Mikrobiologiebefundes wird durch "Laboratory Specialty Sections", die jeweils mit einem fixen Code versehen sind, vorgegeben. Details dazu sind dem Document Level Template des Mikrobiologiebefundes zu entnehmen.
[TODO vermutlich nicht mehr notwendig] 
9.4 Hinweise für akkreditierte Laboratorien gem. ISO 15189:2012
TODO (GKL): Aktuelle Version ist ISO 15189:2014 - ausbessern? passen Kapitel in Nummer/Überschrift dann noch zusammen?
Die Vorgaben dieses Implementierungsleitfadens erlauben die Erzeugung von Befunden gemäß ISO 15189:2012 "Medizinische Laboratorien - Anforderungen an die Qualität und Kompetenz"[25], speziell in Hinblick auf die dort angegebenen Kapitel 5.8 (Befundberichte) und 5.9 (Freigabe der Ergebnisse). Für akkreditierte Laboratorien sind neben der ISO 15189:2012 folgende Hinweise zu beachten:
9.4.1 Angabe des Akkreditierungs-Logos
Das Akkreditierungs-Logo kann neben dem Logo des Labors angegeben werden. Technisch erfolgt das über die Sektion "Brieftext", das Logo ist ggf. gemeinsam mit dem Logo des Labors in einer Grafikdatei anzugeben (siehe Brieftext).
TODO (GKL) ggf. noch Screenshot mit aktuellem Stylesheet

Ein Labor muss nicht zwingend für alle Analysen, die es durchführen kann, akkreditiert sein. Das Akkreditierungs-Logo kann angegeben werden, sobald es akkreditierte Analysen gibt; wenn "nicht akkreditierte Analysen" am Befund erscheinen, soll bei diesen angegeben werden können, dass das Labor für diese Analyse nicht akkreditiert ist. Für die entsprechend Markierung wird die Verwendung von Anmerkungszeichen (wie z.B. *) und Endnoten empfohlen.
9.4.2 Angabe des Untersuchungs- bzw. Messverfahrens
Wenn der Name der Analysen keinen Rückschluss auf die Methode erlaubt, aber Untersuchungs- bzw. Messverfahren dennoch angegeben werden sollen (ISO 15189:2012, Vorgabe 5.8.3 a)), soll dies als Kommentar zur Analyse erfolgen (siehe TODO Link/Kapitel auflösen: Bemerkungen_zu_Analysen_oder_Analyseergebnissen|Bemerkungen zu Analysen oder Analyseergebnissen).
9.4.3 Vorgaben für den Befunddruck
Einige Vorgaben von ISO 15189:2012 beziehen sich auf Qualitätsmerkmale für gedruckte Befunde (Vorgabe 5.8.3 d) "Identifizierung des Patienten und den Aufenthaltsort des Patienten auf jeder Seite" und Vorgabe 5.8.3 p) "Seitenzahl zur Gesamtzahl der Seiten"). Dieser Leitfaden definiert ein elektronisches Format, das diese Anforderungen grundsätzlich unterstützt. Am ELGA-Portal (Zugriff für Bürger) werden Tools zur Darstellung eingesetzt, die diese Vorgaben unterstützen. Diese Tools werden auch von der ELGA GmbH zum Download bereitgestellt (Referenzstylesheet, CDA2PDF auf http://www.elga.gv.at/CDA).
10 Funktionale Anforderungen
10.1 Voraussetzungen für den Zugriff auf e-Befunde in ELGA
Der ELGA GDA ist in ELGA angemeldet, berechtigt und besitzt eine gültige Kontaktbestätigung für den Patienten. Der Patient ist ELGA-Teilnehmer und hat keinen generellen, partiellen oder situativen Widerspruch hinsichtlich ELGA eingelegt.
10.2 Anwendungsfälle des Dokumentenmanagements
Die folgenden Kapiteln aus dem allgemeinen Leitfaden stellen eine Zusammenfassung der Inhalte der ELGA-Gesamtarchitektur, des Leitfadens XDS Metadaten und Usability Styleguides zum Thema e-Befunde dar. Detailinformationen sind in den entsprechenden Dokumenten nachzulesen (verfügbar auf der Homepage der ELGA GmbH). Die wesentlichen Anwendungsfälle sind
- Schreiben und Einbringen von Dokumenten
- Versionierung von Dokumenten
- Stornierung von Dokumenten
- Filtern und Suchen von Dokumenten
- Lesen von Dokumenten
10.2.1 Dokument-Metadaten (XDS-Metadaten)
| XDS-Element mit Link zum XDS-Leitfaden | Optionalität im XDS-Leitfaden | CDA-Element in /ClinicalDocument | Werte mit Beispielen | Erklärung | |
|---|---|---|---|---|---|
| uniqueId | M | ./id |
|
Das uniqueId Element beschreibt den global eindeutigen Identifier des Dokuments und kann mit oder ohne Extension angegeben werden. | |
| |||||
| typeCode | R | ./code |
|
Zur Unterscheidung des "Dokumenttyps" erhält das "code"-Elementes des "Laborbefundes" ein vorgegebenes "code"-Element. | |
|
Zur Unterscheidung des "Dokumenttyps" erhält das "code"-Elementes des "Mikrobiologiebefundes" ein vorgegebenes "code"-Element. | ||||
| classCode | R | ./code/translation |
|
Bezeichnet die "Dokumentklasse" in dem untergeordneten "translation"-Element. Einzig zulässige Wert für Labor- und Mikrobiologiebefund ist Laboratory report (11502-2). | |
| title | R | ./title |
|
Der Titel des CDA Dokuments für den lesenden Empfänger. MUSS die Art des Dokuments (Dokumenttyp) widerspiegeln.
Vorgeschlagene Titel wären zum Beispiel "Laborbefund" oder "Mikrobiologiebefund". | |
| formatCode [TODO] | M | ./hl7at:formatCode |
|
Version des vom CDA erfüllten ELGA Labor- und Mikrobiologiebefund Implementierungsleitfadens. | |
| practiceSettingCode | M | ./hl7at:practiceSettingCode |
|
Fachliche Zuordnung des Dokuments. | |
| creationTime | M | ./effectiveTime |
|
Dokumentiert das Erstellungsdatum bzw. den Zeitpunkt, an dem das Dokument inhaltlich fertiggestellt wurde. | |
| confidentialityCode | M | ./confidentialityCode |
|
Vertraulichkeitscode des Dokuments. Für ELGA-Dokumente ist ausschließlich "N" erlaubt! | |
| languageCode | M | ./languageCode |
|
Für ELGA ist in @code für CDA und Ableitungen in die XDSDocumentEntry-Metadaten derzeit ausschließlich der Wert "de-AT" zulässig. Für eHealth können in zukünftigen Versionen des Leitfadens weitere Sprachcodes erlaubt werden. | |
| referenceIdList | M | ./setId |
|
Eindeutige ID des Dokumentensets. Diese bleibt über alle Versionen der Dokumente gleich (initialer Wert bleibt erhalten). Die setId SOLL unterschiedlich zu /ClinicalDocument/id sein. | |
| sourcePatientId | M | ./recordTarget/patientRole/id[1] |
|
Patienten ID im Informationssystem des GDA, z.B.: im KIS eines Krankenhauses. | |
| author | authorInstitution | M | ./author[1]/assignedAuthor/
representedOrganization/id[1] |
|
ID und Name der Organisation (Kurzbezeichnung), der die Person angehört, wie im GDA-Index angegeben. |
| |||||
| ./author[1]/assignedAuthor/
representedOrganization/name |
| ||||
| authorPerson | M | ./author[1]/assignedAuthor |
|
Daten der Person (Name, ID, etc.) | |
| authorRole | M | ./author[1]/functionCode |
|
Rolle der Person. | |
| authorSpeciality | M | ./author[1]/assignedAuthor/code |
|
Fachrichtung des Verfassers des Dokuments aus ELGA_AuthorSpeciality. | |
| legalAuthenticator | M | ./legalAuthenticator/assignedEntity |
|
Rechtlicher Unterzeichner des Dokuments. | |
| eventCodeList | R | ./documentationOf[n]/serviceEvent/code |
|
Code der Gesundheitsdienstleistung. | |
| serviceStartTime | R | ./documentationOf[1]/serviceEvent/
effectiveTime/low |
|
Zeitpunkt des Behandlungsbeginns (erster medizinisch relevanter Behandlungstag dieser dokumentierter Gesundheitsdienstleistung) | |
| serviceStopTime | R | ./documentationOf[1]/serviceEvent/
effectiveTime/high |
|
Zeitpunkt des Behandlungsendes (letzter medizinisch relevanter Behandlungstag dieser dokumentierter Gesundheitsdienstleistung, muss sich von Behandlungsbeginn unterscheiden) | |
| healthcareFacilityTypeCode | R | ./componentOf/encompassingEncounter/
location/healthCareFacility/code |
|
Klassifizierung des GDA. | |
11 Anwendungsfälle
Die Einsatzszenarien für dieses Datenaustauschformat werden in Form von Anwendungsfälle beschrieben, um dem Leser den Hintergrund zu vermitteln. Diese Beschreibung der Anwendungsfälle ist nicht normativ und keine Vorentscheidung für die tatsächliche Umsetzung.
TODO: Die Definition in passendes Kapitel verschieben.
Definition: Der Laborbefund wurde für die Arbeit an diesem Leitfaden wie folgt definiert:
Ein Laborbefund (aus dem Bereich der med. u. chem. Labordiagnostik) ist der fachärztlich vidierte, kommentierte/interpretierte Befund morphologischer, biologischer, chemischer, molekularer, physikalischer und spezieller immunologischer Untersuchungsverfahren aus Körpersäften, der Beurteilung ihrer morphologischen Bestandteile sowie von ab- und ausgeschiedenem Untersuchungsmaterial zur Erkennung physiologischer Eigenschaften, krankhafter Zustände, zu Verlaufskontrollen und zur Gesundheitsvorsorge/Prophylaxe.
ELGA Laborbefunde umfassen u. a. klinische Chemie und Immunchemie, Hämatologie (Erkrankungen des Blutes) und Hämostaseologie (Störungen der Blutgerinnung), Proteinchemie, Serologie, molekulare Diagnostik, Toxikologie, Drugmonitoring, Mikrobiologie, Infektionsserologie, Zytologie, Untersuchungen und die Hilfestellung für andere Fächer im Rahmen von Therapievorschlägen bei Gerinnungsstörungen, Antikoagulanzientherapien, der Impfkontrolle, Vorsorgediagnostik und Risikostratifizierung.
Untersuchungen des Sonderfaches "Blutgruppenserologie und Transfusionsmedizin" werden in einer gesonderten ELGA Dokumentenklasse (geplant) abgehandelt.
Sofern keine andere Regelung zutrifft, obliegt die Entscheidung ob ein Befund in ELGA gestellt wird dem Befundersteller.
Im ELGA Laborbefund dürfen nur dann Ergebnisse aus genetischen Analysen enthalten sein, wenn ihre Dokumentation in Übereinstimmung mit dem Gentechnikgesetz (GTG § 71a, BGBl. I Nr. 127/2005) erfolgt.
Der in diesem Leitfaden beschriebene Laborbefund dient also zum Austausch von fertiggestellten, und fachärztlich vidierten Befunden innerhalb und zwischen Einrichtungen des Gesundheitswesens. Ein wesentlicher Nutzer der Befunde ist auch der Patient selbst, der die Befunde über das ELGA Bürgerportal einsehen wird.
Der in diesem Leitfaden beschriebene Laborbefund ist zur Dokumentation und Kommunikation (vollständig) fertiggestellter Laborbefunde gedacht.
Der hier beschriebene Laborbefund ist nicht vorgesehen um Zwischenergebnisse und Nachrichten über einzelne Prozessschritte zu kommunizieren, wie etwa
- die Anforderung von Laboruntersuchungen
- das Einlangen einer Probe im Labor
- den Beginn, Stornierung oder die Fertigstellung einzelner Untersuchungen
Ergänzungen und Korrekturen von Laborbefunden werden unterstützt
11.1 Anwendungsfall LAB01: "Laboruntersuchung eines niedergelassenen Labors"
Typischerweise entstehen Laborbefunde in medizinischen Labors. Einerseits sind das niedergelassene Labors, die als selbständige Unternehmen Laboruntersuchungen anbieten. Diese werden vielfach auf Zuweisung von Patienten durch praktische Ärzte im niedergelassenen Bereich tätig. Die Entstehung eines Laborbefundes beginnt mit einer Überweisung durch einen niedergelassenen Arzt, oder mit einer Anforderung innerhalb eines Spitals. Entweder wird das Spezimen am Patienten gleichzeitig entnommen, und dann ins Labor geschickt oder der Patient muss das Labor aufsuchen, und das Spezimen wird dann erst dort entnommen. Nach Abschluss der Untersuchung wird der Befund dem zuweisenden Arzt und/oder dem Patienten in Papierform übermittelt.
Laboruntersuchungen im Rahmen ambulanter Aufenthalte in einem Spital fallen ebenso unter diesen Anwendungsfall.
11.2 Anwendungsfall LAB02: "Laboruntersuchung im Rahmen eines stationären Aufenthalts in einem Spital"
Im Rahmen von stationären Aufenthalten von Patienten in Spitälern kommt es in der Regel zu einer Reihe von Laboruntersuchungen, die in der internen Krankengeschichte (meistens auch elektronisch) abgelegt werden. Relevante Befunde werden dem einweisenden Arzt bzw. dem Patienten im Zuge der Entlassungsdokumentation mit übermittelt. Dieses passiert oftmals als Teil des Entlassungsbriefes. Welche Werte und welche Befunde entsprechende Relevanz haben um weitergeleitet zu werden, entscheidet das jeweilige ärztliche Fachpersonal in der Klinik.
11.3 Anwendungsfall LAB03: "Teilweise externe Vergabe von Laboruntersuchungen"
In vielen Fällen kommt es zu Kooperationen zwischen Laborbefund erstellenden Organisationen. Folgende Fälle seien angeführt:
- Spitäler kooperieren mit niedergelassenen Labors. Zum Teil verfügen nicht alle Spitäler über eigene Labors, andererseits werden auch Spezialuntersuchungen, die das Spitalslabor nicht durchführt, an niedergelassene Labors vergeben.
- Niedergelassene Labors verfügen nicht über das volle Leistungsspektrum und senden Laboruntersuchungen an Spitallabors, welche spezielle Parameter messen können.
- Es bestehen Kooperationen zwischen mehreren Spitälern. Einerseits sind das oft Spitäler, die dem gleichen Spitalsträger angehören. Teilweise bestehen auch Kooperationen zwischen Spitälern unterschiedlicher Träger, die durch die örtliche Nähe leicht Proben austauschen können.
In allen Fällen werden einzelne Labortests nicht selbst durchgeführt sondern diese Tests an ein externes kooperierendes Labor vergeben. Das externe Labor führt dann den Test durch, und übermittelt die Ergebnisse an das ursprünglich für die Untersuchungen zuständige Labor. Dort werden dann die vom externen Labor ermittelten Testergebnisse in den eigenen Laborbefund eingefügt. Das ursprünglich zuständige Labor, das den Befund erstellt, muss in diesem Fall die extern erbrachten Testergebnisse als solche erkennbar kennzeichnen.
11.4 Anwendungsfall LAB04: "Update von Laborbefunden"
Ein fertiggestellter Laborbefund wird korrigiert oder ergänzt, um
- die Inhalte des Befundes zu korrigieren (etwa das Ergebnis einer Analyse),
- einzelne (fehlerhafte) Analysen nachträglich aus dem Befund zu stornieren oder
- fehlende Analysen zu ergänzen (etwa besonders lang dauernde Analysen).
Änderungen sollen im Text für den Leser klar kenntlich gemacht werden (eine codierte Angabe kann im narrativen Text mit Revisionsmarken erfolgen).
Eine Korrekturversion MUSS in ELGA immer alle zum Befund gehörigen Analysen enthalten, da die Vorversion als veraltet (deprecated) gekennzeichnet wird. Stornierte Analysen sind explizit mit dem entsprechenden StatusCode zu kennzeichnen.
Für den Leser/Empfänger gilt: Eine neue Version ersetzt die alte Version des Befundes, alle Analysen sollen beim Import ersetzt bzw. überschrieben werden. Sollte eine Analyse in der neuen Version fehlen, soll diese als "storniert" interpretiert werden.
12 Dataset des Labor- und Mikrobiologiebefunds
Das Dataset (auch "Datenarten" oder "Konzepte") listet alle mit der Arbeitsgruppe abgestimmten Inhalte des Leitfadens auf. Es enthält Beschreibungen der Elemente mit Synonymen.
Dataset-Elemente können auf das CDA Datenmodell gemappt werden. In den Metadaten eines Templates sind alle assoziierten Konzepte auf einen Blick ersichtlich. Im Template-Body wird das assoziierte Konzept beim entsprechenden Datenelement angezeigt.
Die Live-Version des Datasets in Art-Decor kann unter folgendem Link betrachtet werden.
13 Technische Spezifikation
Die Struktur des CDA Austauschformats ist in den nachfolgenden Kapiteln im Detail beschrieben.
Der Header entspricht mit Ausnahme der erwähnten Abweichungen den bisherigen ELGA CDA-Leitfäden ("Allgemeiner Leitfaden"). Der Body enthält die tatsächlichen (medizinischen) Inhalte des Dokuments. Dieses Dokument existiert ausschließlich in einer voll strukturierten Form, eine Unterscheidung der Interoperabilitätsstufen ist daher nicht notwendig.
13.1 Übersichtstabelle der CDA Strukturen des Headers
Dieses Kapitel gibt einen Überblick über die Elemente des CDA Headers und den Vorgaben bezüglich Kardinalität und Konformität.
Die jeweiligen Links in der letzten Spalte zeigen auf die einzelnen Header Elemente im allgemeinen Leitfaden.
Der aktuelle Leitfaden ist für den ELGA Kontext entwickelt worden, kann jedoch auch für andere Zwecke, welche als eHealth zusammengefasst werden, verwendet werden.
[TODO (GKL) wie funktioniert das im eHealth-Bereich, dass die Kardinalitäten/Konformitäten anders sind? Das bedeutet doch, dass im eHealth-Bereich nicht auf das Schematron bzw. Online-Validator zurückgegriffen werden kann, oder?]
| Element | Kard/Konf ELGA | Kard/Konf eHealth | Bedeutung / Link zum Kapitel |
|---|---|---|---|
| realmCode | 1..1 M | 1..1 M | Hoheitsbereich des Dokuments |
| typeId | 1..1 M | 1..1 M | Kennzeichnung CDA R2 |
| templateId | 3..* M | 3..* M | Kennzeichnung von Strukturvorschriften |
| id | 1..1 M | 1..1 M | Dokumenten-Id |
| code
translation |
1..1 M
1..1 M |
1..1 M
0..* R |
Klassifikation des Dokuments (fein und grob) |
| title | 1..1 M | 1..1 M | Titel des Dokuments |
| sdtc:statusCode | 0..1 C | 0..1 O | Status des Dokuments |
| hl7at:terminologyDate | 1..1 M | 0..1 O | Terminologie-Datum des Dokuments |
| hl7at:formatCode | 1..1 M | 0..1 O | FormatCode des Dokuments |
| hl7at:practiceSettingCode | 1..1 M | 0..1 O | Fachliche Zuordnung des Dokuments |
| effectiveTime | 1..1 M | 1..1 M | Erstellungsdatum des Dokuments (medizinisch relevantes Datum) |
| confidentialityCode | 1..1 M | 1..1 M | Vertraulichkeitscode |
| languageCode | 1..1 M | 1..1 M | Sprachcode des Dokuments |
| setId
versionNumber |
1..1 M
1..1 M |
1..1 M
1..1 M |
Versionierung des Dokuments |
| recordTarget | 1..1 M | 0..1 C | Patient |
| recordTarget de-identified | 0..0 NP | 0..1 C | Anonymer oder pseudonymisierter Patient |
| author | 1..* M | 1..* M | Verfasser des Dokuments |
| dataEnterer | 0..1 O | 0..1 O | Personen der Dateneingabe |
| informant | 0..* O | 0..* O | Informant |
| custodian | 1..1 M | 1..1 M | Verwahrer des Dokuments |
| informationRecipient | 0..* O | 0..* O | Beabsichtigte Empfänger des Dokuments |
| legalAuthenticator | 0..* C | 0..* C | Rechtlicher Unterzeichner, wird im speziellen Leitfaden definiert. |
| authenticator | 0..* O | 0..* O | Weitere Unterzeichner |
| participant | 0..* O | 0..* O | Weitere Beteiligte (nähere Unterscheidung im entsprechenden Leitfaden) |
| inFulfillmentOf | 0..* O | 0..* O | Zuweisung und Ordermanagement |
| documentationOf
serviceEvent |
0..* O
1..1 M |
0..* O
1..1 M |
Gesundheitsdienstleistungen |
| relatedDocument | 0..1 O | 0..1 O | Bezug zu vorgehenden Dokumenten |
| authorization | 0..0 NP | 0..* O | Einverständniserklärung |
| componentOf
encompassingEncounter |
0..1 O
1..1 M |
0..1 O
1..1 M |
Patientenkontakt (Aufenthalt) |
[TODO Allgemeine Anmerkungen zur Tabelle]
- [TODO documentationOf müsste 1..* R sein, weil in der Tabelle zu den Zeitangaben im Header ist es auch 1..* R]
13.1.1 Labor- und Mikrobiologiebefund
Für den Labor- und Mikrobiologiebefund gibt es folgende Anpassungen hinsichtlich der Kardinalität/Konformität einzelner Header-Elemente.
| Element | Kard/Konf Laborbefund | Kard/Konf Mikrobiologiebefund | Bedeutung / Link zum Kapitel |
|---|---|---|---|
| informant | 0..0 NP | 0..0 NP | Informant |
| legalAuthenticator | 1..1 M | 1..1 M | Rechtlicher Unterzeichner |
| documentationOf
serviceEvent |
1..* M
1..1 M |
1..1 M
1..1 M |
siehe Spezifikation der Document Level Templates |
13.2 Übersichtstabelle der Header-Elemente für dokumenten-relevante Zeitpunkte/Zeitspannen
Dieses Kapitel gibt einen Überblick über die Elemente des CDA Headers mit Zeitangaben und ihre Zusammenhänge.
Die jeweiligen Links in der letzten Spalte zeigen auf die einzelnen Header Elemente im allgemeinen Leitfaden.
Der aktuelle Leitfaden ist für den ELGA Kontext entwickelt worden, kann jedoch auch für andere Zwecke, welche als eHealth zusammengefasst werden, verwendet werden.
| Element | Kard/Konf
ELGA |
Kard/Konf
eHealth |
Bedeutung | Link zum Kapitel |
|---|---|---|---|---|
| hl7at:terminologyDate | 1..1 M | 0..1 O | Das Datum, an dem die lokal zur Implementierung verwendeten Value Sets mit dem österreichischen Terminologieserver abgeglichen wurden, wird hier angegeben. | Terminologie-Datum des Dokuments |
| effectiveTime | 1..1 M | 1..1 M | Das letzte medizinisch relevante Datum, an welchem das Dokument medizinische Inhalte hinzugefügt worden sind. Kann im speziellen Leitfaden anders definiert werden. | Erstellungsdatum des Dokuments |
| recordTarget
birthTime |
1..1 M
1..1 R |
0..1 C
1..1 R |
Der Geburtstag des Patienten. | Patient |
| recordTarget
deceasedTime |
1..1 M
0..1 O |
0..1 C
1..1 R |
Das Sterbedatum des Patienten. | Patient |
| author
time |
1..* M
0..1 R |
1..* M
0..1 R |
Das jeweilige Datum, an welche der jeweilige Autor neue medizinische Informationen hinzugefügt hat. | Verfasser des Dokuments |
| dataEnterer
time |
0..1 O
0..1 R |
0..1 O
0..1 R |
Das Datum, an welchem eine Schreibkraft die Informationen aus einem Medium in das CDA Dokument überträgt, ohne weitere fachliche Informationen hinzuzufügen. | Personen der Dateneingabe |
| legalAuthenticator
time |
0..* C
1..1 R |
0..* C
1..1 R |
Die Zeitpunkte, an welchem das Dokument von den einzelnen berechtigten Personen vidiert wurde. Diese Personen sind die Hauptunterzeichner. Ist im jeweiligen speziellen Implementierungsleitfaden genauer vorgeschrieben. Dieser Zeitpunkt, wenn vorhanden, sollte nach author.time und dataenterer.time liegen. | Rechtlicher Unterzeichner |
| authenticator
time |
0..* O
1..1 R |
0..* O
1..1 R |
Die Zeitpunkte, an welchem das Dokument von den einzelnen berechtigten Personen vidiert wurde. Diese Personen sind die weiteren Unterzeichner. | Weitere Unterzeichner |
| Notfallkontakt / Auskunftsberechtigte Person
participant [templateId[@root='1.2.40.0.34.6.0.11.1.27']] time |
0..* O
0..1 O |
0..* O
0..1 O |
Zeitraum, in dem der angegebene Kontakt den Notfall-Kontakt darstellt.
Wird nur angegeben, wenn der Kontakt bereits absehbar nur in einem eingeschränkten Zeitraum zur Verfügung steht. |
Weitere Beteiligte |
| Versicherter/Versicherungparticipant
participant [templateId[@root='1.2.40.0.34.6.0.11.1.26']] time |
0..* O
0..1 O |
0..* O
0..1 O |
Gültigkeitszeitraum der Versicherungspolizze. | Weitere Beteiligte |
| documentationOf serviceEvent |
0..* O 1..1 M |
0..* O 1..1 M |
Zeitraum der durchgeführten Gesundheitsdienstleistung. Ist im jeweiligen speziellen Implementierungsleitfaden genauer vorgeschrieben. | Gesundheitsdienstleistungen |
| componentOf encompassingEncounter |
0..1 O 1..1 M |
0..1 O 1..1 M |
Zeitraum des Patientenkontakts. | Patientenkontakt (Aufenthalt) |
13.2.1 Labor- und Mikrobiologiebefund
Für den Labor- und Mikrobiologiebefund gibt es aufgrund der Anpassung hinsichtlich der Kardinalität/Konformität einzelner Header-Elemente folgende Änderungen.
| Element | Kard/Konf Laborbefund | Kard/Konf Mikrobiologiebefund | Bedeutung | Link zum Kapitel |
|---|---|---|---|---|
| legalAuthenticator
time |
1..1 M
1..1 R |
1..1 M
1..1 R |
Die Zeitpunkte, an welchem das Dokument von der berechtigten Personen vidiert wurde. Diese Person ist der Hauptunterzeichner. Dieser Zeitpunkt sollte, wenn vorhanden, nach /ClinicalDocument/author/time und /ClinicalDocument/dataEnterer/time liegen. | Rechtlicher Unterzeichner |
| documentationOf serviceEvent |
1..* M 1..1 M |
1..1 M 1..1 M |
Zeitraum der durchgeführten Gesundheitsdienstleistung. | siehe Spezifikation der Document Level Templates |
13.3 Übersichtstabelle der CDA Strukturen des Bodys
Die folgenden Tabellen geben die im ELGA Labor- bzw. Mikrobiologiebefund verwendeten Sektionen und Entries wieder. Angaben über die Verwendung einzelner Elemente können - sofern nicht in dieser Tabelle aufgeführt - in den jeweiligen Sektions- oder Entry-Spezifikationen gefunden werden (aus Gründen der Übersichtlichkeit wurde auf die Darstellung aller Ebenen verzichtet).
13.3.1 Laborbefund
| Sektion bzw. Entry | OID | Kard/Konf | Kapitel | |||
|---|---|---|---|---|---|---|
| Brieftext | 1.2.40.0.34.6.0.11.2.69 | 0..1 O | Link | |||
| Überweisungsgrund - optional codiert | 1.2.40.0.34.6.0.11.2.6 | 0..1 O | Link | |||
| Angeforderte Untersuchungen - optional codiert | 1.2.40.0.34.6.0.11.2.15 | 0..1 O | Link | |||
| Probeninformation (Specimen Section) | 1.2.40.0.34.6.0.11.2.93 | 0..1 C | Link | |||
| Probeninformation (Specimen Entry) | 1.2.40.0.34.6.0.11.3.160 | 1..1 M | Link | |||
| Specimen Collection | 1.2.40.0.34.6.0.11.3.161 | 1..* M | Link | |||
| Specimen Received | 1.2.40.0.34.6.0.11.3.162 | 0..1 O | Link | |||
| Laboratory Specialty Section | 1.2.40.0.34.6.0.11.2.102 | 1..* M TODO: vielleicht nur 1..* R? | Link | |||
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Struktur | |||
| Befundbewertung | 1.2.40.0.34.6.0.11.2.103 | 0..* O | Link | |||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 1..1 R | Link | |||
| Beilagen | 1.2.40.0.34.6.0.11.2.71 | 0..* O | Link | |||
| Abschließende Bemerkung | 1.2.40.0.34.6.0.11.2.70 | 0..* O | Link | |||
13.3.2 Mikrobiologiebefund
| Sektion bzw. Entry | OID | Kard/Konf | Kapitel | |||
|---|---|---|---|---|---|---|
| Brieftext | 1.2.40.0.34.6.0.11.2.69 | 0..1 O | Link | |||
| Überweisungsgrund - optional codiert | 1.2.40.0.34.6.0.11.2.6 | 0..1 O | Link | |||
| Angeforderte Untersuchungen - optional codiert | 1.2.40.0.34.6.0.11.2.15 | 0..1 O | Link | |||
| Probeninformation (Specimen Section) | 1.2.40.0.34.6.0.11.2.93 | 0..1 C | Link | |||
| Probeninformation (Specimen Entry) | 1.2.40.0.34.6.0.11.3.160 | 1..1 M | Link | |||
| Specimen Collection | 1.2.40.0.34.6.0.11.3.161 | 1..* M
Im Mikrobiologiebefund MUSS genau eine "Specimen Collection" vorkommen. |
Link | |||
| Specimen Received | 1.2.40.0.34.6.0.11.3.162 | 0..1 O | Link | |||
| Von den folgenden "Laboratory Specialty Sections" MUSS zumindest eine vorkommen. | ||||||
| Laboratory Specialty Section (Mikroskopie) | 1.2.40.0.34.6.0.11.2.105 | 0..1 O | Link | |||
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Struktur | |||
| Laboratory Specialty Section (Kultureller Erregernachweis) | 1.2.40.0.34.6.0.11.2.106 | 0..1 O | Link | |||
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Struktur | |||
| Laboratory Specialty Section (Molekularer Erregernachweis) | 1.2.40.0.34.6.0.11.2.107 | 0..1 O | Link | |||
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Struktur | |||
| Laboratory Specialty Section (Infektionsserologie) | 1.2.40.0.34.6.0.11.2.108 | 0..1 O | Link | |||
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Struktur | |||
| Befundbewertung | 1.2.40.0.34.6.0.11.2.103 | 0..* O | Link | |||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 1..1 R | Link | |||
| Beilagen | 1.2.40.0.34.6.0.11.2.71 | 0..* O | Link | |||
| Abschließende Bemerkung | 1.2.40.0.34.6.0.11.2.70 | 0..* O | Link | |||
13.3.3 Struktur: Laboratory Report Data Processing Entry
| Sektion bzw. Entry | OID | Kard/Konf | Kapitel | ||
|---|---|---|---|---|---|
| Laboratory Report Data Processing Entry | 1.2.40.0.34.6.0.11.3.25 | 1..1 M | Link | ||
| Von den folgenden Elementen MUSS zumindest eines vorkommen: | |||||
| Specimen Collection | 1.2.40.0.34.6.0.11.3.161 | 0..* C
Im Mikrobiologiebefund MUSS genau eine "Specimen Collection" vorkommen. |
Link | ||
| Specimen Received | 1.2.40.0.34.6.0.11.3.162 | 0..1 O | Link | ||
| Notification Organizer | 1.2.40.0.34.6.0.11.3.165 | 0..* O | Link | ||
| Von den folgenden Elementen MUSS zumindest eines vorkommen: | |||||
| Notifiable Condition | 1.2.40.0.34.6.0.11.3.166 | 0..* O | Link | ||
| TODO? Case Identification | 0..* O | ||||
| TODO? Outbreak Identification | 0..* O | ||||
| Laboratory Isolate Organizer | 1.2.40.0.34.6.0.11.3.167 | 0..* O | Link | ||
| Von den folgenden Elementen MUSS zumindest eines vorkommen: | |||||
| Laboratory Battery Organizer | 1.2.40.0.34.6.0.11.3.26 | 0..* O | Link | ||
| Laboratory Observation | 1.2.40.0.34.6.0.11.3.27 | 0..* O | Link | ||
| TODO? Eingebettetes Objekt Entry | |||||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 0..* O | Link | ||
| Laboratory Battery Organizer | 1.2.40.0.34.6.0.11.3.26 | 0..* O | Link | ||
| TODO? Specimen Collection | |||||
| Laboratory Observation | 1.2.40.0.34.6.0.11.3.27 | 0..* O | Link | ||
| Eingebettetes Objekt Entry | 1.2.40.0.34.6.0.11.3.19 | 0..* O | Link | ||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 0..* O | Link | ||
| Laboratory Observation | 1.2.40.0.34.6.0.11.3.27 | 0..* O | Link | ||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 0..* O | Link | ||
| Eingebettetes Objekt Entry | 1.2.40.0.34.6.0.11.3.19 | 0..* O | Link | ||
| Comment Entry | 1.2.40.0.34.6.0.11.3.11 | 0..* O | Link | ||
13.4 CDA Templates
13.4.1 IHE PaLM TF-3 Konformität
Der vorliegende Leitfaden baut auf den Definitionen des "IHE Pathology and Laboratory Medicine (PALM) Technical Framework Volume 3 (PaLM TF-3) Revision 10.0, 2019"[23] auf, welche durch diesen Leitfaden weiter eingeschränkt werden. Dadurch erhalten die entsprechenden Templates ihre Gültigkeit und sind aus Konformitätsgründen bei Komponenten, welche über eine entsprechende Definition verfügen, auch anzugeben.
Entsprechend den Vorgaben des IHE Frameworks für Labor sind für Personen und Organisationen die Angabe eines Namens (name-Element), einer Adresse (addr-Element) und einer Telekom-Verbindung (telecom-Element) verpflichtend. Diese können jedoch mit einem nullFlavor versehen werden.
13.4.2 Document Level Templates
13.4.2.1 Laborbefund
[TODO Beschreibung in Template]
| Id | 1.2.40.0.34.6.0.11.0.11 | Gültigkeit ab | 2020‑08‑25 14:35:13 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 3.0.0+20211214 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_document_Laborbefund | Bezeichnung | Laborbefund | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Pfadname / | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Document Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.2.2 Mikrobiologiebefund
[TODO Beschreibung in Template]
| Id | 1.2.40.0.34.6.0.11.0.14 | Gültigkeit ab | 2021‑03‑29 15:24:59 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 3.0.0+20211214 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_document_Mikrobiologiebefund | Bezeichnung | Mikrobiologiebefund | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Pfadname / | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Document Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.6.0.11.0.11 Laborbefund (2020‑08‑25 14:35:13) ref at-lab- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.3 Header Level Templates
Wichtiger Hinweis: Header-Element welche spezifisch für den Labor- und Mikrobiologiebefund angepasst wurden oder für die es spezielle Einschränkungen in Form von Asserts gibt, sind grundsätzlich der Spezifikation im Kapitel Document Level Templates zu entnehmen.
Diese angepassten bzw. betroffenen Elemente umfassen:
- ClincialDocument/templateId
- ClincialDocument/code
- ClinicalDocument/title
- ClinicalDocument/formatCode
- ClinicalDocument/author
- ClinicalDocument/authenticator
- ClinicalDocument/componentOf/encompassingEncounter
Ebenso wurden folgende Header-Elemente angepasst und werden in diesem Kapitel detailliert dargestellt:
- ClinicalDocument/participant[@typeCode='REF'] (Participant Auftraggeber / Ordering Provider)
- ClinicalDocument/documentationOf/serviceEvent
13.4.3.1 Participant Auftraggeber / Ordering Provider
| Id | 1.2.40.0.34.6.0.11.1.42 ref at-cda-bbr- | Gültigkeit ab | 2021‑04‑28 08:55:00 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.1.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_header_ParticipantAuftraggeber_OrderingProvider | Bezeichnung | Participant Auftraggeber / Ordering Provider | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Der Auftraggeber (IHE "Ordering Provider") ist die Organisation oder der Arzt, welche/welcher den Auftrag erstellt hat. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.1.42 Participant Auftraggeber / Ordering Provider (2021‑02‑19 11:12:16) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.1.42 Participant Auftraggeber / Ordering Provider (2020‑02‑10 08:46:46) ref at-cda-bbr- Version: Template 1.2.40.0.34.11.1.1.1 HeaderParticipant Ansprechpartner (2014‑03‑25) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.3.2 Documentation Of Service Event - Labor- und Mikrobiologie
| Id | 1.2.40.0.34.6.0.11.1.48 | Gültigkeit ab | 2020‑08‑26 15:29:24 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_header_DocumentationOfServiceEventLaborUndMikrobiologie | Bezeichnung | Documentation Of Service Event - Labor und Mikrobiologie | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Header Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.6.0.11.1.17 Documentation Of Service Event (2019‑03‑14 15:08:34) ref at-cda-bbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4 Section Level Templates
13.4.4.1 Brieftext
| Id | 1.2.40.0.34.6.0.11.2.69 ref at-cda-bbr- | Gültigkeit ab | 2021‑06‑28 11:19:35 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.1+20210628 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_section_Brieftext | Bezeichnung | Brieftext | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.69 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.2.69 Brieftext (2021‑02‑19 11:44:10) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.2.69 Brieftext (2019‑04‑02 15:48:06) ref at-cda-bbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.2 Überweisungsgrund - optional codiert
| Id | 1.2.40.0.34.6.0.11.2.6 | Gültigkeit ab | 2021‑01‑14 09:58:40 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_UeberweisungsgrundCodiert | Bezeichnung | Überweisungsgrund - codiert | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.6 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.6.0.11.2.47 Konsultations- oder Überweisungsgrund - kodiert (2019‑11‑05 10:43:44) ref at-cda-bbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.3 Angeforderte Untersuchungen - optional codiert
| Id | 1.2.40.0.34.6.0.11.2.15 | Gültigkeit ab | 2021‑01‑14 12:18:39 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_AngeforderteUntersuchungenCodiert | Bezeichnung | Angeforderte Untersuchungen - codiert | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.15 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.6.0.11.2.13 Durchgeführte Maßnahmen - kodiert (2018‑12‑04 10:21:16) ref at-cda-bbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.4 Probeninformation (Specimen Section)
| Id | 1.2.40.0.34.6.0.11.2.93 | Gültigkeit ab | 2021‑01‑14 14:01:18 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_ProbeninformationSpecimenSection | Bezeichnung | Probeninformation (Specimen Section) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.93 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.11.4.2.1 Spezimen-Section (2013‑11‑07) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.5 Laboratory Specialty Section
| Id | 1.2.40.0.34.6.0.11.2.102 | Gültigkeit ab | 2021‑01‑21 11:16:21 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_LaboratorySpecialtySection | Bezeichnung | Laboratory Specialty Section | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.102 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.3.2.1 Speciality-Section (2013‑11‑07) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.6 Laboratory Specialty Section (Mikroskopie)
| Id | 1.2.40.0.34.6.0.11.2.105 | Gültigkeit ab | 2021‑04‑06 08:10:32 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_LaboratorySpecialtySectionMikroskopieCodiert | Bezeichnung | Laboratory Specialty Section (Mikroskopie) - codiert | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.105 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.2.102 Laboratory Specialty Section (2021‑01‑21 11:16:21) ref at-lab- Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.3.2.1 Speciality-Section (2013‑11‑07) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.7 Laboratory Specialty Section (Kultureller Erregernachweis)
| Id | 1.2.40.0.34.6.0.11.2.106 | Gültigkeit ab | 2021‑04‑06 08:46:53 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_LaboratorySpecialtySectionKulturellerErregernachweis | Bezeichnung | Laboratory Specialty Section (Kultureller Erregernachweis) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.106 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.2.102 Laboratory Specialty Section (2021‑01‑21 11:16:21) ref at-lab- Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.3.2.1 Speciality-Section (2013‑11‑07) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.8 Laboratory Specialty Section (Molekularer Erregernachweis)
| Id | 1.2.40.0.34.6.0.11.2.107 | Gültigkeit ab | 2021‑04‑06 08:56:54 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_LaboratorySpecialtySectionMolekularerErregernachweis | Bezeichnung | Laboratory Specialty Section (Molekularer Erregernachweis) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.107 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.2.102 Laboratory Specialty Section (2021‑01‑21 11:16:21) ref at-lab- Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.3.2.1 Speciality-Section (2013‑11‑07) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.9 Laboratory Specialty Section (Infektionsserologie)
| Id | 1.2.40.0.34.6.0.11.2.108 | Gültigkeit ab | 2021‑04‑06 09:46:38 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_section_LaboratorySpecialtySectionInfektionsserologie | Bezeichnung | Laboratory Specialty Section (Infektionsserologie) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.108 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.2.102 Laboratory Specialty Section (2021‑01‑21 11:16:21) ref at-lab- Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.3.2.1 Speciality-Section (2013‑11‑07) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.10 Befundbewertung
| Id | 1.2.40.0.34.6.0.11.2.103 ref at-cda-bbr- | Gültigkeit ab | 2021‑02‑03 09:56:36 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_section_Befundbewertung | Bezeichnung | Befundbewertung | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Bemerkungen oder Kommentare, die für den gesamten Befund von Bedeutung sind, werden in der Section "Befundbewertung" am Befundende angeführt. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.103 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.11.4.2.2 Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) (2013‑02‑10) ref elgabbr- Version: Template 1.2.40.0.34.11.4.2.2 Bereichsübergreifende Befundbewertung (Laboratory Report Comment Section) (2013‑02‑10) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.11 Beilagen
| Id | 1.2.40.0.34.6.0.11.2.71 ref at-cda-bbr- | Gültigkeit ab | 2023‑04‑05 13:40:58 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.2+20230717 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_section_Beilagen | Bezeichnung | Beilagen | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.71 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.2.71 Beilagen (2021‑06‑28 11:22:40) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.2.71 Beilagen (2021‑02‑19 11:43:44) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.2.71 Beilagen (2020‑01‑09 09:53:16) ref at-cda-bbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.4.12 Abschließende Bemerkung
| Id | 1.2.40.0.34.6.0.11.2.70 ref at-cda-bbr- | Gültigkeit ab | 2021‑06‑28 11:25:03 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.1+20210628 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_section_AbschliessendeBemerkung | Bezeichnung | Abschließende Bemerkung | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.2.70 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Section level template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Assoziiert mit |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.2.70 Abschließende Bemerkung (2021‑02‑19 11:27:16) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.2.70 Abschließende Bemerkung (2020‑01‑09 09:53:27) ref at-cda-bbr- Version: Template 1.2.40.0.34.11.1.2.2 AbschliessendeBemerkung (2012‑07‑14) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5 Entry Level Template
13.4.5.1 Probeninformation (Specimen Entry)
| Id | 1.2.40.0.34.6.0.11.3.160 | Gültigkeit ab | 2021‑01‑18 12:58:24 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_entry_ProbeninformationSpecimenEntry | Bezeichnung | Probeninformation (Specimen Entry) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Die "Probeninformation (Specimen Entry)" repräsentiert die CDA Level 3 Codierung der menschenlesbar dargestellten Informationen über das zu befundende Material. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.160 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.11.4.3.1 Laboratory Specimen Entry (2013‑02‑10) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.2 Specimen Collection
| Id | 1.2.40.0.34.6.0.11.3.161 ref at-cda-bbr- | Gültigkeit ab | 2021‑01‑18 13:46:31 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_entry_SpecimenCollection | Bezeichnung | Specimen Collection | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.11.30021 Abnahmeinformationen (Specimen Collection) (2014‑03‑04) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.3 Specimen Received
| Id | 1.2.40.0.34.6.0.11.3.162 ref at-cda-bbr- | Gültigkeit ab | 2021‑01‑18 14:25:23 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atlab_entry_SpecimenReceived | Bezeichnung | Specimen Received | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Adaptation: Template 1.2.40.0.34.11.30022 Annahmeinformationen (Specimen Received) (2014‑03‑04) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.4 Laboratory Report Data Processing Entry
| Id | 1.2.40.0.34.6.0.11.3.25 ref at-cda-bbr- | Gültigkeit ab | 2023‑06‑01 13:53:03 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_LaboratoryReportDataProcessing | Bezeichnung | Laboratory Report Data Processing Entry | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Geschwisterknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.25 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.3.25 Laboratory Report Data Processing Entry (2019‑05‑07 12:59:27) ref at-cda-bbr- Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.1 BC Laboratory Report Data Processing Entry (DYNAMIC) ref bccdapilot- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.5 Notification Organizer
| Id | 1.2.40.0.34.6.0.11.3.165 ref at-cda-bbr- | Gültigkeit ab | 2021‑02‑02 08:42:49 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_NotificationOrganizer | Bezeichnung | Notification Organizer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | Der "Notification Organizer" ermöglicht die CDA Level 3 Codierung von wichtigen Erregern ("Notifiable Condition") bzw. der Dokumentation der separat erfolgten Meldung ans EMS ("Case Identification"). | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.165 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.1.1 Notification Organizer (2013‑09‑09) ref elgabbr- Version: Template 1.3.6.1.4.1.19376.1.3.1.1 Notification Organizer (2013‑09‑09) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.6 Notifiable Condition
| Id | 1.2.40.0.34.6.0.11.3.166 ref at-cda-bbr- | Gültigkeit ab | 2021‑02‑02 10:46:26 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20211213 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_NotifiableCondition | Bezeichnung | Notifiable Condition | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beschreibung | CDA Level 3 Codierung von wichtigen Erregern. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.166 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.3.6.1.4.1.19376.1.3.1.1.1 Notification Condition (2013‑09‑09) ref elgabbr- Version: Template 1.3.6.1.4.1.19376.1.3.1.1.1 Notification Condition (2013‑09‑09) ref elgabbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.7 Laboratory Isolate Organizer
| Id | 1.2.40.0.34.6.0.11.3.167 ref at-cda-bbr- | Gültigkeit ab | 2023‑06‑01 13:39:19 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_LaboratoryIsolateOrganizer | Bezeichnung | Laboratory Isolate Organizer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.3.167 Laboratory Isolate Organizer (2021‑02‑02 11:18:12) ref at-cda-bbr- Spezialisierung: Template 1.2.40.0.34.11.30025 Kultureller Keimnachweis (Laboratory Isolate Organzier) (2017‑02‑23) ref elgabbr- Version: Template 1.2.40.0.34.11.30025 Kultureller Keimnachweis (Laboratory Isolate Organzier) (2017‑02‑23) ref elgabbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.8 Laboratory Battery Organizer
| Id | 1.2.40.0.34.6.0.11.3.26 ref at-cda-bbr- | Gültigkeit ab | 2023‑06‑01 13:50:16 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_LaboratoryBatteryOrganizer | Bezeichnung | Laboratory Battery Organizer | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.26 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.3.26 Laboratory Battery Organizer (2019‑05‑29 10:51:34) ref at-cda-bbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.9 Laboratory Observation
| Id | 1.2.40.0.34.6.0.11.3.27 ref at-cda-bbr- | Gültigkeit ab | 2023‑06‑01 13:58:20 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 2.0.1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_LaboratoryObservation | Bezeichnung | Laboratory Observation | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.27 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.3.27 Laboratory Observation (2021‑04‑19 16:15:55) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.3.27 Laboratory Observation Entry (2019‑05‑07 13:44:02) ref at-cda-bbr- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.10 Eingebettetes Objekt Entry
| Id | 1.2.40.0.34.6.0.11.3.19 ref at-cda-bbr- | Gültigkeit ab | 2023‑05‑09 16:42:36 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.2+20230717 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabbr_entry_EingebettetesObjektEntry | Bezeichnung | Eingebettetes Objekt Entry | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.19 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Spezialisierung: Template 1.2.40.0.34.6.0.11.3.19 Eingebettetes Objekt Entry (2021‑06‑28 11:13:27) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.3.19 Eingebettetes Objekt Entry (2021‑02‑19 12:43:14) ref at-cda-bbr- Version: Template 1.2.40.0.34.6.0.11.3.19 Eingebettetes Objekt Entry (2020‑12‑17 12:24:45) ref at-cda-bbr- | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.5.11 Comment Entry
| Id | 1.2.40.0.34.6.0.11.3.11 ref at-cda-bbr- | Gültigkeit ab | 2021‑02‑19 12:42:56 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Status | Versions-Label | 1.0.0+20210219 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name | atcdabrr_entry_Comment | Bezeichnung | Comment Entry | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Kontext | Elternknoten des Template-Element mit Id 1.2.40.0.34.6.0.11.3.11 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Klassifikation | CDA Entry Level Template | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Offen/Geschlossen | Geschlossen (nur definierte Elemente sind erlaubt) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Benutzt |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beziehung | Version: Template 1.2.40.0.34.6.0.11.3.11 Comment Entry (2019‑02‑07 13:10:44) ref at-cda-bbr- Spezialisierung: Template 1.3.6.1.4.1.19376.1.5.3.1.4.2 Comment (2013‑12‑20) ref epsos- Spezialisierung: Template 2.16.840.1.113883.10.20.1.40 Befundtext (Anmerkungen und Kommentare)-deprecated (DYNAMIC) ref elga- | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Beispiel |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
13.4.6 Weitere CDA Fragmente
Die weiteren CDA Fragmente, oder auch Compilation Templates genannt, wurden aus dem bestehenden "Allgemeinen Implementierungsleitfaden für ELGA CDA Dokumente" übernommen. Diese sind auch unter Allgemeiner Leitfaden - Kapitel Sonstige Templates (Fragmente) zu finden.
13.5 Terminologien
Die erforderlichen Terminologien sind im Folgenden aufgelistet.
Falls Werte in den definierten Value-Sets fehlen, dann bitten wir um die Meldung mit einem Vorschlag an cda@elga.gv.at.
14 Anhang
14.1 Abbildungen
14.2 Tabellen
- ↑ Im Labor- und Mikrobiologiebefund abzubildende medizinische Daten
- ↑ Liste der Befundbereiche, auszugsweise gem. ELGA Value Set "ELGA_Laborstruktur", die sich auch im ELGA Value Set "ELGA_Laborparameter" widerspiegeln.
- ↑ Übersichtstabelle der CDA Strukturen des Headers
- ↑ Übersichtstabelle der angepassten CDA Strukturen des Headers für Labor- und Mikrobiologiebefund
- ↑ Übersichtstabelle der Header-Elemente für Zeitpunkte/Zeitspannen
- ↑ Übersichtstabelle der angepassten Header-Elemente für Zeitpunkte/Zeitspannen in Labor- und Mikrobiologiebefund
- ↑ Übersichtstabelle der CDA Strukturen des Bodys des Laborbefundes
- ↑ Übersichtstabelle der CDA Strukturen des Bodys des Mikrobiologiebefundes
- ↑ Übersichtstabelle der CDA Strukturen des Laboratory Report Data Processing Entries
14.3 Referenzen
- ↑ Logical Observation Identifiers Names & Codes (LOINC) loinc.org
- ↑ 2,0 2,1 Regenstrief Institute, Inc. www.regenstrief.org
- ↑ Unified Code for Units of Measure (UCUM) www.unitsofmeasure.org
- ↑ WHO ICD-10 www.who.int/classifications/icd/en/
- ↑ 5,0 5,1 www.who.int
- ↑ Internationale statistische Klassifikation der Krankheiten und verwandter Gesundheitsprobleme 10. Revision – aktuelle Version bitte unter Gesundheitssystem - Krankenanstalten heraussuchen.
- ↑ Anatomical Therapeutic Chemical Classification System (ATC) https://www.who.int/tools/atc-ddd-toolkit/atc-classification
- ↑ ARGE Pharma im Fachverband der chemischen Industrie Österreichs (FCIO) argepharma.fcio.at
- ↑ EDQM Council of Europe www.edqm.eu
- ↑ Health informatics - Medical / health device communication standards ISO/IEEE 11073 Nomenclature Part 10101: Nomenclature
- ↑ Health informatics - Medical / health device communication standards ISO/IEEE 11073 Nomenclature Amendment 1 Part 10101: Nomenclature Amendment 1: Additional Definitions
- ↑ Health Level Seven International www.hl7.org
- ↑ ISO/HL7 27932:2009 Data Exchange Standards — HL7 Clinical Document Architecture, Release 2 [1]
- ↑ World Wide Web Consortium. Extensible Markup Language, 1.0, 5th Edition. [2]
- ↑ HL7 Version 3 Product Suite [3]
- ↑ ART-DECOR® www.art-decor.org
- ↑ HL7 Clinical Document Architecture (CDA) [4]
- ↑ HL7 Version 3: Reference Information Model (RIM) [5]
- ↑ HL7 Version 3 Standard: Data Types – Abstract Specification, Release 2[6]
- ↑ HL7 Templates Standard: Specification and Use of Reusable Information Constraint Templates, Release 1 [7]
- ↑ HL7 Austria www.hl7.at
- ↑ IHE Patient Care Coordination (PCC) [Online Juli 2019]: https://www.ihe.net/resources/technical_frameworks/#pcc
- ↑ 23,0 23,1 IHE Pathology and Laboratory Medicine (PALM) Technical Framework Volume 3 (PaLM TF-3) Revision 10.0, 2019 [8]
- ↑ Leitfaden zur Verwendung von LOINC® im ELGA CDA® R2 Laborbefund [9]
- ↑ ISO 15189:2012 "Medizinische Laboratorien - Anforderungen an die Qualität und Kompetenz"